고차원 데이터의 반복적 특징 선택과 비지도 학습
i‑IF‑Learn은 고차원·노이즈가 많은 데이터에서 클러스터를 형성하는 핵심 특징(영향력 있는 특징)을 자동으로 찾아내고, 동시에 군집 라벨을 추정하는 반복적 프레임워크이다. 의사 라벨의 신뢰도를 동적으로 평가해 지도‑비지도 통계량을 가중 결합하고, PCA 혹은 라플라시안 고유맵을 이용한 저차원 임베딩 후 k‑means로 군집을 재구성한다. 마이크로어레이와 단일세포 RNA‑seq 실험에서 기존 방법들을 크게 능가했으며, 선택된 특징을 전처리로…
저자: Chen Ma, Wanjie Wang, Shuhao Fan
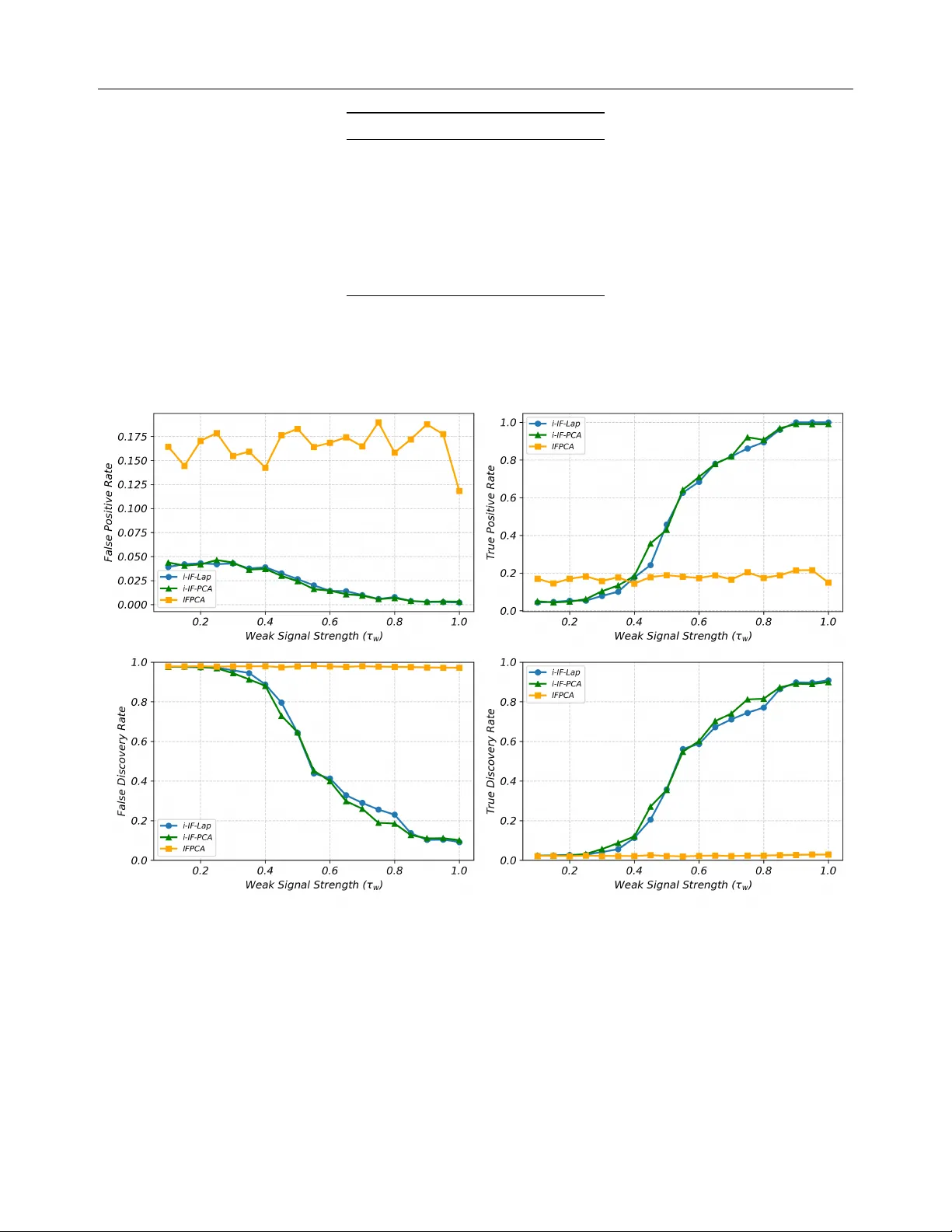
본 논문은 고차원·노이즈가 많은 데이터에서 클러스터링 성능을 저해하는 비관련 특징들을 자동으로 걸러내고, 동시에 군집 라벨을 추정하는 새로운 프레임워크 i‑IF‑Learn을 제안한다. 저자는 “영향력 있는 특징”(influential features)이라는 개념을 도입하여, 실제 클러스터 구조를 정의하는 소수의 특징만을 찾아내면 해석 가능성과 군집 정확도가 동시에 개선된다고 주장한다.
i‑IF‑Learn은 두 단계인 IF(Influential Features)와 Learn을 반복하는 구조로 설계되었다. IF 단계에서는 현재 의사 라벨 ℓ⁽ᵗ⁻¹⁾ 에 기반한 지도 통계 T_supⱼ와 비지도 통계 T_unsupⱼ를 가중 평균한 복합 점수 S⁽ᵗ⁾ⱼ를 계산한다. 여기서 ω⁽ᵗ⁾ 는 라벨 신뢰도 w⁽ᵗ⁾ 에 의해 동적으로 결정되며, w⁽ᵗ⁾ 는 이전 단계에서 선택된 특징 집합이 실제 신호를 포함하고 있는지를 검정한 p‑값 p₁⁽ᵗ⁾ 를 이용해 w⁽ᵗ⁾ = 1‑p₁⁽ᵗ⁾/(p₁⁽ᵗ⁾+c) 로 정의한다. 이 설계는 초기 라벨이 불안정할 때는 비지도 통계에 더 큰 비중을 두고, 라벨이 점점 신뢰성을 얻으면 지도 통계의 비중을 늘려 오류 전파를 억제한다.
점수 S⁽ᵗ⁾ⱼ 에 대해 Higher‑Criticism Thresholding(HCT)을 적용해 임계값 τ⁽ᵗ⁾ 을 자동으로 설정하고, S⁽ᵗ⁾ⱼ ≥ τ⁽ᵗ⁾ 인 특징을 I⁽ᵗ⁾ 에 포함한다. 이렇게 선정된 특징 집합은 저차원 임베딩 단계로 전달된다. Learn 단계에서는 X(I⁽ᵗ⁾) 에 대해 두 가지 임베딩 방법을 제공한다. i‑IF‑PCA는 전통적인 주성분 분석(PCA)을 사용하고, i‑IF‑Lap은 라플라시안 고유맵(Laplacian eigenmaps)을 이용해 비선형 구조를 보존한다. 임베딩된 좌표 U⁽ᵗ⁾ 에 k‑means를 적용해 새로운 라벨 ℓ⁽ᵗ⁾ 을 얻으며, 특징 집합 변화 비율 r = |I⁽ᵗ⁾ΔI⁽ᵗ⁻¹⁾|/|I⁽ᵗ⁾| 가 10 % 이하가 되거나 사전에 정의된 최대 반복 T 에 도달하면 알고리즘을 종료한다.
이론적 분석에서는 저신호(high‑dimensional weak‑signal) 모델 하에 라벨 복구와 특징 선택의 일관성을 증명하였다. 복잡도는 초기화 단계 O(n + ns) 와 매 반복 O(n + n²s) 을 합쳐 O(T n²s) 이며, 여기서 n은 샘플 수, s는 선택된 특징 수, T는 반복 횟수이다. 이는 실제 데이터 규모에서도 충분히 실행 가능함을 의미한다.
실험에서는 두 종류의 실제 데이터셋을 사용하였다. 첫 번째는 다양한 암 종류를 포함한 마이크로어레이 데이터이며, 두 번째는 인간 및 마우스 조직에서 수집한 단일세포 RNA‑seq 데이터이다. 비교 대상에는 Sparse k‑means, IFPCA, DEC, DeepCluster, SC3, Seurat 등 기존의 고전 및 최신 딥 클러스터링 방법이 포함되었다. 평가 지표는 NMI, ARI, 정확도, 그리고 선택된 특징의 생물학적 의미(예: 알려진 바이오마커와의 겹침)였다. i‑IF‑Learn(i‑IF‑Lap)은 모든 지표에서 가장 높은 점수를 기록했으며, 특히 비선형 임베딩을 사용했을 때 복잡한 데이터 구조를 더 잘 구분함을 확인했다.
또한, i‑IF‑Learn이 선택한 특징 집합을 전처리 단계로 사용해 DeepCluster, UMAP, VAE와 같은 최신 딥러닝 기반 클러스터링 모델을 재학습시켰다. 이 경우에도 NMI와 ARI가 평균 10‑15 % 상승했으며, 시각화된 임베딩에서도 클러스터 간 경계가 뚜렷해졌다. 이는 특징 선택이 데이터의 본질적 구조를 압축하고, 이후 모델이 더 효율적으로 학습하도록 돕는다는 실증적 증거이다.
결론적으로 i‑IF‑Learn은 (1) 지도‑비지도 통계의 동적 가중 결합을 통한 안정적인 특징 선택, (2) 라플라시안 기반 비선형 임베딩을 통한 복잡한 구조 포착, (3) 이론적 일관성 보장, (4) 다양한 실제 고차원 바이오 데이터에서의 뛰어난 성능을 모두 만족한다. 따라서 고차원·노이즈가 심한 분야, 특히 유전체·전사체 분석과 같은 해석 가능성이 중요한 영역에서 강력한 도구로 활용될 수 있다.
원본 논문
고화질 논문을 불러오는 중입니다...
댓글 및 학술 토론
Loading comments...
의견 남기기