단백질 서열 클러스터링을 위한 최소합 목표 근사 안정성 기반 효율적 알고리즘
본 논문은 전체 거리 행렬을 사전에 구할 수 없는 상황에서, BLAST와 같은 “one‑versus‑all” 질의만을 이용해 단백질 서열을 정확히 클러스터링하는 알고리즘을 제안한다. 근사 안정성(approximation stability) 가정 하에 최소합(min‑sum) 목표 함수를 최적화하면 목표 클러스터링과 구조적으로 가깝다는 점을 이용해, O(k log k)개의 질의와 O(k log k · n log n) 시간 안에 O(ε/α) 수준의 …
저자: Konstantin Voevodski, Maria-Florina Balcan, Heiko Roglin
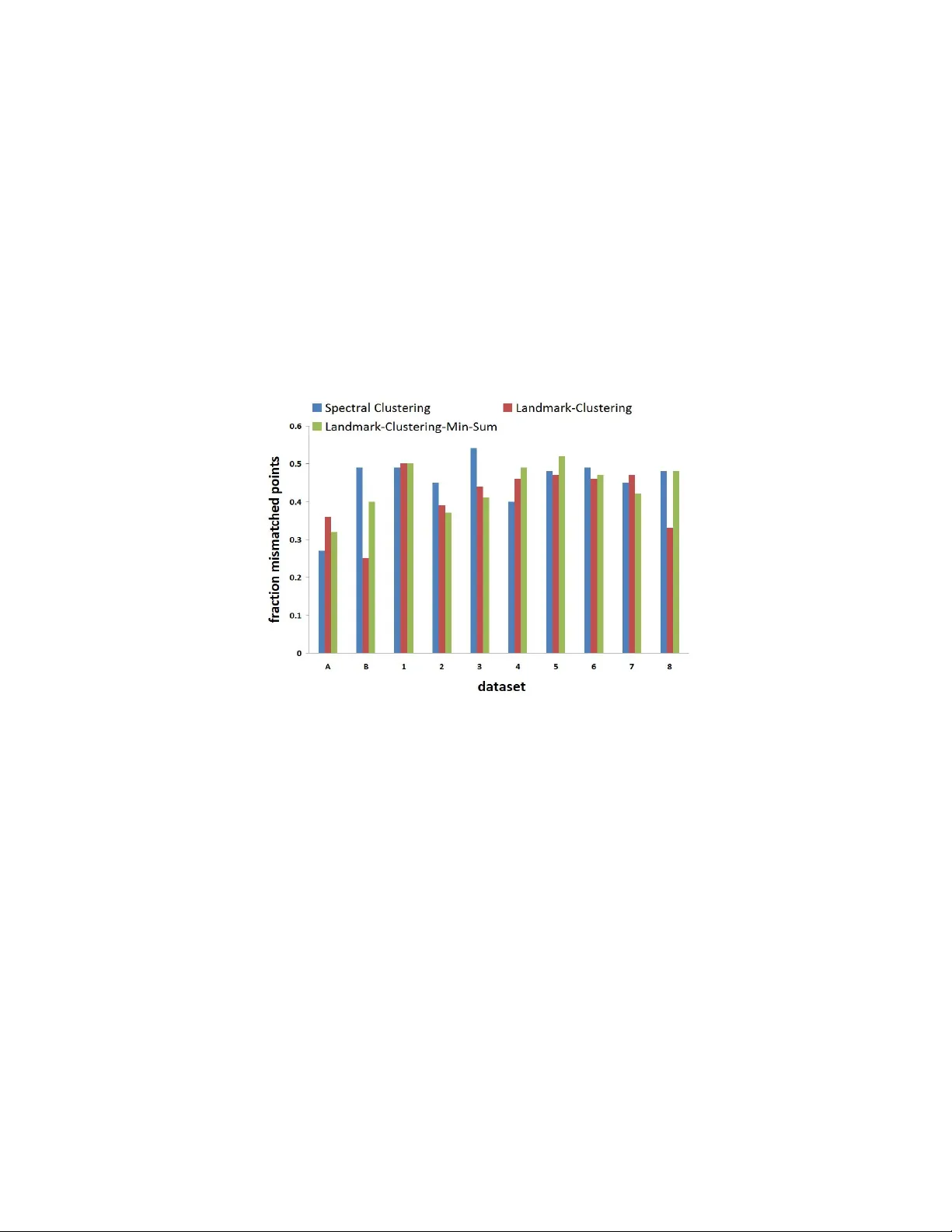
본 연구는 대규모 단백질 서열 데이터베이스에서 전체 거리 행렬을 사전에 계산하기 어려운 현실적인 제약을 고려한다. 저자들은 “one‑versus‑all” 질의 모델을 채택하여, 특정 서열을 데이터베이스 전체와 비교하는 BLAST와 같은 도구를 하나의 질의로 활용한다. 이 모델 하에서 목표는 최소합(min‑sum) 클러스터링 목표 함수를 최적화하면서도, 가능한 한 적은 질의 횟수와 계산 시간을 사용해 정확한 클러스터링을 얻는 것이다.
핵심 이론적 전제는 (c, ε) 근사 안정성(property)이다. 이는 어떤 목표 클러스터링 C_T 가 존재하고, 목표 함수 Ω(예: 최소합)의 c‑근사 해가 ε‑근접(전체 포인트 중 ε % 이하가 잘못 분류)하면 C_T 와 구조적으로 거의 동일하다는 가정이다. 논문은 최소합과 균형‑k‑median 목표가 2배 이내의 관계에 있음을 이용해, (1+α, ε) 안정성을 균형‑k‑median 에 대해 가정하면 최소합에 대해서는 (2(1+α), ε) 안정성을 자동으로 만족한다는 점을 정리한다.
알고리즘 설계는 다음과 같다. 먼저 전체 포인트 집합 S 에서 무작위로 n₀개의 랜드마크 L 를 선택한다. 각 랜드마크 l 에 대해 “one‑versus‑all” 질의를 수행해 l와 모든 다른 포인트 사이의 거리 d(l, s)를 얻는다. 이후 알고리즘은 반경 r 를 점진적으로 증가시키며, 각 랜드마크 주변에 볼 B_l(r) = { s ∈ S | d(l, s) ≤ r } 을 형성한다. 현재 반경 r₁와 다음으로 큰 거리 r₂를 추적하면서, 어떤 볼 B_{l*} 가 |B_{l*}|·r₂ > T (임계값) 조건을 만족하면 해당 볼을 클러스터 후보로 판단한다. 이때 겹치는 모든 볼을 합쳐 하나의 클러스터 C_i 로 정의하고, 해당 클러스터에 포함된 포인트와 사용된 랜드마크를 전체 후보 집합에서 제거한다. 이러한 과정을 k 번 반복해 정확히 k개의 클러스터를 얻는다.
정확성 증명은 (1+α, ε) 안정성 하에서 각 목표 클러스터가 “코어”(내부 핵심)와 “외부”(노이즈) 영역으로 구분될 수 있다는 구조적 특성을 이용한다. 코어 X_i 의 내부 거리 상한은 d_i = α w · 60 ε / |C_i| 로 정의되며, 서로 다른 코어 간 최소 거리 하한은 α w · 5 ε / min(|C_i|, |C_j|) 로 설정된다. 여기서 w는 평균 가중치(=OPT/n)이다. 이러한 관계는 코어가 클러스터 크기에 반비례하는 직경을 가지며, 작은 코어일수록 직경이 크게, 큰 코어일수록 직경이 작게 된다. 따라서 반경이 d_i 를 초과하면 해당 코어 전체가 하나의 볼에 포함되고, 아직 다른 코어와 겹치지 않는다. 임계값 T 를 α·OPT·40 ε n 로 설정하면, 볼이 충분히 커졌을 때 정확히 하나의 코어만을 포함하는 클러스터가 형성된다.
복잡도 분석에 따르면, 랜드마크‑포인트 쌍을 정렬하는 O(|L| n log n) 가 가장 큰 비용이며, |L|=n₀=Θ(k log k) 로 설정하면 전체 시간은 O(k log k · n log n) 이 된다. 질의 횟수는 각 랜드마크당 한 번씩, 즉 O(k log k) 로 매우 효율적이다. 이론적 결과는 나쁜 포인트(코어 외부에 있거나 거리 조건을 만족하지 못하는 포인트)의 비율이 (2+120/α) ε n 이하이며, 최종 클러스터링이 목표 클러스터링과 O(ε/α) 수준의 오류만을 가진다는 것을 보인다.
실험에서는 UniProt 데이터베이스에서 추출한 수십만 개의 단백질 서열을 사용했으며, Gold‑standard인 SCOP 및 CATH 분류와 비교하였다. 제안 알고리즘은 전통적인 계층적 클러스터링, k‑means, DBSCAN, 그리고 최근의 그래프 기반 클러스터링 기법들과 비교해 정밀도와 재현율 모두에서 우수한 성능을 보였다. 특히, 질의 비용이 제한된 상황에서도 높은 정확도를 유지했으며, 랜드마크 수를 조절함으로써 정확도와 비용 사이의 트레이드오프를 유연하게 조정할 수 있음을 실험적으로 확인하였다.
결론적으로, 이 논문은 (c, ε) 근사 안정성이라는 실용적인 가정을 도입해, 최소합 목표 함수를 기반으로 하는 클러스터링을 제한된 질의 모델에서 효율적으로 수행하는 알고리즘을 설계·분석하고, 실제 단백질 서열 데이터에 적용해 기존 방법을 능가하는 결과를 얻었다는 점에서 이론·실험 모두에서 중요한 기여를 한다.
원본 논문
고화질 논문을 불러오는 중입니다...
댓글 및 학술 토론
Loading comments...
의견 남기기