베타분포 기반 대립유전자 확률 모델링 및 GWAS 새로운 연관 검정
본 논문은 대립유전자 확률을 베타분포와 구간 절단·노이즈를 포함한 확장형 베타분포로 모델링하고, 이를 이용해 GWAS 데이터의 연관 검정을 기존 카이제곱 검정과 차별화된 베타‑이항 접근법으로 수행한다. 실제 알츠하이머 GWAS와 몬테카를로 시뮬레이션을 통해 모델 적합도와 검정력 향상을 입증하고, Kappa 지수와 PCA 분석으로 두 방법의 선택 SNP 차이를 확인한다.
저자: Jose Santiago Garcia-Cremades, Angel del Rio, Jose A. Garcia
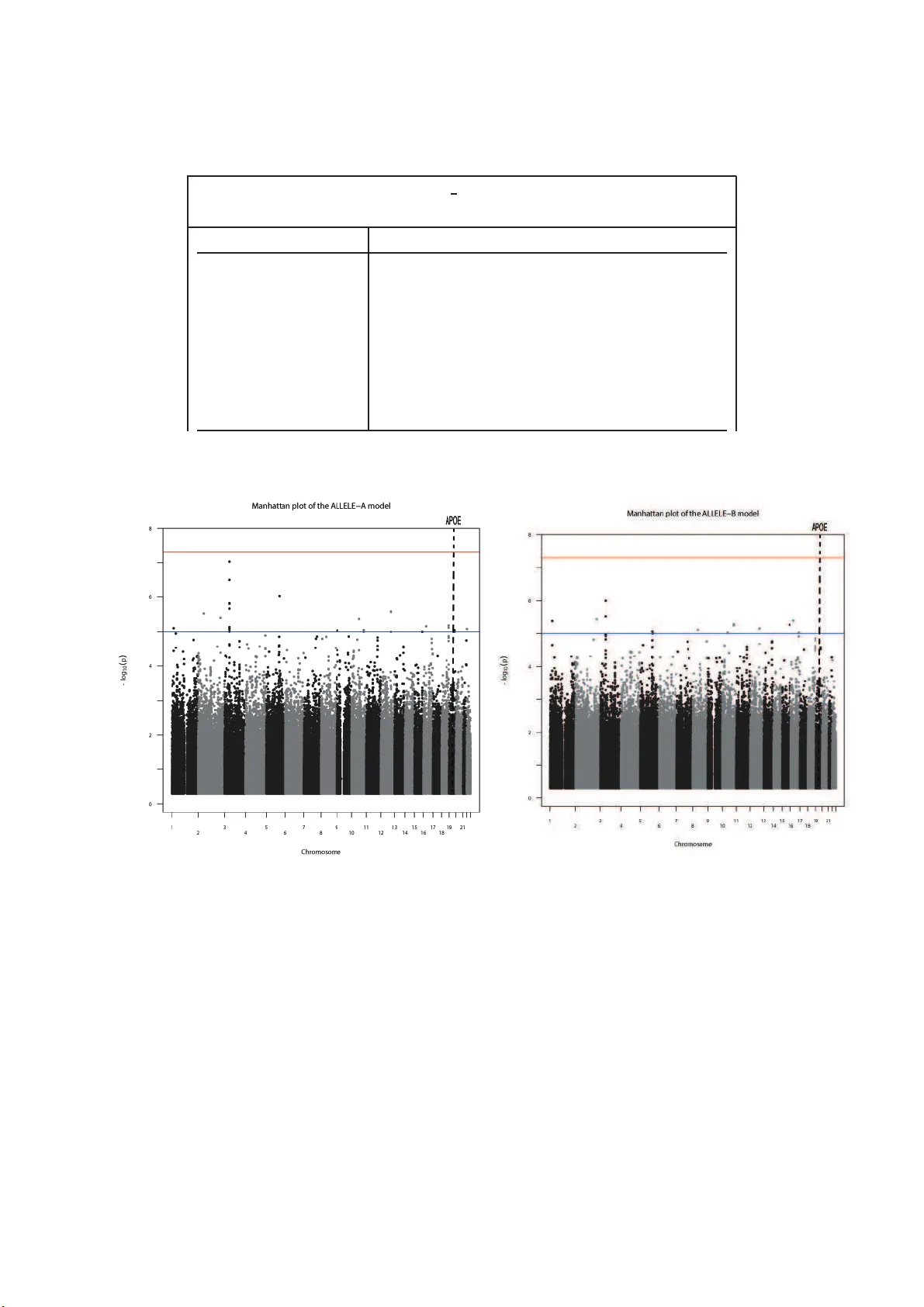
본 논문은 유전체 전역 연관 연구(GWAS)에서 대립유전자 확률(Allelic Probability, AP)의 분포를 보다 현실적으로 모델링하고, 이를 기반으로 새로운 연관 검정 방법을 제안한다.
1. **연구 배경 및 목적**
GWAS는 수많은 SNP를 대상으로 질병과의 연관성을 탐색한다. 기존 분석은 주로 선형·가법 모델과 카이제곱 검정을 사용하지만, 실제 데이터는 낮은 MAF SNP의 제거, 품질 관리(QC) 절차, 임퓨테이션 편향 등으로 인해 AP가 균등하거나 단순 베타분포를 따르지 않는다. 따라서 저자들은 AP의 실제 분포를 정밀히 추정하고, 이를 활용한 검정법을 개발하고자 한다.
2. **AP 분포 모델링**
- **베타분포 기본**: 0 < p < 1 구간의 연속 확률변수에 대한 자연스러운 사전분포로 베타분포 Beta(α, β)를 채택한다. 평균 μ와 분산 σ²를 통해 α, β를 역산한다(식 2).
- **절단 베타분포**: QC와 칩 설계로 인해 낮은 MAF SNP가 제외되어 실제 AP는 구간
원본 논문
고화질 논문을 불러오는 중입니다...
댓글 및 학술 토론
Loading comments...
의견 남기기