고해상도 간 MRI 합성을 위한 라벨 기반 3D 잠재 확산 모델
초록
**
본 논문은 Gd‑EOB‑DTPA 강화 간 MRI의 고해상도 합성 볼륨과 정확한 해부학적 라벨을 동시에 생성하는 3D‑LLDM을 제안한다. 720건의 실제 HBP MRI를 학습해 라벨‑Guided ControlNet을 적용한 3D 잠재 확산 모델을 구축했으며, FID 28.31로 기존 GAN·Diffusion 기반 모델보다 크게 개선하였다. 합성 데이터를 데이터 증강에 활용한 결과, 5가지 CNN 세그멘테이션 모델에서 특히 HCC 종양 분할 Dice가 최대 11.15% 상승하는 등 실질적인 성능 향상을 입증하였다.
**
상세 분석
**
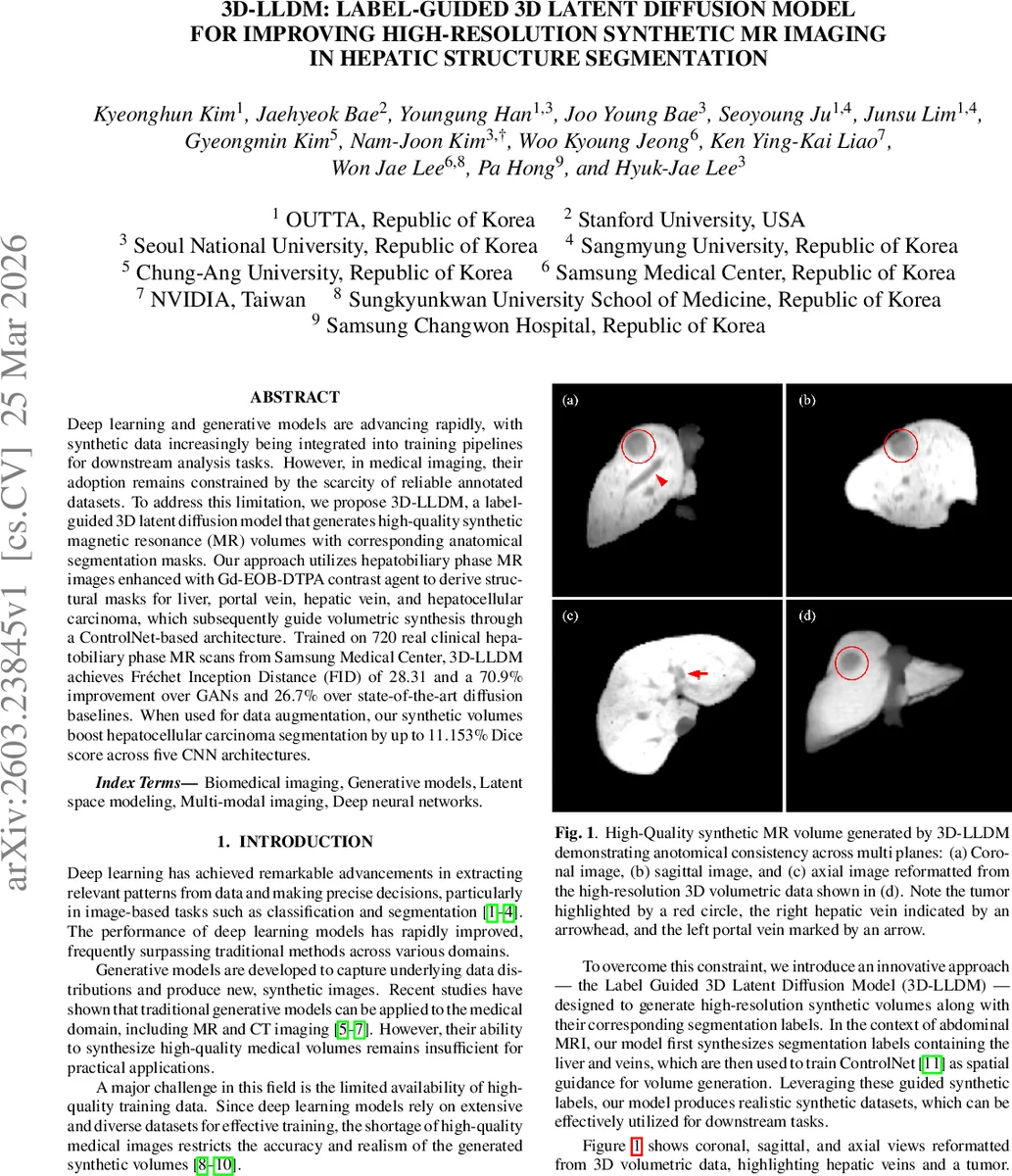
3D‑LLDM은 두 단계의 라벨‑볼륨 생성 파이프라인으로 설계되었다. 첫 단계에서는 라벨 전용 VAE(또는 VQ‑VAE)를 학습해 간, 문맥정맥, 간정맥, HCC 종양의 3D 마스크를 잠재 공간에 압축한다. 두 번째 단계에서는 동일한 잠재 공간에 이미지 디코더와 ControlNet을 결합해, 앞 단계에서 얻은 라벨 잠재 표현을 조건(condition)으로 사용한다. 이렇게 하면 라벨과 이미지 사이의 공간적 일관성이 보장되며, 전통적인 2D slice‑wise 생성 방식에서 흔히 발생하는 단면 간 불연속성을 효과적으로 해소한다.
ControlNet은 기존 확산 모델에 추가적인 공간적 가이드를 제공하는 모듈로, 라벨을 직접 입력받아 노이즈 제거 과정에서 원하는 해부학적 구조를 강제한다. 논문에서는 NVIDIA MONAI 프레임워크와 3D ResNet‑50 기반 FID 계산을 활용해, 축별(Axial, Sagittal, Coronal) 및 전체 평균 FID를 측정하였다. 3D‑LLDM은 평균 FID 28.31을 기록했으며, 이는 HA‑GAN 대비 70.9% 감소, 가장 강력한 3D‑LDM(VAE) 대비 26.7% 감소한 수치이다.
데이터 증강 실험에서는 실제 720건의 HBP MRI와 동일 비율의 합성 데이터를 혼합해 5가지 최신 3D CNN(U‑Net, ResUNet, WideResUNet, DynUNet, VNet)을 학습시켰다. 모든 모델에서 라벨‑가이드 합성 데이터가 성능을 끌어올렸으며, 특히 HCC 종양 분할에서 U‑Net은 Dice 0.733→0.815(+11.15%)를 달성했다. 혈관 분할(Vein‑Only)과 다중 클래스 분할에서도 평균 8~9% 수준의 개선이 관찰되었다. 이는 라벨‑조건부 합성이 복잡한 혈관·종양 구조를 정확히 재현함을 의미한다.
연산 측면에서는 80GB 메모리 A100 한 대에서 약 1주일간 학습했으며, 추론 시에도 라벨 노이즈 → 라벨 → 이미지 순서로 진행되어 실시간 생성은 아직 제한적이다. 또한 라벨 생성 단계에서 실제 라벨을 직접 사용해 성능을 최적화했는데, 이는 완전한 라벨‑생성 모델만으로는 아직 품질이 부족함을 시사한다. 향후 라벨‑생성 품질 향상 및 경량화, 다양한 MRI 시퀀스와 장기 추적 데이터에 대한 일반화 검증이 필요하다.
**
댓글 및 학술 토론
Loading comments...
의견 남기기