동적 트랩 스페이스를 이용한 바이오마커와 표현형 연결
초록
본 논문은 Boolean 네트워크에서 부분적인 정상 상태인 트랩 스페이스를 ‘동적 표현형’으로 정의하고, 이를 통해 실험적으로 측정 가능한 바이오마커와 세포 표현형을 효율적으로 연결하는 방법을 제시한다. 트랩 스페이스는 전체 어트랙터를 전부 탐색하지 않아도 식별 가능하며, 70노드 T세포 분화 모델을 포함한 네 가지 실제 모델에 적용해 알려진 세포 유형과 활성 상태를 재현하였다. 또한, Boolean 함수의 관통성(canalization)을 이용해 핵심 바이오마커 후보를 자동으로 선정하는 절차를 제안한다.
상세 분석
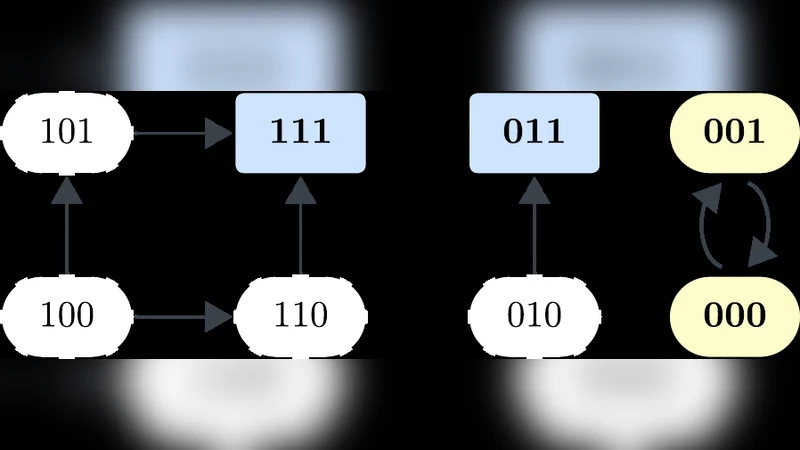
본 연구는 시스템 생물학에서 가장 난제 중 하나인 ‘모델 동역학과 실험적 표현형 사이의 연결 고리’를 새로운 수학적 개념인 동적 트랩 스페이스(dynamical trap space)를 통해 해소하고자 한다. 트랩 스페이스는 Boolean 네트워크의 상태 공간에서 한 번 진입하면 탈출이 불가능한 부분집합으로, 전통적인 어트랙터(고정점·주기)를 포함하지만 그보다 더 일반적인 구조를 가진다. 저자들은 ‘표현형’을 특정 바이오마커 노드들의 값이 고정된 부분 정상 상태로 정의하고, 외부 입력 노드는 자유롭게 두어 환경 의존성을 명시한다. 이렇게 정의된 동적 표현형은 ‘완전 트랩 스페이스(complete trap space)’이며, 선택된 바이오마커 집합을 최대한 구체화하면서도 불필요한 제약을 최소화한다는 두 가지 최적화 목표를 만족한다.
방법론적으로는 SAT/SMT 기반의 논리식 인코딩을 활용해 트랩 스페이스를 효율적으로 탐색한다. 기존에 어트랙터 전체를 열거해야 했던 문제와 달리, 트랩 스페이스는 부분적인 고정 변수 집합만으로도 존재 여부를 판단할 수 있어 계산 복잡도가 크게 감소한다. 특히, ‘관통성(canalization)’이라는 Boolean 함수의 구조적 특성을 이용해 어떤 노드가 다른 노드에 비해 더 강하게 결정적인지를 정량화하고, 이를 기반으로 ‘표현형 결정 노드(phenotype‑determining nodes)’를 자동 선택한다. 관통성이 높은 노드는 입력값 변화에 강인하게 고정된 출력을 제공하므로, 실험적으로 측정하기에 적합한 바이오마커 후보가 된다.
네 가지 공개 모델(예: T‑cell 분화 70노드, 대장균 대사, 세포주기 등)에 적용한 결과, 동적 표현형은 기존 연구자가 수작업으로 정의한 세포 유형과 거의 일치하면서도 추가적인 환경 조건(외부 신호)과의 연관성을 명시적으로 제공한다. 특히 T‑cell 모델에서는 Th1, Th2, Th17, Treg 등 알려진 분화 경로를 정확히 재현했으며, 각 경로가 활성화되기 위한 사이토카인 및 성장인자 조합을 트랩 스페이스의 자유 입력 변수로 제시한다. 또한, 관통성 기반 바이오마커 선정 결과는 두 가지 독립적인 어트랙터 기반 검증(고정점 탐색·주기 탐색)과 일치하여 제안된 방법의 신뢰성을 입증한다.
이 논문의 주요 기여는 다음과 같다. 첫째, 표현형을 ‘부분 정상 상태’라는 수학적 개념으로 공식화함으로써 모델 구조와 실험적 측정값 사이의 매핑을 명확히 했다. 둘째, 트랩 스페이스 탐색을 통해 어트랙터 전체를 열거하지 않아도 충분히 정확한 표현형 정보를 얻을 수 있는 효율적인 알고리즘을 제공했다. 셋째, 관통성 분석을 통해 자동화된 바이오마커 후보 도출 절차를 제시함으로써 실험 설계 단계에서의 비용과 시간을 절감할 수 있다. 넷째, 다양한 규모와 복잡도의 실제 모델에 적용 가능함을 입증함으로써 스케일러블한 프레임워크임을 강조했다. 향후 연구에서는 연속형(다중값) 논리 모델이나 확률적 Boolean 네트워크에도 이 개념을 확장하고, 임상 데이터와의 통합을 통해 정밀 의학에 직접 적용하는 방안을 모색할 수 있을 것이다.
댓글 및 학술 토론
Loading comments...
의견 남기기