3D 의료영상의 효율적 2D 변환, 2.75D 기법으로 학습 강화
본 논문은 3차원 의료 영상을 나선형 스캔을 통해 단일 2차원 이미지로 변환하는 2.75D 방식을 제안한다. 이를 통해 기존 2D CNN의 사전학습 모델을 그대로 활용하면서도 3D 구조 정보를 보존할 수 있다. 다중 뷰(2.75D×3) 전략을 추가해 성능을 높였으며, LUNA16 CT, 유방 MRI, 전립선 MRI 데이터셋에서 2D, 2.5D, 3D 대비 우수한 정확도와 현저한 학습·추론 속도 향상을 입증하였다. 특히 데이터가 제한된 상황이나 …
저자: Xin Wang, Ruisheng Su, Weiyi Xie
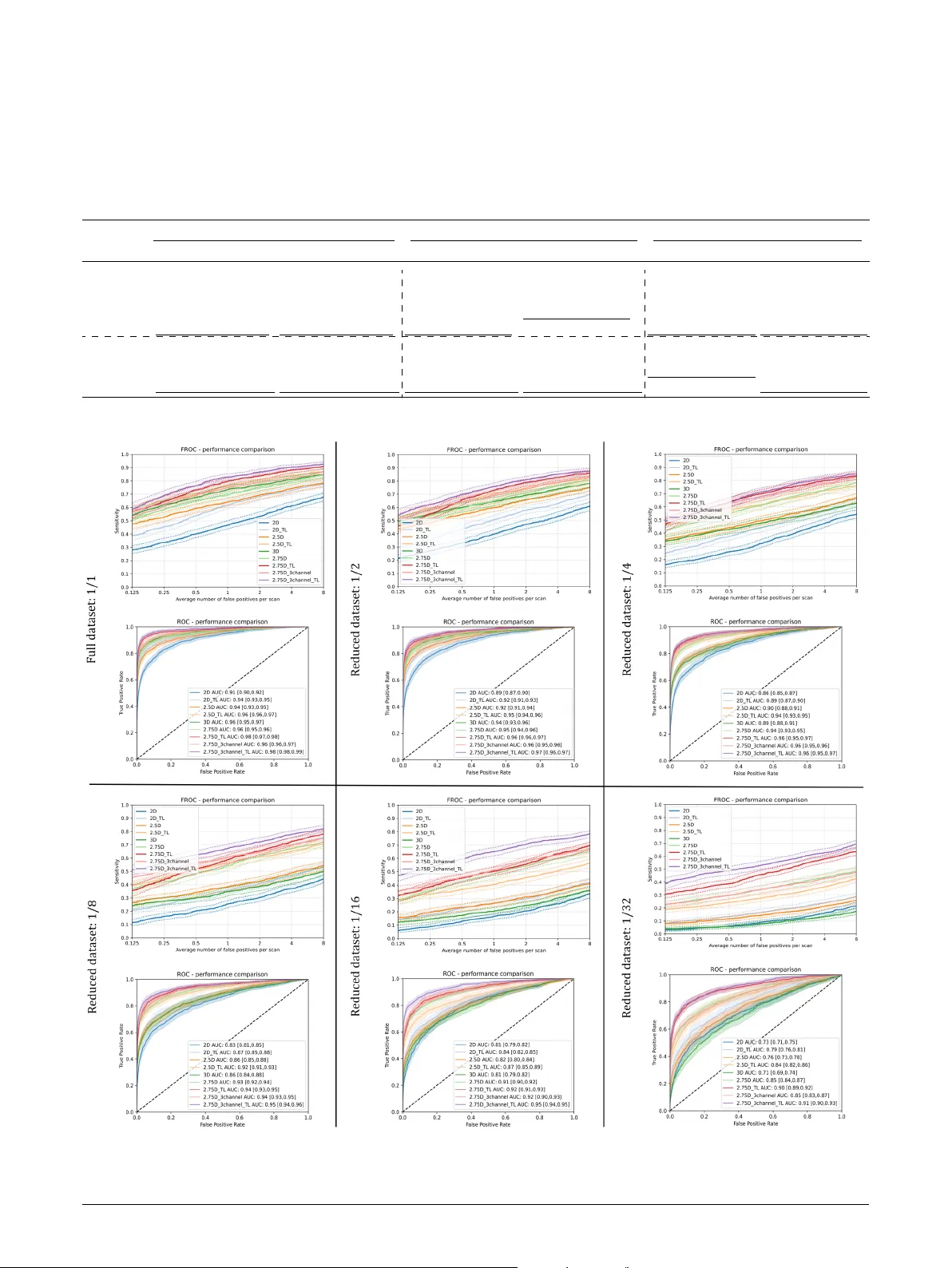
본 연구는 3차원 의료 영상 데이터를 효율적으로 2차원 형태로 변환해 2D CNN을 활용할 수 있게 하는 새로운 방법인 2.75D를 제안한다. 기존 3D CNN은 부피 전체 정보를 학습해 높은 정확도를 보이지만, 대규모 GPU 메모리와 연산량, 그리고 3D 전이학습 모델 부족이라는 실용적 제약이 있다. 반면 2D CNN은 사전학습된 모델이 풍부하고 연산이 가볍지만, 3D 구조를 직접 다루지 못한다. 2.5D는 여러 정면을 병렬로 입력해 일부 3D 정보를 보완하지만, 샘플링이 임의적이어서 공간적 연관성을 충분히 전달하지 못한다.
2.75D는 이러한 한계를 극복하기 위해 나선형 스캔(spiral scanning) 기법을 도입한다. 3D 부피의 중심을 기준으로 구면을 따라 나선형으로 라인을 뽑아, 각 라인에 포함된 voxel 값을 열(column)로 정렬하고, 라인 순서를 행(row)으로 배열한다. 결과적으로 3D 부피의 모든 방향에서의 구조적 정보를 하나의 2D 이미지에 압축한다. 논문에서는 64³ 패치를 기준으로 N=9(azimuth 단계)와 32개의 샘플 포인트를 사용해 32×123 크기의 2D 이미지를 만든다. 이 이미지 크기는 기존 2D 입력(64×64)보다 작지만, 공간 정보를 더 풍부하게 담고 있어 성능이 향상된다.
다중 뷰 전략인 2.75D×3는 기본 축(X, Y, Z) 각각에 대해 독립적인 2.75D 이미지를 생성하고, 이를 3채널 입력으로 결합한다. 이렇게 하면 서로 다른 방향에서 얻은 구조적 특징을 동시에 학습할 수 있어 분류 정확도가 추가로 상승한다.
세 가지 공개 데이터셋(LUNA16 폐 CT, PROSTATE 유방 MRI, Duke 전립선 MRI)을 대상으로 2D, 2.5D, 3D와 비교 실험을 수행했다. LUNA16에서는 2.75D가 스크래치 학습 시에도 3D CNN을 능가했으며, ImageNet 사전학습된 ResNet, EfficientNet 등을 전이학습했을 때 성능 차이가 더욱 크게 나타났다. 특히 제한된 학습 데이터(전체의 10% 이하)에서도 2.75D는 안정적인 학습 곡선을 유지했으며, 3D CNN은 과적합 위험이 커졌다.
시간 및 메모리 효율성도 크게 개선되었다. 2.75D는 2.5D·3D 대비 훈련 시간과 추론 시간이 각각 약 30~50% 단축되었으며, 메모리 사용량도 크게 감소한다. 이는 2D 연산 최적화와 작은 입력 크기 덕분이다.
결론적으로 2.75D는 “데이터 표현” 단계에서 3D 정보를 효과적으로 압축해 2D CNN의 장점을 그대로 활용하게 함으로써, 작은 데이터셋에서도 높은 성능을 달성하고, 연산·메모리 비용을 크게 절감한다. 이는 임상 현장에서 대규모 스크리닝 및 실시간 진단 지원 시스템에 적용하기에 매우 유리한 접근법이다.
원본 논문
고화질 논문을 불러오는 중입니다...
댓글 및 학술 토론
Loading comments...
의견 남기기