생체조직 이미지 색균형 기반 셀리악병·환경성 장염 자동 진단
초록
본 연구는 색균형 전처리와 패치‑클러스터링을 적용한 합성곱 신경망(CNN)으로, 셀리악병(CD), 환경성 장염(EE), 정상 소장 조직을 구분한다. 1,000장의 듀오덴얼 생검 이미지(3118개 패치)로 학습한 모델은 CD 0.99, EE 1.00, 정상 0.97의 AUC를 달성하였다.
상세 분석
이 논문은 저자들이 저비용·고효율의 병리학적 영상 분류 파이프라인을 설계한 점에서 의미가 크다. 첫 단계는 전통적인 Whole‑Slide Image(WSI)를 그대로 사용하면 메모리·연산량이 과도해지는 문제를 해결하기 위해 1,000 × 1,000 픽셀 크기의 패치로 분할한다. 그러나 단순 분할만으로는 배경이나 비정상적인 영역이 포함된 불필요한 패치가 다수 생성된다. 이를 보완하기 위해 저자들은 자동인코더(Autoencoder)로 패치의 저차원 임베딩을 추출하고, K‑means 클러스터링을 통해 ‘유용’과 ‘불필요’ 두 그룹으로 나눈다. 클러스터 1(유용)에는 CD, EE, 정상 조직의 핵심 병변이 포함되며, 전체 패치의 34 %만이 최종 학습에 사용된다.
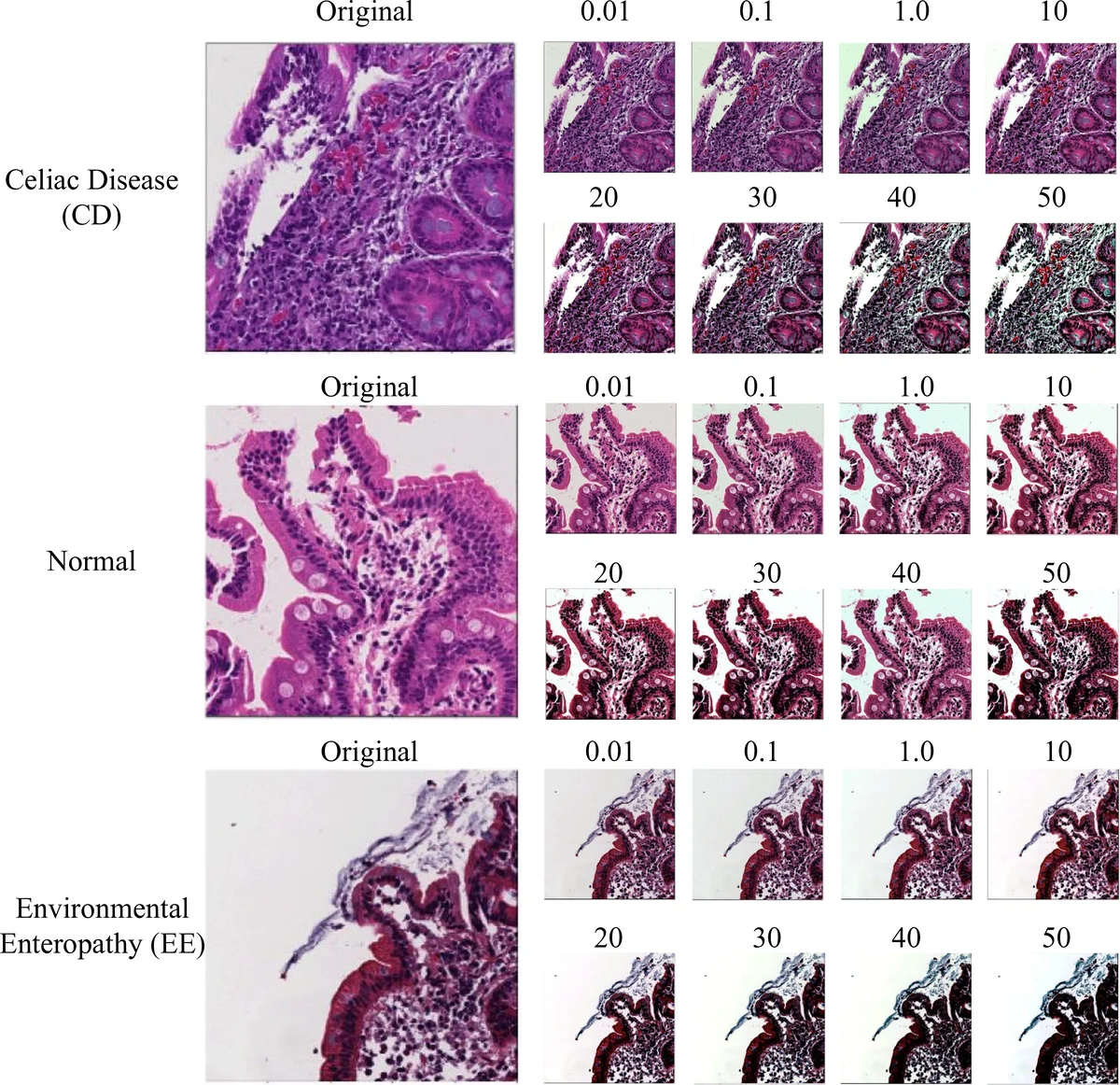
색균형(Color Balancing) 단계는 H&E 염색의 변동성을 정규화한다. 논문은 광원 스펙트럼 I(λ), 표면 반사율 S(λ), 센서 감도 C(λ)를 이용한 물리적 모델을 제시하고, 이를 행렬 연산 α·A·I_w·RGB_in^γ 형태로 구현한다. 색조 보정 비율을 0.01%부터 50%까지 다양하게 적용해 시각적 일관성을 확보했으며, 이는 CNN이 색상 편향에 덜 민감하도록 만든다.
CNN 구조는 비교적 단순하지만 목적에 최적화돼 있다. 입력 패치는 3채널 RGB이며, 첫 번째 Conv 레이어는 32개의 3 × 3 필터, 그 뒤 5 × 5 MaxPooling으로 1,000 × 1,000 → 200 × 200으로 축소한다. 두 번째 Conv‑Pool 조합이 200 × 200 → 40 × 40, 세 번째 Conv‑Pool 조합이 40 × 40 → 8 × 8로 최종 특성 맵을 만든다. Flatten 후 128개의 뉴런을 가진 완전 연결층을 거쳐 Softmax 출력층에서 3클래스를 예측한다. 활성화 함수는 ReLU, 최적화는 Adam(학습률 0.001, β₁=0.9, β₂=0.999)이며 손실은 Sparse Categorical Cross‑Entropy를 사용한다.
성능 평가는 ROC 곡선 기반 AUC로 이루어졌으며, CD 0.99, EE 1.00, 정상 0.97이라는 높은 값을 기록했다. 이는 색균형과 패치 클러스터링이 모델의 구분력을 크게 향상시켰음을 시사한다. 다만, 데이터셋 규모가 121장의 슬라이드(총 3,118 패치)로 제한적이며, 클래스 비율이 약 41 % 정상, 33 % CD, 26 % EE로 다소 불균형이다. 교차 검증이나 외부 독립 테스트셋이 제시되지 않아 일반화 가능성에 대한 검증이 부족하다. 또한, 모델이 병변의 미세한 형태학적 특징(예: 상피세포 비대, 림프구 침윤 정도)을 어떻게 학습했는지에 대한 시각화(Grad‑CAM 등)도 제공되지 않아 임상 적용 시 해석 가능성이 제한된다.
향후 연구에서는 (1) 다기관·다국가 데이터셋을 통한 외부 검증, (2) 클래스 불균형을 해결하기 위한 데이터 증강 및 비용 민감 학습, (3) 모델 설명성을 높이기 위한 시각화 기법 도입, (4) 전이 학습이나 보다 깊은 네트워크(ResNet, EfficientNet)와의 비교 실험이 필요하다. 특히, 색균형 파라미터를 자동 최적화하는 메타‑러닝 접근법은 실제 병리실 환경에서의 적용성을 크게 높일 수 있을 것이다.
댓글 및 학술 토론
Loading comments...
의견 남기기