대규모 적응형 앙상블 생체분자 시뮬레이션
초록
**
본 논문은 적응형 앙상블 기법을 활용해 생체분자 시뮬레이션을 대규모 HPC 환경에서 효율적으로 실행할 수 있는 소프트웨어 프레임워크인 Ensemble Toolkit(EnTK)의 확장을 제안한다. 적응형 워크플로우의 유형을 정의하고, 두 가지 대표적인 과학 애플리케이션(Expanded Ensemble와 Markov State Modeling)을 구현·평가함으로써, 수천 코어·수천 개의 앙상블 멤버를 2¹² 규모까지 확장 가능한 방법을 제시한다.
**
상세 분석
**
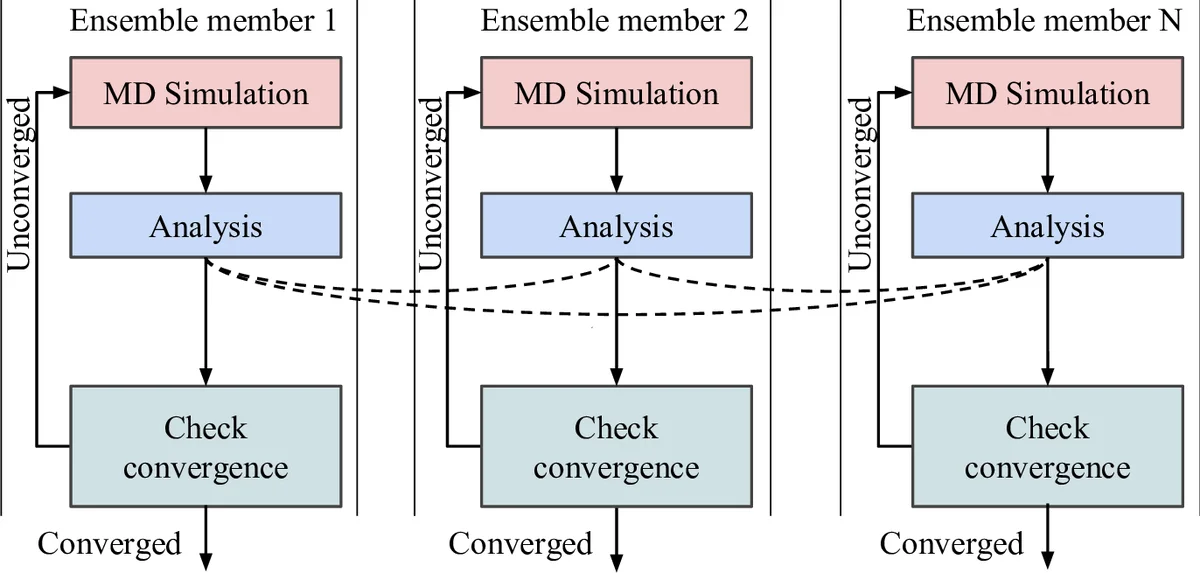
이 연구는 적응형 앙상블 시뮬레이션이 기존의 순차적 MD 실행보다 수천 배 이상의 효율성을 제공한다는 점을 강조한다. 저자들은 적응성을 “실행 중간에 얻은 데이터에 기반해 작업의 파라미터·구성을 동적으로 변경하는 능력”으로 정의하고, 이를 크게 세 가지 차원(시뮬레이션 파라미터, 작업 흐름 구조, 외부 자원·데이터)에서 분류한다. EnTK는 작업을 ‘Task’, 작업 간 의존성을 ‘Task Graph’로 모델링하여, 런타임에 그래프를 수정하거나 새로운 작업을 삽입하는 ‘Adaptive’ 모듈을 추가한다. 핵심 구현은 (1) 작업 정의와 메타데이터를 JSON/YAML 형태로 선언, (2) 파이썬 기반의 ‘Adaptor’ 인터페이스를 통해 사용자 정의 적응 로직을 삽입, (3) MPI·SSH 기반의 실행 엔진이 동적으로 할당된 노드에 작업을 스케줄링하도록 설계된 점이다.
두 가지 과학 사례는 각각 다른 적응 패턴을 보여준다. Expanded Ensemble(EE)에서는 각 워커가 로컬 분석을 수행하거나, 전역 분석을 위해 비동기적으로 데이터를 교환한다. 여기서 적응은 시뮬레이션 조건 가중치를 실시간으로 업데이트해 다음 라운드의 샘플링 분포를 조정한다. 반면 Markov State Modeling(MSM)에서는 수십만 개의 짧은 MD 트라젝터리를 수집·클러스터링한 뒤, 전이 행렬을 추정하고, 불확실도가 큰 마이크로스테이트에 추가 샘플을 할당한다. 이 과정은 ‘Adaptive Sampling’이라고 불리며, 매 반복마다 새로운 초기 구조를 생성해 워크플로우에 삽입한다.
성능 평가에서는 세 개의 서로 다른 슈퍼컴퓨터(Stampede2, Theta, Summit)에서 2¹²(4096) 멤버, 수천 코어 규모의 실험을 수행했다. 적응 오버헤드는 전체 실행 시간의 2~5% 수준에 머물렀으며, 특히 전역 분석을 포함한 EE 경우 네트워크 대역폭이 제한될 때 오버헤드가 약간 증가했다. 그러나 전체 시뮬레이션 가속도는 10배 이상, 경우에 따라 1000배에 달하는 효율 향상을 보였다.
이 논문의 주요 기여는 (i) 적응형 앙상블 워크플로우의 유형 체계화, (ii) EnTK에 적응성 지원을 통합한 설계·구현, (iii) 적응 오버헤드 정량화, (iv) 두 가지 대표적인 과학 애플리케이션을 통한 실증, (v) 도메인 독립적인 프레임워크 제공이다. 특히 MD 엔진(NAMD, GROMACS 등)과 무관하게 적용 가능하도록 설계된 점은 향후 다양한 과학 분야(재료 과학, 기후 모델링 등)로의 확장성을 크게 높인다.
**
댓글 및 학술 토론
Loading comments...
의견 남기기