불확실성 기반 그래프 컨볼루션 네트워크를 활용한 장기 분할 정밀화
초록
본 논문은 CT 영상에서 장기(췌장·비장) 분할 결과를 개선하기 위해, 2D U‑Net의 불확실성 맵을 이용해 부분적으로 라벨링된 3D 그래프를 구성하고, 이를 semi‑supervised 방식으로 학습한 그래프 컨볼루션 네트워크(GCN)로 후처리하는 방법을 제안한다. NIH 췌장 데이터와 Medical Segmentation Decathlon 비장 데이터를 실험한 결과, 기존 CRF 기반 정밀화보다 Dice 점수가 각각 1%·2% 향상되었다.
상세 분석
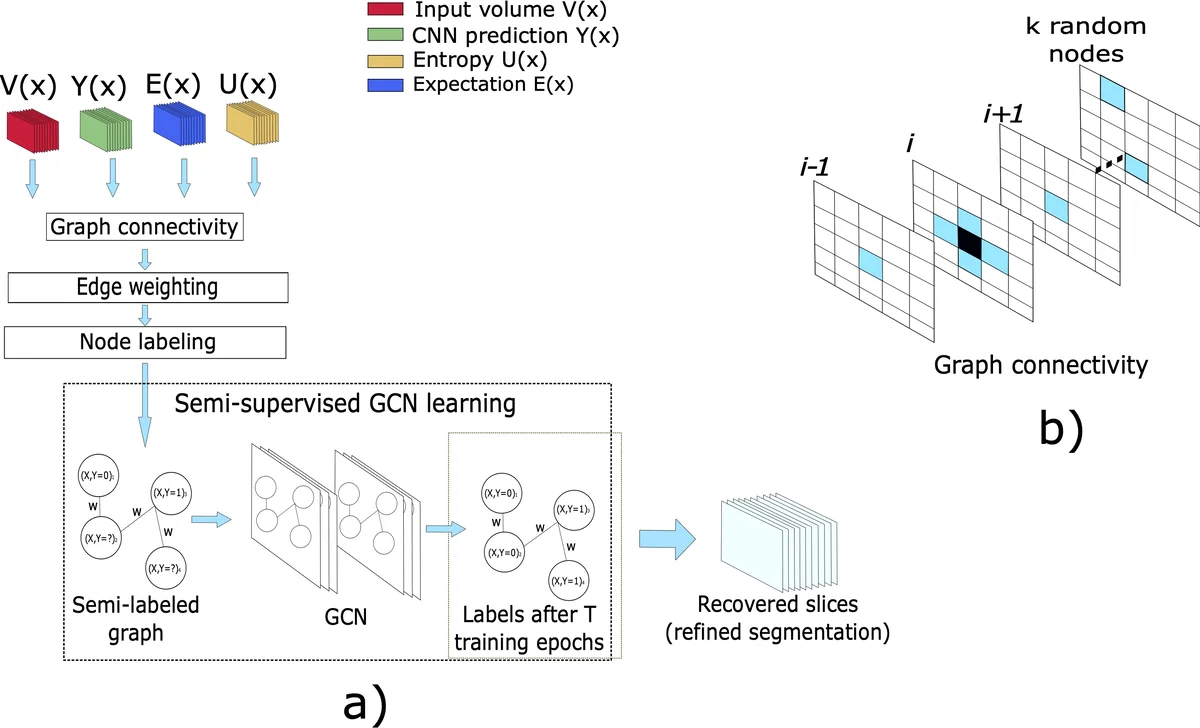
이 연구는 기존 CNN 기반 장기 분할에서 발생하는 경계 부정확성 및 FP/FN을 보완하기 위해 두 단계 접근법을 채택한다. 첫 단계에서는 Monte‑Carlo Dropout(MCDO)을 활용해 2D U‑Net의 출력에 대한 불확실성(엔트로피) 맵을 추정한다. 엔트로피가 일정 임계값 τ를 초과하는 voxels를 ‘불확실 영역’으로 정의하고, 이와 동시에 모델이 높은 확신을 보이는 배경·전경 voxels를 ‘라벨된 노드’로 활용한다. 이렇게 얻어진 불확실성 기반 ROI는 dilation(불확실 영역)와 기대값(E) 이진화 결과를 합쳐 구성되며, 그래프의 노드 수를 크게 줄여 메모리 효율성을 확보한다. 각 노드는 intensity(V), 기대값(E), 엔트로피(U) 세 가지 특성 벡터로 표현된다.
그래프 연결은 6방향 인접 이웃과 무작위로 선택된 k=16개의 전역 노드와의 연결을 결합한 희소 연결 방식으로 설계되었다. 가중치는 Gaussian 커널과 클래스 확률 다양성(div) 함수를 결합한 additive 형태이며, 이는 유사·비유사 노드 간 정보 전달을 동시에 가능하게 한다. 이러한 그래프 구조 위에 2‑layer GCN(숨은 차원 32, 출력 1)을 semi‑supervised 학습시켜, 라벨된 고확신 노드의 레이블을 지도 학습 신호로, 나머지 불확실 노드를 무라벨 데이터로 활용한다. 손실 함수는 바이너리 엔트로피이며, Adam 옵티마이저와 1e‑2 학습률로 200 epoch 동안 최적화한다.
실험에서는 2D U‑Net을 기본 CNN으로 사용했으며, dropout 비율 0.3, stochastic pass 수 20을 적용해 불확실성 맵을 생성한다. 정밀화 후 전체 볼륨에 대해 GCN 출력을 그대로 적용하는 방식을 선택했으며, 이는 부분 교체보다 Dice 향상이 더 크게 나타났다. 비교 대상인 CRF는 dense pairwise 잠재력을 사용했지만, 그래프 기반 접근법에 비해 메모리·연산 비용이 높고, 불확실 영역에 대한 전역적 정보 전달이 제한적이었다. 결과적으로 GCN 정밀화는 췌장(76.9→77.8%)과 비장(93.2→95.1%)에서 각각 평균 Dice를 1.0%·1.9% 상승시켰다.
이 방법의 강점은 (1) 기존 CNN 모델을 그대로 재사용하면서도 불확실성 정보를 활용해 후처리 가능, (2) 희소 그래프 설계로 3D 전체 볼륨을 효율적으로 처리, (3) semi‑supervised 학습으로 라벨링 비용 최소화이다. 한계점으로는 불확실성 임계값 τ와 ROI 설정이 데이터마다 민감하게 작용할 수 있으며, 2D 기반 불확실성 추정이 3D 연속성을 완전히 반영하지 못한다는 점이다. 향후 연구에서는 3D CNN 기반 MCDO와 동적 그래프 구조 최적화를 통해 정밀화 성능과 일반화를 동시에 향상시킬 여지가 있다.
댓글 및 학술 토론
Loading comments...
의견 남기기