인공 세균 뉴런으로 구현한 단일층 인공 신경망
초록
본 연구는 유전공학적으로 설계된 대장균을 인공 뉴런으로 활용해 단일층 인공 신경망(ANN)을 구현하였다. 외부 화학 물질을 입력으로 받아 선형 결합 후 합성 유전자 회로가 구현한 로그‑시그모이드 활성화 함수를 통과시켜 형광 단백질로 출력한다. 무게와 바이어스는 프로모터 강도·리보솜 결합 부위·전사 억제제 농도 등을 조절해 수동으로 설정했으며, 이를 기반으로 2‑to‑4 디코더와 1‑to‑2 디멀티플렉서를 구현하였다. 생물학적 세포를 ANN 하드웨어로 활용한 최초 사례로, 향후 생명공학‑컴퓨팅 융합 연구에 새로운 길을 제시한다.
상세 분석
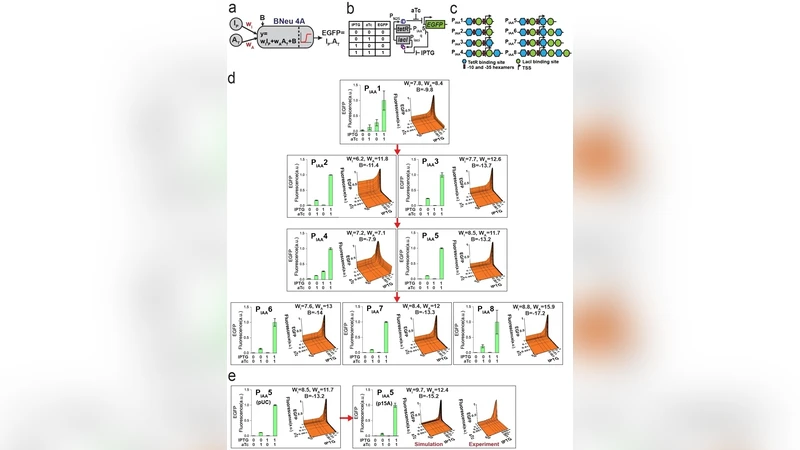
이 논문은 인공 신경망을 전통적인 전자·광학·DNA‑in‑vitro 시스템이 아닌 살아있는 세포 내에서 구현한다는 근본적인 전환점을 제시한다. 저자들은 단일 대장균 세포를 ‘인공 뉴런’으로 정의하고, 입력 신호를 외부 화학 물질(예: IPTG, 아라비노스 등)로 설정한다. 각 입력은 세포막 수용체 혹은 직접적인 전사인자 활성화를 통해 내부 농도에 비례하는 전사량으로 변환되며, 이는 선형 가중치와 바이어스에 해당한다. 가중치는 프로모터 강도, 리보솜 결합 부위(RBS) 효율, 전사 억제제(예: LacI, TetR)의 발현 수준을 조절함으로써 정량화된다. 바이어스는 기본 전사 레벨을 조절하는 ‘constitutive’ 프로모터의 강도로 구현된다.
핵심은 로그‑시그모이드 형태의 활성화 함수를 합성 유전자 회로로 재현한 점이다. 저자들은 두 단계의 전사‑번역 억제·활성화 모듈을 결합해 입력 신호의 로그 변환을 수행하고, 이어서 히스톤‑유사 억제 회로를 통해 포화와 비선형성을 부여한다. 결과적으로 출력은 GFP·RFP 등 형광 단백질의 발현량으로 측정되며, 이는 연속적인 실시간 모니터링이 가능하도록 설계되었다.
구현된 ANN은 단일층 퍼셉트론 구조로, 2개의 입력을 4개의 출력으로 매핑하는 2‑to‑4 디코더와, 1개의 입력을 2개의 출력 중 하나로 선택하는 1‑to‑2 디멀티플렉서를 시연했다. 각 논리 함수는 가중치와 바이어스를 조정해 수동으로 ‘학습’시켰으며, 실험 결과는 기대한 진리표와 일치하였다.
기술적 강점은 (1) 생물학적 시스템의 고유한 병렬성 및 자가 복제 능력, (2) 화학 신호를 직접 처리함으로써 전자‑기반 인터페이스 없이도 환경 감지가 가능함, (3) 유전 회로 설계의 모듈화로 다양한 논리 연산을 확장 가능하다는 점이다. 반면 제한점으로는 (①) 가중치 조정이 현재 수동이며 고정돼 있어 대규모 학습에 부적합, (②) 신호 전달 속도가 전자 회로에 비해 수십 분~시간 수준으로 느리며, (③) 세포 간 연결이 물리적·화학적 확산에 의존해 정확한 연결 구조를 구현하기 어렵다. 또한, 형광 출력의 감도와 배경 잡음, 세포 성장에 따른 회로 변이 등 실험적 변동성이 존재한다.
향후 연구는 (i) CRISPR‑i/a 기반의 가중치 자동 조정 메커니즘, (ii) 세포‑세포 전자 전송(예: 전도성 나노와이어) 혹은 합성 신호 전달 분자를 이용한 정밀 연결, (iii) 다층 네트워크와 피드백 루프를 포함한 복합 회로 설계, (iv) 환경 센서와 연계한 실시간 적응 학습 등으로 확장될 수 있다. 궁극적으로는 바이오‑컴퓨팅 플랫폼으로서, 의료 진단, 환경 모니터링, 스마트 바이오‑공정 제어 등에 적용 가능성이 기대된다.
댓글 및 학술 토론
Loading comments...
의견 남기기