LabPipe: 대규모 임상 대사체 연구를 위한 확장 가능한 데이터·메타데이터 관리 플랫폼
초록
LabPipe는 로컬 클라이언트와 원격 서버 기반의 모듈형 시스템으로, 임상 대사체 연구에서 샘플 수집·메타데이터 입력·데이터 전송을 자동화한다. NoSQL 데이터베이스와 플러그인 아키텍처를 활용해 다양한 장비와 프로토콜을 지원하며, 영국 레스터 대학의 EMBER 프로젝트에서 다중 사이트·다중 기기 환경에 성공적으로 적용되었다.
상세 분석
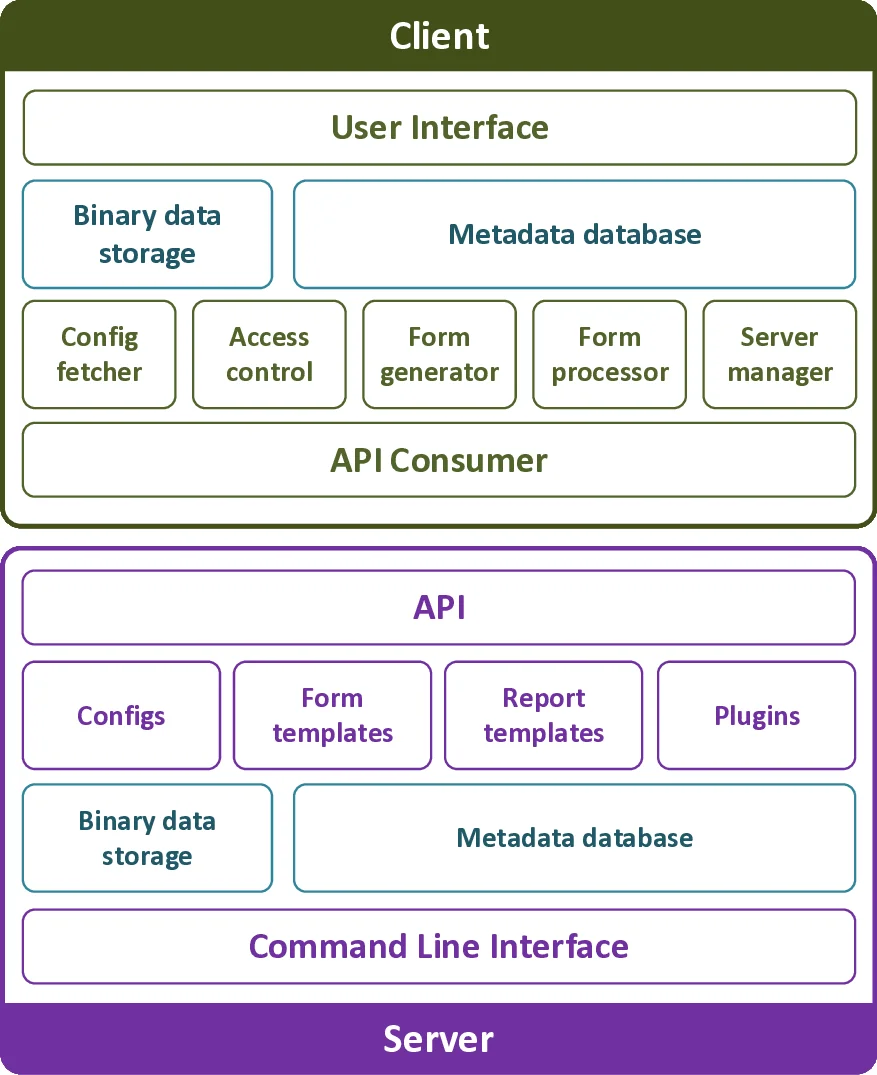
LabPipe는 클라이언트‑서버 구조를 기본으로 하며, 서버(LPserver)는 경량화된 RESTful API와 역할 기반 인증을 제공한다. 백엔드에 NoSQL 데이터베이스를 채택함으로써 메타데이터 스키마를 유연하게 정의하고, 새로운 수집 구성(configuration)을 JSON 형태로 로드할 수 있다. 클라이언트(LPclient)는 Electron 프레임워크로 구현돼 Windows, macOS, Linux에서 동일하게 동작한다. 사용자는 서버에서 제공하는 설정 파일과 폼 템플릿을 자동으로 받아 로컬에서 샘플 수집 폼을 생성하고, 현장 입력된 메타데이터와 파일을 연계한다. 파일 ID 자동 생성, 변경 파일 자동 탐지, 네트워크 연결이 불안정할 경우 로컬 큐에 저장 후 재전송하는 폴백 메커니즘 등 자동화 기능이 핵심이다. 플러그인 인터페이스를 통해 이메일 알림, 추가 데이터 변환, 맞춤형 검증 로직 등을 손쉽게 확장할 수 있다. EMBER 연구에서는 4가지 호흡 샘플링 방식(온라인·오프라인 포함)과 9대의 장비를 두 개 사이트에서 동시에 관리했으며, 기존의 종이 기반 기록과 USB 수동 전송에 비해 데이터 손실 위험을 크게 감소시켰다. 또한, 메타데이터와 분석 결과를 즉시 서버에 업로드함으로써 연구자들이 중앙 데이터베이스에 바로 접근해 통합 분석을 수행할 수 있었다. 기존 i2b2, REDCap, OpenSpecimen 등은 각각 데이터 웨어하우징·eCRF·바이오뱅크 관리에 특화돼 있었지만, 로컬 파일 시스템과의 직접 연동·자동 전송을 지원하지 않아 LabPipe가 충족시키지 못했던 요구를 메워준다. 현재는 대사체 외에도 흐름세포학, 실시간 PCR 등 다른 실험실 기반 데이터에도 적용 가능하도록 설계 단계에 있으며, ISA‑Tab 표준 자동 변환·온톨로지 연동, 감사 로그 강화 등 향후 기능이 로드맵에 포함돼 있다.
댓글 및 학술 토론
Loading comments...
의견 남기기