다양한 MRI 영상 분할을 위한 딥러닝 모델 DeepMRSeg
DeepMRSeg는 다중 스케일 특징 추출을 위해 수정된 UNet 구조에 ResNet 및 Inception‑ResNet‑A 블록을 결합한 모델이다. 최소 전처리된 원시 MRI에 바로 적용 가능하며, 백색질 병변, 심부 뇌 구조 및 해마 분할 등 여러 neuroimaging 과제에서 기존 UNet 대비 높은 Dice와 정확도를 달성한다. 코드와 사전 학습된 가중치를 공개하여 연구자들이 손쉽게 활용할 수 있다.
저자: Jimit Doshi, Guray Erus, Mohamad Habes
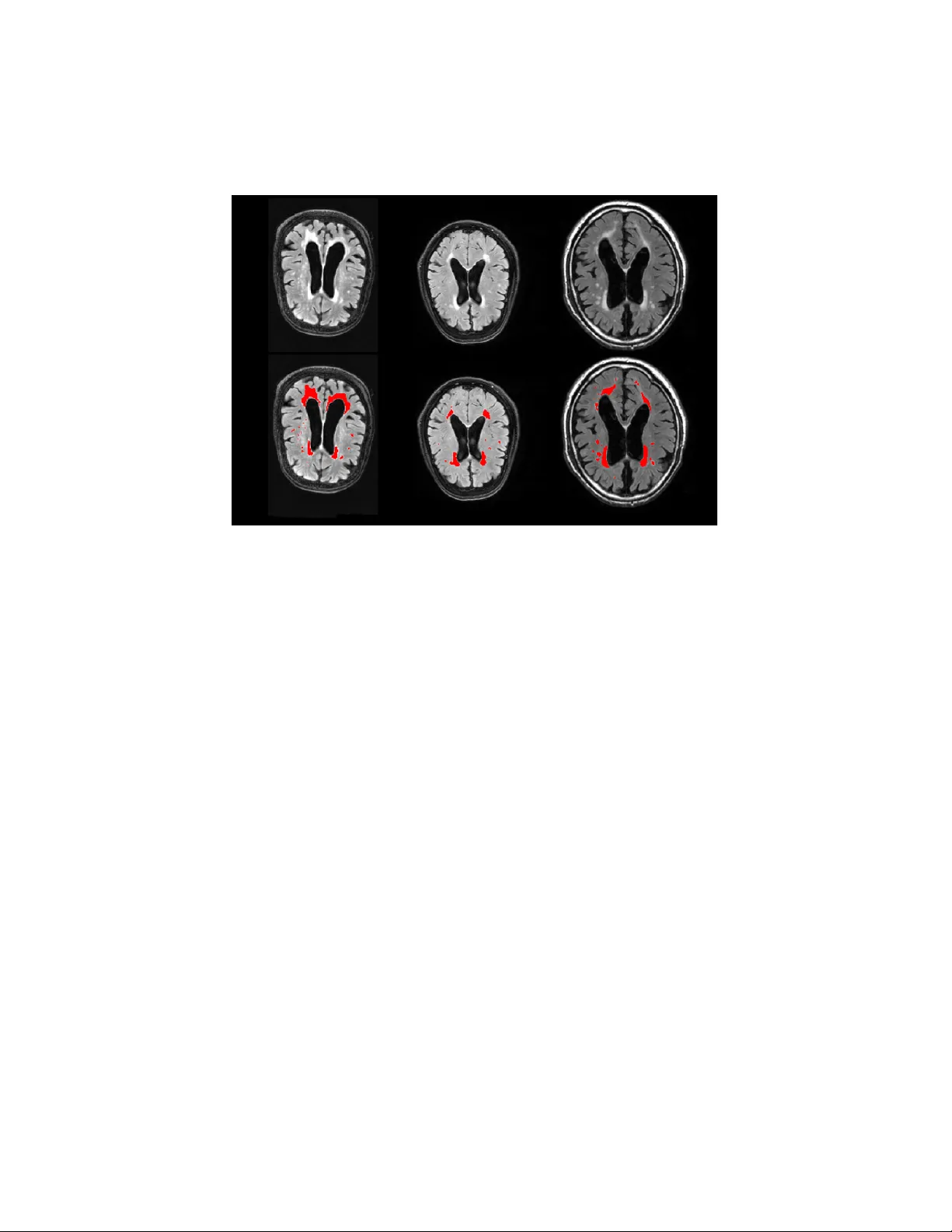
본 논문은 뇌 영상 분석에서 핵심적인 역할을 하는 해부학적 및 병변 분할 작업을 위해 새로운 딥러닝 기반 프레임워크인 DeepMRSeg를 제안한다. 기존의 UNet 구조는 뛰어난 성능을 보였지만, 스케일 다양성 부족, 깊은 네트워크 학습 시 발생하는 그래디언트 소실, 그리고 max‑pool에 의한 경계 손실 등의 한계가 존재한다. 이를 해결하기 위해 저자들은 세 가지 주요 설계 요소를 도입하였다.
첫 번째 설계 요소는 인코더와 디코더 양쪽에 ResNet 잔차 블록을 삽입한 것이다. ResNet은 입력 신호를 그대로 전달하는 shortcut 연결을 통해 네트워크가 잔차 매핑을 학습하도록 하여, 층이 깊어져도 학습이 안정적으로 진행되도록 돕는다. 이는 특히 3D MRI와 같이 데이터 차원이 높은 경우에 유용하며, 모델이 더 깊어질수록 성능이 향상되는 효과를 가져온다.
두 번째 설계 요소는 Inception‑ResNet‑A 구조를 변형한 ResInc 모듈이다. 이 모듈은 입력 피처맵을 네 개의 병렬 브랜치로 분할하고, 각각 1×1, 3×3, 5×5 등 다양한 커널 크기의 컨볼루션을 적용한다. 각 브랜치는 서로 다른 수용 영역을 학습함으로써 다중 스케일 특징을 동시에 추출한다. 이후 1×1 컨볼루션을 통해 차원을 재조정하고, 잔차 연결을 통해 원본 피처와 결합한다. 이러한 구조는 파라미터 수를 크게 늘리지 않으면서도 네트워크 폭을 확대할 수 있게 해준다. 저자들은 ResInc 모듈이 전통적인 ResNet 블록 대비 파라미터 수가 약 1/3에 불과함을 강조한다.
세 번째 설계 요소는 전통적인 max‑pool 대신 stride‑2 1×1 컨볼루션을 사용한 Transition Down 블록이다. 이 블록은 다운샘플링 과정에서 학습 가능한 가중치를 통해 피처맵을 축소하므로, 단순히 최대값을 선택하는 max‑pool에 비해 경계 정보를 더 잘 보존한다. 또한, 이 과정에서 피처맵 수를 두 배로 늘릴 수 있어 디코더 단계에서 풍부한 정보를 활용할 수 있다. Upsampling은 transposed convolution(1×1, stride 2)으로 수행되며, 인코더의 skip connection과 결합해 정확한 위치 정보를 복원한다.
학습 과정에서는 softmax cross‑entropy, 평균 제곱 오차(MSE), 그리고 soft Intersection‑over‑Union(IoU)를 동일 가중치로 합산한 복합 손실 함수를 사용한다. 이는 픽셀‑레벨 정확도와 영역 겹침을 동시에 최적화하도록 설계된 것이다. 최적화 알고리즘은 Adam이며, 초기 학습률 0.05에 매 epoch마다 0.98의 감쇠율을 적용한다. 데이터 증강으로는 좌우 플립, 무작위 회전·이동, 밝기·대비 변화를 적용해 모델의 일반화 능력을 강화하였다.
평가에서는 세 가지 공개 데이터셋을 사용하였다. 첫 번째는 MICCAI 2017 백색질 병변(WML) 챌린지 데이터로, 60명의 피험자에 대해 T1 및 FLAIR 스캔과 전문가가 만든 병변 마스크가 제공된다. 두 번째는 MICCAI 2013 심부 뇌 구조 데이터로, OASIS 프로젝트의 T1 스캔과 14개의 뇌 구조(양측) 라벨이 포함된다. 세 번째는 Medical Decathlon 해마 데이터로, 195명의 피험자에 대한 3D T1 MPRAGE와 해마 몸통·꼬리 라벨이 제공된다. 각 과제마다 4‑fold 교차 검증을 20회 반복해 평균 및 표준편차를 보고하였다.
비교 대상은 배치 정규화 레이어만 추가된 기존 UNet이며, 손실 함수와 데이터 증강은 동일하게 유지하였다. 실험 결과, DeepMRSeg는 평균 Dice(또는 F1) 점수에서 기존 UNet 대비 2~5% 향상을 보였으며, 특히 작은 병변이나 복잡한 경계가 있는 구조에서 F2 점수와 Balanced Accuracy가 현저히 개선되었다. 파라미터 효율성 측면에서도 ResInc 모듈 덕분에 전체 파라미터 수는 기존 ResNet 기반 UNet 대비 약 30% 수준으로 감소하면서도 네트워크 깊이와 폭을 확대할 수 있었다.
마지막으로 저자들은 코드와 사전 학습된 모델을 온라인 플랫폼(IPP)에서 공개함으로써, 연구자와 임상가가 별도의 환경 설정 없이 바로 적용할 수 있도록 하였다. 이는 재현성을 높이고, 다양한 연구 분야에서 빠른 프로토타이핑과 임상 적용을 촉진한다는 점에서 큰 의미를 가진다.
요약하면, DeepMRSeg는 다중 스케일 특징 추출, 잔차 학습, 경계 보존이라는 세 가지 혁신적 설계를 결합해 MRI 기반 뇌 구조 및 병변 분할에서 기존 방법을 능가하는 성능을 달성했으며, 범용성과 실용성을 동시에 갖춘 딥러닝 프레임워크로 평가된다.
원본 논문
고화질 논문을 불러오는 중입니다...
댓글 및 학술 토론
Loading comments...
의견 남기기