유전체 코돈 분포와 삼중 나선 가설을 통한 생명 3계통 진화 해석
초록
본 논문은 현대 유전체의 코돈 분포를 통계적으로 분석하여, 전생물학적 코돈 모집 순서와 연계된 ‘생물다양성 공간’을 구축한다. 이 공간에서 종 간 유클리드 거리를 계산하면 기존 3계통(세균·고세균·진핵) 나무를 재구성할 수 있음을 보이며, 코돈 자체의 진화 나무도 동일한 모집 순서를 반영한다. 또한, 삼중 나선(DNA) → 이중 나선 전환 과정에서 ‘3’이라는 수가 코돈 길이의 기원이라는 가설을 제시한다.
상세 분석
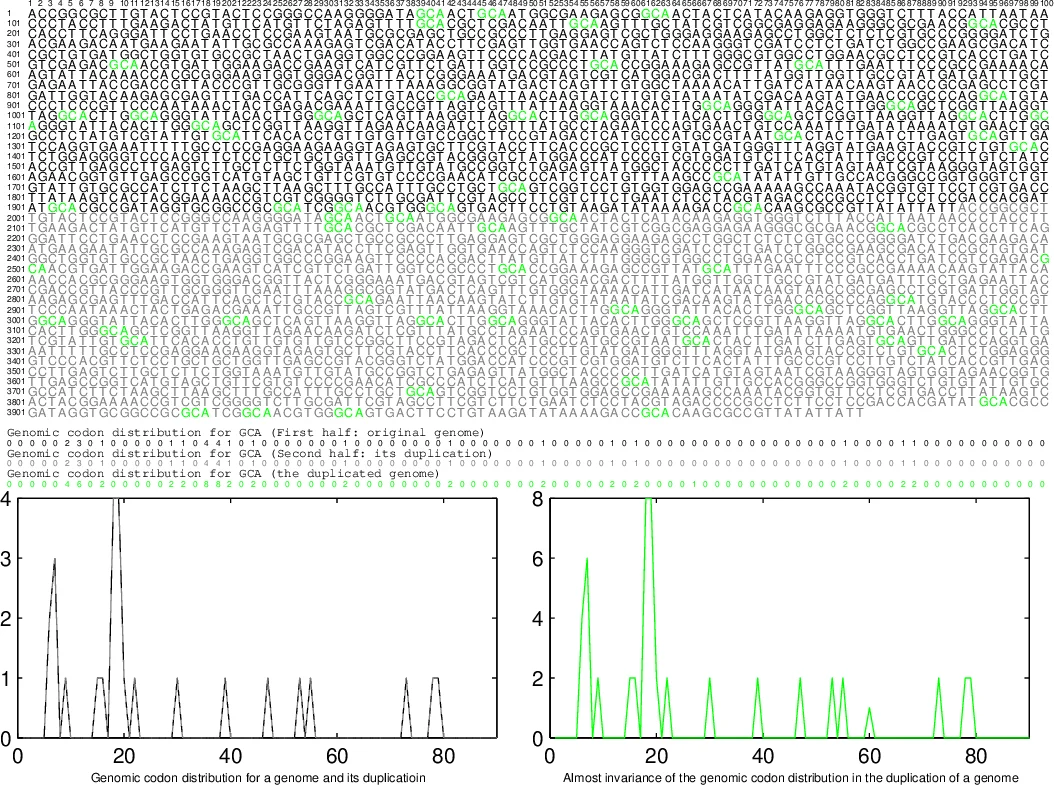
이 연구는 크게 네 가지 핵심 아이디어에 기반한다. 첫째, 전생물학적 코돈 ‘모집 순서’를 가정하고, 현대 완전 유전체에서 64개의 코돈이 나타나는 간격 분포(코돈 간 거리)를 정규화하여 ‘유전체 코돈 분포’를 정의한다. 둘째, 각 종의 코돈 분포를 벡터화한 뒤, 코돈 모집 순서에 따라 ‘경로 편향(route bias)’, ‘계층 편향(hierarchy bias)’, ‘변동 진폭(fluctuation amplitude)’이라는 세 축을 도입해 3차원 ‘생물다양성 공간(biodiversity space)’을 만든다. 셋째, 이 공간에서 유클리드 거리 행렬을 계산하고, 거리 기반 클러스터링/계통수 재구성을 수행함으로써 전통적인 3계통 트리를 재현한다. 넷째, 코돈 자체의 분포를 비교해 코돈 진화 트리를 만들고, 이것이 앞서 제시한 코돈 모집 로드맵과 일치한다는 점을 강조한다.
통계적 방법론은 ‘코돈 간 거리 분포’를 이용한다는 점에서 독창적이지만, 구체적인 정규화 절차, 거리 계산 방식, 그리고 클러스터링 알고리즘(예: UPGMA, Neighbor‑Joining 등)의 선택이 논문에 명시되지 않아 재현 가능성이 낮다. 또한, 코돈 모집 순서를 ‘전생물학적 로드맵’이라 부르지만, 그 근거가 실험적·화학적 데이터가 아닌 저자 이전 논문에 의존하고 있어 가설적 성격이 강하다.
삼중 나선(DNA) → 이중 나선 전환을 통해 ‘3’이라는 수가 코돈 길이의 기원이 된다는 주장은 흥미롭지만, 현재 알려진 삼중 나선 구조는 제한된 조건(고농도 Mg²⁺, 특정 pH 등)에서만 형성되며, 원시 지구 환경에서의 지속 가능성에 대한 실험적 증거가 부족하다. 또한, ‘triplex2duplex picture’가 코돈 길이와 직접 연결된 메커니즘을 제시하지 못하고, 단순히 ‘공통 약수 3’이라는 수학적 우연을 인용하는 수준에 머문다.
생물다양성 공간을 이용해 3계통 트리를 재구성한 결과는 기존 3계통 가설을 지지하지만, 동일한 데이터(코돈 분포)로도 eocyte 트리를 만들 수 있는지에 대한 부정확한 대조 실험이 결여돼 있다. 즉, ‘데이터 선택 편향’ 가능성이 존재한다.
결론적으로, 이 논문은 코돈 분포를 새로운 차원에서 바라보는 시도와 전생물학적 가설을 연결하려는 창의적인 시도를 보여준다. 그러나 통계적 절차의 불명확성, 가설 검증 부족, 그리고 삼중 나선 가설에 대한 실험적 뒷받침이 미비한 점은 향후 연구에서 보완되어야 할 주요 과제이다.
댓글 및 학술 토론
Loading comments...
의견 남기기