자기참조 DNA와 단백질: 물리·기하학적 고찰
초록
**
이 논문은 DNA와 단백질 사이의 자기참조 루프를 물리·기하학적 관점에서 탐구한다. 유전자가 단백질로 전사·번역되고, 그 단백질이 다시 동일 유전자의 전사 조절에 관여하는 과정을 ‘DNA→단백질→DNA’ 매핑으로 정의하고, 이를 단순화한 토이 모델을 통해 구조적 제약과 에너지 흐름을 분석한다. 저자는 이러한 루프가 생명 시스템의 다중 스케일 피드백 메커니즘의 핵심임을 강조한다.
**
상세 분석
**
논문은 먼저 생명 현상이 여러 공간·시간·에너지 스케일을 아우르는 피드백 네트워크로 구성된다는 일반적 프레임워크를 제시한다. 그 중에서도 가장 근본적인 루프는 DNA와 단백질 사이의 상호작용이다. DNA 서열이 전사·번역 과정을 거쳐 폴리펩타이드 사슬, 즉 단백질이 되고, 이 단백질이 다시 전사인자 혹은 리프레서로 작용해 원래의 DNA 서열 근처에 결합함으로써 자신의 발현을 조절한다는 ‘자기참조’ 현상은 정보 흐름이 두 물질 형태 사이를 왕복한다는 점에서 독특하다.
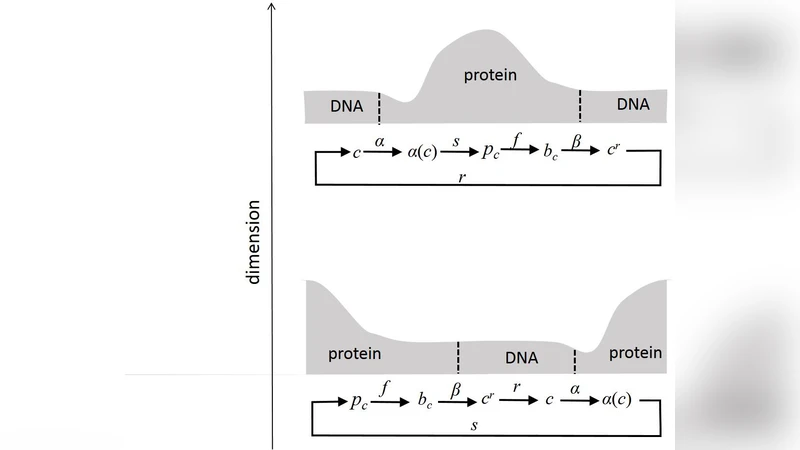
저자는 이 과정을 ‘매핑’이라고 부르며, 매핑의 물리적·기하학적 특성을 두 단계로 나눈다. 첫 번째 매핑(DNA→단백질)은 1차 서열 정보가 3차원 폴리펩타이드 구조로 변환되는 과정으로, 여기서는 아미노산의 물리적 성질(소수성·친수성, 전하 등)과 폴딩 에너지 지형이 핵심 변수다. 두 번째 매핑(단백질→DNA)은 단백질 표면의 결합 부위가 DNA의 특정 서열(프로모터, 오페레이터 등)과 상호작용하는 기하학적 적합성, 즉 ‘키‑와‑록’ 모델에 해당한다. 이때 전자기적 인력, 수소결합, 그리고 DNA의 굽힘 강성 등이 결합 친화도를 결정한다.
논문은 이러한 두 매핑을 연결하는 ‘루프 비용(loop cost)’ 개념을 도입한다. 루프를 완성하기 위해서는 (1) 전사·번역 과정에서 에너지 소비(ATP, GTP), (2) 폴딩 과정에서 자유 에너지 최소화, (3) DNA 결합 시 발생하는 엔트로피 손실 등이 모두 고려되어야 한다. 저자는 특히 기하학적 제약—예를 들어, 단백질이 DNA에 접근하기 위해서는 특정 회전·전이 자유도가 필요하고, DNA 자체가 나선 구조를 유지하기 위해서는 토션 스트레스가 제한된다—가 루프의 안정성과 동역학에 결정적 영향을 미친다고 주장한다.
이를 설명하기 위해 제시된 토이 모델은 1차원 이진 문자열(‘DNA’)과 2차원 격자상의 점(‘단백질’) 사이의 매핑 규칙을 정의한다. 문자열의 각 비트는 특정 점의 존재·부재를 결정하고, 점들은 인접한 비트와 상호작용해 에너지 함수를 최소화한다. 모델은 간단하지만, 실제 생물학적 시스템에서 관찰되는 ‘피드백 억제’, ‘양성 자동조절’, ‘다중 결합 부위’ 등을 재현한다. 시뮬레이션 결과는 매핑 효율이 기하학적 정렬도와 에너지 장벽에 민감함을 보여주며, 이는 실제 DNA‑단백질 상호작용에서도 동일한 원리가 작용한다는 강력한 암시를 제공한다.
결론적으로, 논문은 DNA와 단백질 사이의 자기참조 루프가 단순한 화학 반응을 넘어 물리적·기하학적 제약에 의해 형성된 고차원 피드백 시스템임을 강조한다. 이러한 관점은 합성 생물학에서 인공 회로를 설계하거나, 질병에서 변이된 결합 부위가 피드백 루프를 어떻게 파괴하는지를 이해하는 데 유용한 이론적 토대를 제공한다.
**
댓글 및 학술 토론
Loading comments...
의견 남기기