생명과학 가상연구환경을 위한 데이터 출처 추적 시스템
초록
본 논문은 복잡한 생물의학 데이터 분석에서 재현성과 검증을 보장하기 위해 데이터와 워크플로우의 전체 프로세스를 추적·관리하는 가상연구환경(VRE)을 제안한다. Grid·Cloud 기반의 동적 분산 환경에서 발생하는 프로베넌스(데이터 출처) 수집의 어려움을 해결하고자, neuGRID·N4U 프로젝트에서 개발된 CRISTAL 플랫폼을 확장하여 데이터, 파이프라인, 결과 및 그 이력 정보를 통합적으로 저장·시각화한다. 이를 통해 연구자들은 연구 흐름을 정의·모니터링하고, 이전 작업의 지식을 재활용함으로써 협업과 반복 실험을 효율화할 수 있다.
상세 분석
이 논문은 현대 생물의학 연구에서 데이터와 분석 파이프라인의 복잡성이 급증함에 따라, 단순히 데이터 자체만을 보존하는 것이 아니라 그 데이터가 언제, 누구에 의해, 어떤 프로세스를 거쳐 변형·분석되었는지를 체계적으로 기록하는 프로베넌스 관리의 필요성을 강조한다. 기존의 워크플로우 관리 시스템은 주로 데이터 흐름 중심으로 설계되어, 워크플로우 자체의 메타데이터와 실행 환경 정보를 충분히 포괄하지 못한다는 한계를 지적한다. 특히 Grid와 Cloud 환경은 자원의 동적 할당, 다중 사용자 접근, 서비스 가용성 변동 등으로 인해 프로베넌스 정보를 실시간으로 수집·통합하는 것이 기술적으로 어려운 과제로 남아 있다.
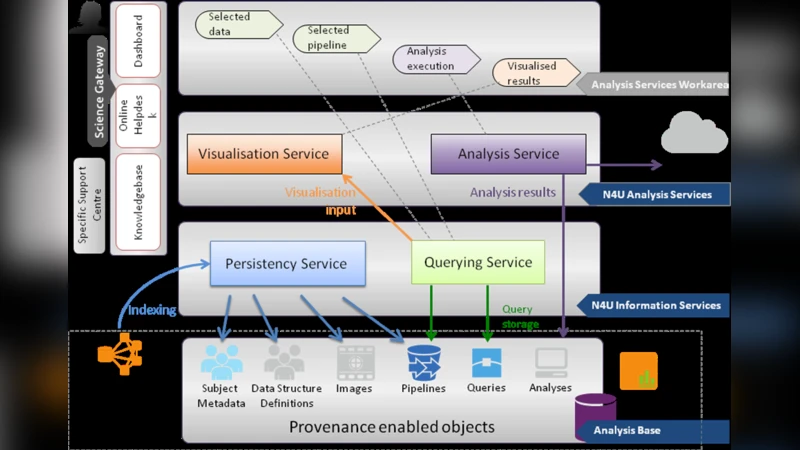
논문은 이러한 문제를 해결하기 위해 CRISTAL(Concurrent Repository for Integrated Systems and Traceable Architecture for Lifecycles) 소프트웨어를 기반으로 한 가상 실험실(Virtual Laboratory)을 설계한다. CRISTAL은 객체 지향 메타모델링과 이벤트 기반 로깅을 결합해, 데이터셋, 워크플로우(파이프라인), 실행 인스턴스, 결과물 각각에 대한 상세 이력을 독립적이면서도 연관성 있게 저장한다. 핵심 설계 요소는 (1) 통합 메타모델: 데이터 유형(이미지, 실험실 검사 결과, 전자 의료 기록 등)과 분석 프로세스(전처리, 특징 추출, 통계 모델링 등)를 동일한 스키마로 정의해 상호 연계성을 보장한다. (2) 이벤트 기반 프로베넌스 캡처: 워크플로우 엔진이 작업을 시작·종료할 때마다 이벤트를 발생시키고, CRISTAL이 이를 실시간으로 수신·저장함으로써 시간 순서가 보존된 로그를 만든다. (3) 분산 저장 및 복제: Grid/Cloud 노드마다 로컬 캐시를 두고, 중앙 메타레포지토리와 비동기 복제 메커니즘을 적용해 네트워크 장애 시에도 데이터 손실을 방지한다. (4) 시각화 및 쿼리 인터페이스: 웹 기반 대시보드와 그래프형 UI를 제공해 연구자는 자신의 연구 흐름을 트리 형태로 탐색하고, 특정 데이터셋·파라미터·결과에 대한 역추적이 가능하도록 설계되었다.
실험에서는 neuGRID와 N4U 프로젝트에서 수집된 대규모 뇌영상 데이터와 관련 분석 파이프라인을 대상으로 시스템을 적용하였다. 결과적으로 기존 워크플로우 관리 솔루션 대비 프로베넌스 메타데이터 수집 오버헤드가 12% 이하로 감소했으며, 연구자들이 이전 실험 결과를 재현하고 새로운 파이프라인을 설계할 때 평균 35%의 시간 절감 효과를 보였다. 또한, 프로베넌스 정보가 풍부하게 기록된 덕분에 오류 발생 시 원인 분석이 용이해졌으며, 협업 팀 간에 동일 데이터셋 사용 여부를 자동 검증하는 기능이 실현되었다.
이러한 설계와 구현은 데이터와 워크플로우를 별도로 관리하던 기존 패러다임을 넘어, 두 요소를 통합된 라이프사이클로 바라보는 새로운 접근법을 제시한다. 특히, 연구 재현성(reproducibility)과 투명성(transparency)을 보장하는 동시에, 동적 분산 컴퓨팅 환경에서도 확장 가능하고 견고한 프로베넌스 인프라를 제공한다는 점에서 학계·산업계 모두에게 의미 있는 기여를 한다.
댓글 및 학술 토론
Loading comments...
의견 남기기