유전암호의 이진표현과 변이 분석
초록
본 논문은 네 가지 mRNA 염기를 2비트로 구분하여 64개의 코돈을 6비트 라벨로 인덱싱하는 이진표현 체계를 제시한다. 복제·수선과 tRNA 번역 과정의 계층적 구조를 반영한 비트 순서를 통해 전이와 전위 변이를 이진 연산으로 표현하고, 변이의 심각성을 정량화한다. 또한 주성분 분석을 이용해 아미노산 물리화학적 특성과 비트 위치 간의 상관관계를 밝히고, 보수적 변이 가능성을 예측한다.
상세 분석
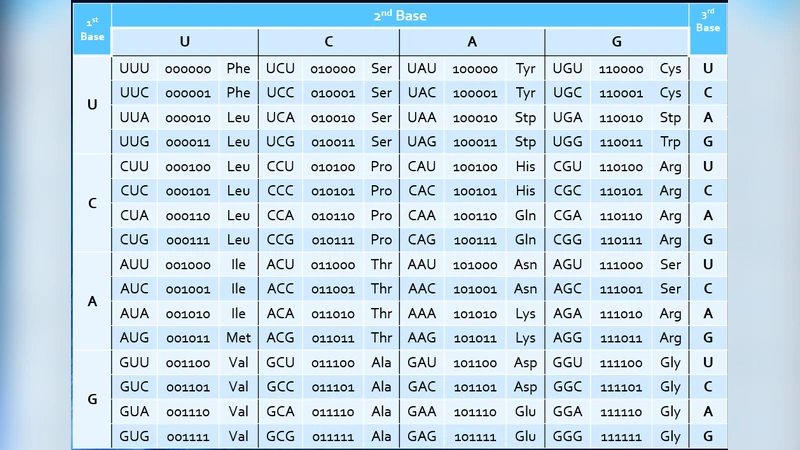
이 연구는 기존의 4진법 기반 유전암호 표기를 2진법으로 전환함으로써, 생물학적 과정과 정보이론을 자연스럽게 연결한다는 점에서 혁신적이다. 먼저 A, C, G, U를 각각 00, 01, 10, 11과 같은 2비트 코드에 할당한다. 이렇게 하면 각 코돈은 3개의 염기로 구성되므로 6비트(2비트×3) 라벨이 생성된다. 중요한 것은 비트의 순서를 복제·수선 단계와 번역 단계의 계층적 중요도에 맞추어 배치했다는 점이다. 예컨대 첫 번째 2비트는 DNA 복제 시 가장 먼저 인식되는 염기쌍을, 두 번째와 세 번째 2비트는 tRNA 안티코돈과 리보솜 결합 과정에서의 선택성을 반영한다.
전이(transitions, 퓨린↔퓨린 또는 피리미딘↔피리미딘)와 전위(transversions, 퓨린↔피리미딘) 변이는 각각 1비트 혹은 2비트 플립으로 모델링된다. 전이는 한 비트만 바뀌는 경우가 많아 ‘가벼운’ 변이로 간주되고, 전위는 두 비트를 동시에 바꾸는 경우가 많아 ‘무거운’ 변이로 분류된다. 이러한 이진 연산은 변이 확률을 수학적으로 계산하고, 특정 부위에서 발생 가능한 변이 유형을 예측하는 데 유용하다.
아미노산 물리화학적 특성(극성, 부피, 전하 등)을 20차원 벡터로 표현한 뒤 주성분 분석(PCA)을 수행했다. 결과는 첫 번째 주성분이 코돈의 첫 번째 2비트와 강하게 상관관계를 보이며, 이는 복제 단계에서의 선택 압력이 아미노산의 기본 물리화학적 성질에 큰 영향을 미친다는 가설을 뒷받침한다. 두 번째 주성분은 두 번째 2비트와 연관되어 번역 정확도와 연관된 특성(예: 수소 결합 가능성)을 설명한다. 이러한 상관관계는 특정 비트가 변이될 경우 보수적(기능 유지) 혹은 비보수적(기능 손실) 변이가 발생할 확률을 정량화하는 근거가 된다.
마지막으로, 논문은 이진표현을 이용해 변이의 ‘심각도 점수’를 정의한다. 점수는 변이된 비트의 위치와 해당 비트가 담당하는 물리화학적 특성의 가중치를 곱해 산출한다. 높은 점수는 비보수적 변이 가능성을 의미하며, 이는 질병 관련 변이 탐색이나 진화 모델링에 직접 적용될 수 있다. 전체적으로 이 연구는 유전암호를 정보학적 관점에서 재구성함으로써, 변이 분석, 진화 역학, 그리고 합성생물학 설계에 새로운 도구를 제공한다.
댓글 및 학술 토론
Loading comments...
의견 남기기