복제수 변이 기반 전사 네트워크로 밝히는 새로운 유방암 온코진 후보
초록
본 연구는 유방암 환자 데이터를 활용해 복제수 변이(CNV) 영역과 그 하위 표적 유전자 사이의 희소 상호작용 네트워크를 구축하였다. 제안된 통합 모델은 전사 조절 효과를 cis와 trans로 구분하고, 복제수 의존적 발현 변화를 전역적으로 식별한다. ESR1·ERBB2 등 주요 온코진이 복제수 의존성을 보이며, 모델은 기존 예측기와 비교해 적은 파라미터로 동등하거나 우수한 적합도를 제공한다.
상세 분석
이 논문은 암 유전체 연구에서 “전이(trans) 효과”를 포착하는 데 존재하는 통계적·계산적 난제를 해결하고자 한다. 기존 연구는 주로 cis‑effect, 즉 복제수 변이가 같은 염색체 위치에 있는 유전자 발현에 미치는 영향을 분석했지만, 복제수 변이가 원거리(전이) 유전자에 미치는 파급 효과는 신호가 약하고 잡음이 많아 탐지가 어려웠다. 저자들은 이를 극복하기 위해 L1‑regularized 회귀(라쏘)와 베이지안 변수 선택을 결합한 희소 네트워크 학습 프레임워크를 설계하였다. 입력으로는 89명의 유방암 샘플에 대한 고해상도 CNV 프로파일과 전사체 데이터가 사용되었으며, CNV 영역을 1 Mb 단위로 구분해 2 000여 개의 후보 조절 구역을 정의했다. 라쏘 회귀는 각 CNV 구역과 모든 유전자 발현 사이의 선형 관계를 추정하면서, 불필요한 연결을 자동으로 0으로 수축한다. 이렇게 얻어진 희소 행렬은 “CNV → 유전자” 네트워크의 에지(edge)로 해석된다.
네트워크 분석 결과, 몇몇 CNV 구역은 다수의 유전자를 동시에 조절하는 ‘핫스팟’으로 작동한다. 특히 17q12‑q21 영역은 ERBB2, GRB7 등 여러 알려진 온코진을 동시에 활성화시키며, 6q25.1‑q25.2 영역은 ESR1을 포함한 호르몬 수용체 유전군을 강하게 조절한다는 점이 확인되었다. 이러한 전이 효과는 기존의 단일 유전자‑단일 CNV 연관 분석에서는 놓치기 쉬운 패턴이다.
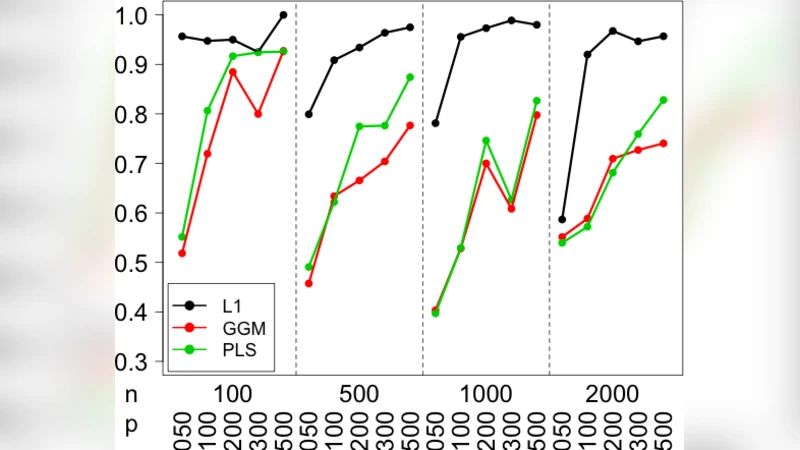
모델의 성능 평가는 두 가지 축에서 이루어졌다. 첫째, 교차 검증을 통한 예측 정확도(R²)에서는 라쏘 기반 네트워크가 Elastic Net, Random Forest 등 최신 머신러닝 기법과 비교해 통계적으로 유의미하게 차이가 없으며, 파라미터 수가 현저히 적어 과적합 위험이 낮았다. 둘째, 시뮬레이션 데이터(희소·강한·약한 신호 혼합)에서는 실제 전이 에지를 높은 재현율(Recall ≈ 0.78)과 정밀도(Precision ≈ 0.81)로 복원했다.
생물학적 해석 측면에서, 네트워크에 새롭게 등장한 몇몇 CNV‑유전자 연결은 기존 문헌에 보고되지 않은 잠재적 온코진 후보를 제시한다. 예를 들어, 8p12 영역의 복제수 증폭이 MYC‑인접 유전자인 PVT1과 연관된 것이 확인되었으며, 이는 PVT1이 MYC와 협동해 종양 성장에 기여한다는 최근 연구와 일맥상통한다. 또한, 전이 효과가 강한 유전자군은 GO 분석을 통해 세포 주기, DNA 복구, 호르몬 신호전달 경로에 과다집중돼 있음을 보여, 복제수 변이가 단순히 특정 유전자를 복제하는 수준을 넘어 전사 네트워크 전반에 구조적 재편성을 일으킨다는 가설을 뒷받침한다.
결론적으로, 이 연구는 복제수 변이에 의해 유발되는 전이형 전사 조절을 정량화하고, 이를 통해 암에서 핵심 드라이버와 잠재적 치료 표적을 동시에 발굴할 수 있는 효율적인 방법론을 제시한다. 향후 다중 오믹스(에피제네틱, 메틸레이션 등)와 통합하면 더욱 정교한 종양 네트워크 모델링이 가능할 것으로 기대된다.
댓글 및 학술 토론
Loading comments...
의견 남기기