다중안정 진동 패턴의 확률적 전이와 미세구조 감지
초록
본 논문은 E. coli의 Min 시스템이 3차원 미세공간에서 보여주는 다중안정 진동 패턴을 입자 기반 브라운 운동 시뮬레이션으로 재현하고, 각 패턴의 발생 빈도와 전이 속도를 정량적으로 분석한다. 실험과 일치하는 결과를 얻으며, 새로운 패턴과 부피‑표면 비와 결합 단백질 농도 사이의 선형 관계를 제시한다.
상세 분석
이 연구는 기존의 결정론적 PDE 모델이 포착하지 못한 확률적 현상을 입자 기반(Particle‑based) 브라운 다이내믹스 시뮬레이션으로 해결한다. 최소 모델(minimal model)을 기반으로 MinD와 MinE의 결합·해리, ATP/ADP 전환, 그리고 막‑내 확산을 1차·2차 반응으로 구현했으며, 세 가지 파라미터 세트(A, B, C)를 비교한다. 시뮬레이션은 Δt = 10⁻⁴ s의 고정 타임스텝으로 진행되며, 자유 입자는 3차원 확산, 막 결합 입자는 2차원 확산을 각각 수행한다. 반응 확률은 포아송 과정(p = 1−e^{−κΔt})과 Smoldyn‑기반의 Smoluchowski 충돌 모델을 사용해 정확히 계산한다.
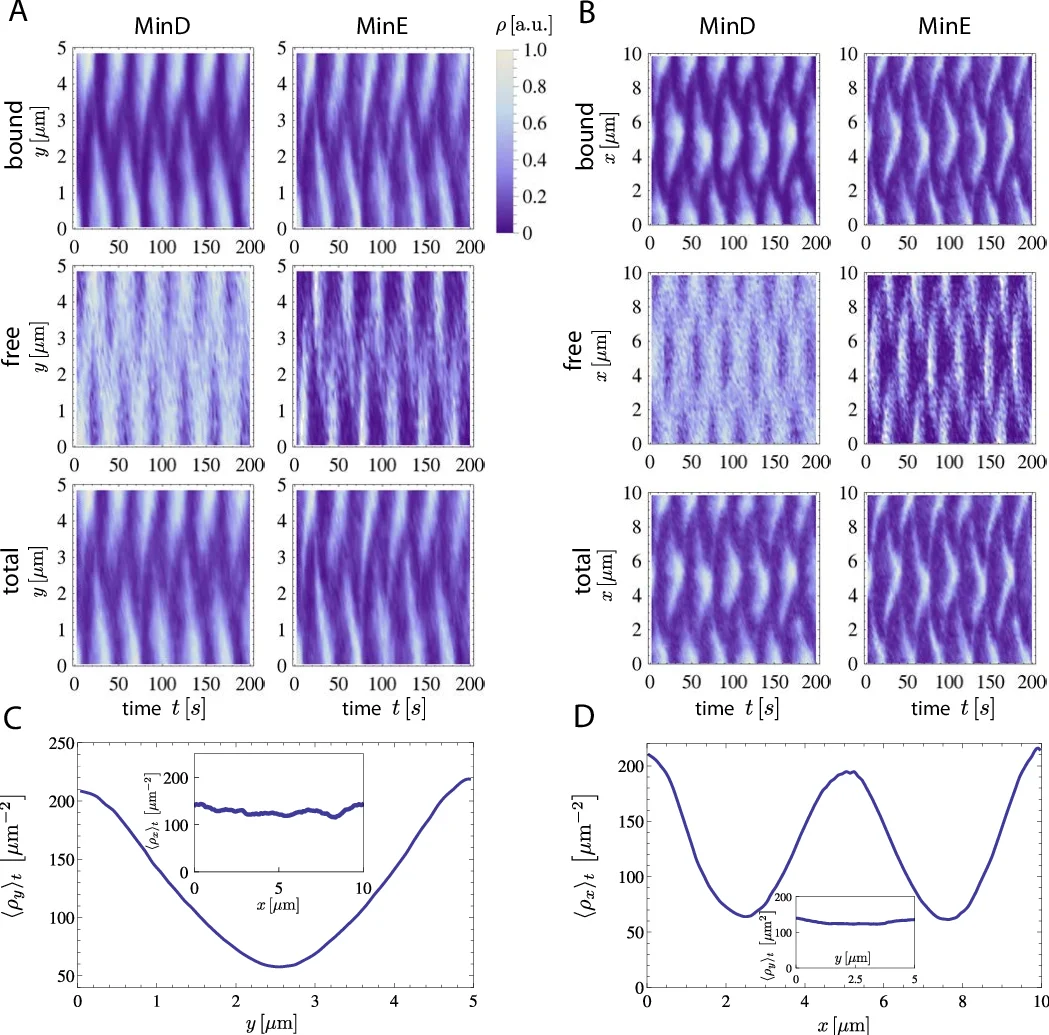
주요 결과는 다음과 같다. 첫째, 동일한 기하학적 구획(Geometry A, B, C)에서도 pole‑to‑pole, transverse pole‑to‑pole, strip‑like 등 최소 3가지 이상의 안정적인 진동 모드가 존재한다. 둘째, 각 모드의 상대 빈도는 부피‑표면 비(V/S)와 막 면적 커버리지에 강하게 의존한다. 특히 Geometry C(전면 막 코팅)에서는 새로운 “edge‑localized” 패턴이 관찰되었으며, 이는 기존 실험에서는 보고되지 않은 형태이다. 셋째, Fourier 분석과 자동 패턴 인식 알고리즘을 결합해 수천 초에 걸친 시뮬레이션 데이터에서 전이 이벤트를 자동 검출하였다. 전이 평균 시간은 수십 초에서 수백 초 사이로, 실험에서 보고된 전이 확률과 정량적으로 일치한다.
또한, 막에 결합된 Min 단백질의 평균 농도 ρ_bound은 V/S 비와 선형 관계(ρ_bound ≈ α·V/S + β)를 보이며, 이는 세포가 자신의 부피와 형태를 단백질 농도 변화를 통해 “감지”할 수 있는 메커니즘을 시사한다. 파라미터 세트 B와 C를 적용했을 때도 동일한 선형성은 유지되었지만, 전이 속도와 패턴 분포는 약간씩 차이를 보였다(예: 세트 C에서는 전이 빈도가 감소).
이와 같이, 입자 기반 시뮬레이션은 미세구조에 대한 Min 시스템의 감지 능력을 정량화하고, 다중안정성(multistability)과 확률적 전이가 실제 세포 내에서 어떻게 작동하는지를 명확히 보여준다. 연구는 향후 인공 세포 설계, 미세유체 장치에서의 패턴 제어, 그리고 다른 반응‑확산 시스템의 stochastic bifurcation 연구에 중요한 기반을 제공한다.
댓글 및 학술 토론
Loading comments...
의견 남기기