핵 내부 점성 탄성 특성 크기 의존 단백질 이동성으로 본 크로마틴 네트워크
초록
이 연구는 살아있는 인간 세포 핵 안에서 다양한 크기의 관성형 녹색 형광 단백질 트레이서를 이용해 이동성을 측정하고, 이를 통해 핵 내부가 작은·큰 스케일에서는 점성 유체와 유사하지만 중간 스케일에서는 크기에 따라 변하는 점탄성 거동을 보인다는 것을 밝혀냈다. 시뮬레이션 결과는 크로마틴이 고정된 프랙탈 차원을 가진 자기유사 구조보다 무작위 장애물 네트워크를 형성한다는 가설을 지지한다. 또한 분자들이 이전 위치를 기억하는 시간(메모리 커널)을 크기별로 계산해, 핵 환경이 DNA 표적 탐색 과정에 미치는 영향을 정량화하였다.
상세 분석
본 논문은 핵 내 물리적 매질을 정량적으로 규정하기 위해 2 nm에서 10 nm 정도의 반경을 갖는 관성형 GFP 변종 5종을 제작하고, 살아있는 HeLa 세포에 발현시킨 뒤 단일 입자 추적(SPT)과 플루오레선스 회복(FRAP) 기법을 병행하였다. 각 트레이서의 평균 제곱 변위(MSD)를 시간 지연 τ에 대해 로그‑로그 플롯으로 나타내면, 짧은 τ(≤ 10 ms) 구간에서는 MSD∝τ^1에 가까워 순수 점성 흐름을 의미하고, 긴 τ(≥ 1 s) 구간에서도 동일한 선형 관계가 유지된다. 그러나 중간 τ 구간(10 ms ~ 1 s)에서는 지수 α가 0.7~0.9 사이로 감소하여, 점탄성 거동을 나타낸다. 이 α값은 트레이서 크기가 클수록 더 낮아지는 경향을 보였으며, 이는 큰 분자가 크로마틴 네트워크의 격자 구조를 더 강하게 ‘느끼게’ 된다는 물리적 해석을 가능하게 한다.
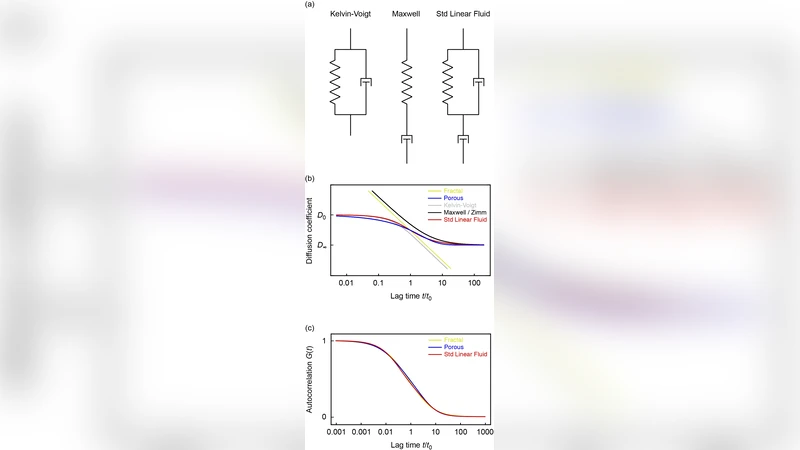
점탄성 특성을 정량화하기 위해 복소 점탄성 모듈러스 G*(ω)=G′(ω)+iG″(ω)를 구했으며, 저주파(ω < 10 rad·s⁻¹)에서는 저장 모듈러스 G′가 손실 모듈러스 G″보다 현저히 작아 점성 주도임을, 중간 주파수(10 rad·s⁻¹ ~ 100 rad·s⁻¹)에서는 G′와 G″가 교차하며 최대 탄성 응답을 보임을 확인했다. 고주파(ω > 100 rad·s⁻¹)에서는 다시 G″가 우세해 순수 점성으로 회귀한다. 이러한 스케일 의존적 전이 현상은 폴리머 물리학에서 보고된 ‘세미-덴드리티드’ 네트워크와 유사하며, 크로마틴이 단순한 프랙탈 구조가 아니라 무작위 장애물(랜덤 오블리크) 형태의 폴리머 매시를 형성한다는 가설을 뒷받침한다.
시뮬레이션 측면에서는 라우스-데이비드스(Langevin) 동역학을 이용해 3차원 격자에 무작위 길이와 방향을 갖는 체인들을 배치하고, 동일한 크기의 가상 입자를 확산시켰다. 실험 데이터와 시뮬레이션 결과의 MSD와 G* 곡선이 정량적으로 일치했으며, 특히 중간 스케일에서 관찰된 α 감소와 G′·G″ 교차점이 재현되었다. 이는 크로마틴이 ‘랜덤 오블리크’ 모델을 따를 때, 입자 크기에 따라 유효 메쉬 사이즈가 변한다는 점을 시뮬레이션적으로 검증한 것이다.
또한 저자들은 메모리 커널 K(t)=⟨Δr(0)·Δr(t)⟩/⟨Δr(0)^2⟩를 계산해, 입자가 이전 위치를 기억하는 지속 시간을 τ_mem으로 정의하였다. 작은 트레이서(GFP‑WT)의 τ_mem은 ~20 ms 수준에 불과했지만, 큰 트레이서(10 nm 반경)의 경우 200 ms 이상으로 증가했다. 이러한 크기 의존적 메모리 효과는 전사인자나 복제 기구와 같은 대형 복합체가 핵 내 목표 DNA 서열을 탐색할 때, 단순 확산보다 ‘구속된’ 확산(컨파인먼트) 모델을 적용해야 함을 시사한다.
결론적으로, 이 연구는 핵 내부가 다중 스케일에서 복합적인 점탄성 매질이며, 크로마틴이 무작위 장애물 네트워크를 형성한다는 물리적 근거를 제공한다. 이는 기존에 프랙탈 차원을 고정하고 스케일 프리(self‑similar)라고 가정했던 모델을 재검토하게 만들며, 핵 내 효소 반응 속도와 전사인자 탐색 효율성을 예측하는 새로운 이론적 토대를 마련한다.