제브라피시 유전자 공동발현 네트워크의 스펙트럼 분석
초록
본 연구는 제브라피시 유전자 발현 데이터를 복합 네트워크와 랜덤 매트릭스 이론(RMT)으로 분석한다. 인접 행렬의 고유값 간격 분포가 Gaussian Orthogonal Ensemble(GOE)와 일치함을 확인하고, 고유벡터의 국소화 정도에 따라 두 개의 스펙트럼 영역을 구분한다. 국소화된 고유벡터는 세 그룹으로 나뉘며, 각 그룹의 상위 기여 유전자는 구조적으로 뚜렷한 특징을 보이고, 생물학적 기능에서도 공통성을 가진다.
상세 분석
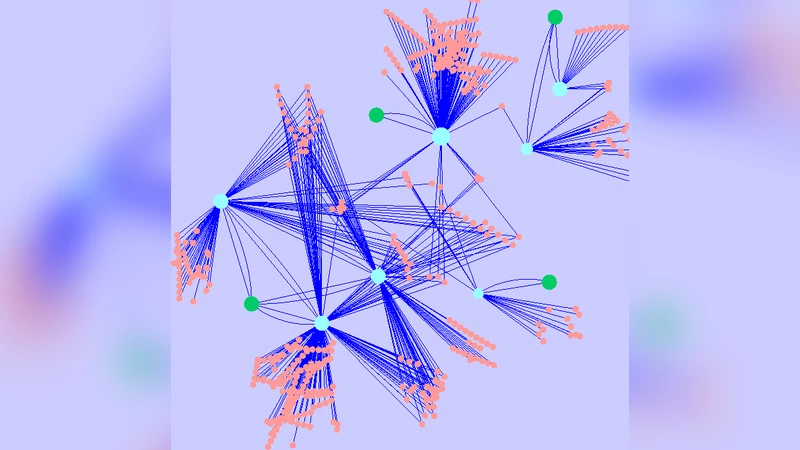
본 논문은 제브라피시(Zebrafish) 조직에서 수집된 대규모 유전자 발현 데이터를 기반으로, 유전자 간 상관관계를 네트워크 형태로 변환한 뒤, 해당 네트워크의 인접 행렬 스펙트럼을 랜덤 매트릭스 이론(RMT) 프레임워크에 적용하였다. 먼저 Pearson 상관계수를 이용해 유전자 쌍 간의 가중 연결을 정의하고, 임계값을 설정해 희소화된 무향 가중 네트워크를 구축하였다. 이 네트워크의 대칭 인접 행렬은 실수 원소를 가지며, 고유값을 정렬한 후 인접 고유값 사이의 간격을 정규화하여 nearest‑neighbor spacing distribution(NNSD)을 구하였다. 결과는 Gaussian Orthogonal Ensemble(GOE)의 Wigner‑Dyson 분포와 높은 적합도를 보였으며, 이는 네트워크가 무작위성 성분을 크게 포함하고 있음을 의미한다.
다음 단계에서는 고유벡터의 국소화 정도를 측정하기 위해 inverse participation ratio(IPR)를 계산하였다. IPR 값이 평균값에 근접한 고유벡터는 RMT가 예측하는 delocalized 상태에 해당하고, 반대로 IPR이 크게 상승한 고유벡터는 국소화된 특성을 보인다. 저자들은 이러한 국소화된 고유벡터들을 고유값의 위치에 따라 세 그룹(저에너지, 중간, 고에너지)으로 분류하였다. 각 그룹에 속한 고유벡터의 상위 기여 유전자(Top contributing nodes)를 추출한 뒤, 이들 간의 구조적 연관성을 평가하기 위해 overlap measure를 도입하였다. overlap measure는 두 유전자 집합 간의 공통 연결 비율을 정량화하며, 결과는 서로 다른 그룹의 상위 유전자 집합이 네트워크 내에서 거의 겹치지 않고, 각각 독립적인 고밀도 서브그래프를 형성한다는 것을 보여준다.
생물학적 해석 단계에서는 이러한 서브그래프에 포함된 유전자들의 기능적 주석을 Gene Ontology 및 KEGG 경로 분석을 통해 검증하였다. 동일한 고유벡터에 속한 유전자들은 대사, 세포 골격, 신호 전달 등 특정 생물학적 프로세스와 강하게 연관되어 있었으며, 이는 고유벡터 국소화가 시스템 고유의 기능적 모듈을 반영한다는 가설을 뒷받침한다. 또한, 저에너지 영역의 국소화된 고유벡터는 네트워크 중심성(centrality)이 높은 핵심 유전자를 포함하는 반면, 고에너지 영역은 주변부이면서도 특수한 환경 스트레스 반응에 관여하는 유전자를 포함한다는 차이를 보였다.
전반적으로 이 연구는 복합 네트워크와 RMT를 결합함으로써, 무작위성에 의해 지배되는 전체 스펙트럼과 시스템 고유의 구조적·생물학적 정보를 담고 있는 국소화된 스펙트럼을 명확히 구분한다. 특히, 고유벡터 국소화와 overlap measure를 활용한 서브그래프 탐지는 기존의 단순 연결성 분석을 넘어, 기능적 모듈을 정량적으로 식별할 수 있는 새로운 방법론을 제시한다.
댓글 및 학술 토론
Loading comments...
의견 남기기