DNA에 단백질 결합을 위한 이산 지속 사슬 모델
이 논문은 DNA의 각 염기 위치에 단백질 결합 여부를 나타내는 이진 변수 σᵢ를 도입한 이산 지속 사슬(persistent chain) 모델을 제시한다. σᵢ=1이면 단백질이 결합하고, 결합 시 추가 에너지 ε가 소모된다. 저힘 영역에서는 힘‑연장 곡선과 결합 단백질 비율에 대한 해석적 식을 유도하고, 고힘 영역에서는 수치적 해법을 통해 전체 힘‑연장 특
초록
이 논문은 DNA의 각 염기 위치에 단백질 결합 여부를 나타내는 이진 변수 σᵢ를 도입한 이산 지속 사슬(persistent chain) 모델을 제시한다. σᵢ=1이면 단백질이 결합하고, 결합 시 추가 에너지 ε가 소모된다. 저힘 영역에서는 힘‑연장 곡선과 결합 단백질 비율에 대한 해석적 식을 유도하고, 고힘 영역에서는 수치적 해법을 통해 전체 힘‑연장 특성과 결합 비율을 계산한다. 모델은 비특이적 결합 상황에서 실험 데이터로부터 결합된 단백질 수를 추정하는 도구로 활용될 수 있다.
상세 요약
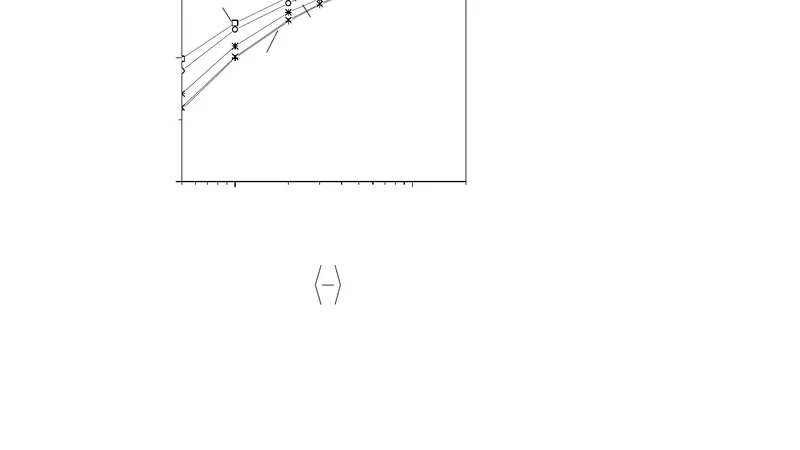
본 연구는 DNA의 기계적 거동을 설명하는 전통적인 웰링거-프리드리히(WLC) 모델에 단백질 결합을 위한 이산 자유도를 추가함으로써, 단백질‑DNA 상호작용을 물리적으로 정량화한다. 각 염기 위치 i에 대해 σᵢ∈{0,1}이라는 이진 변수와 결합 에너지 ε를 도입함으로써, 단백질이 결합된 구간은 굽힘 강성(또는 지속 길이)이 변하는 효과를 포함한다. 저힘 한계에서는 전이 행렬 방법과 퍼트루베니안 전개를 이용해 자유에너지의 1차 및 2차 항을 계산하고, 이에 따라 평균 연장 ⟨z⟩와 결합 비율 ⟨σ⟩에 대한 폐쇄형 식을 얻는다. 이 식들은 힘이 작용할 때 DNA가 더 긴 지속 길이를 보이는 경우와, 결합 단백질이 굽힘 저항을 증가시켜 연장이 억제되는 경우를 모두 포괄한다.
고힘 영역에서는 전이 행렬의 최대 고유값을 수치적으로 구해 자유에너지 밀도를 평가한다. 이때 σᵢ의 통계적 평균은 ε와 외부 힘 f에 대한 볼츠만 인자 exp
📜 논문 원문 (영문)
🚀 1TB 저장소에서 고화질 레이아웃을 불러오는 중입니다...