폴리머가 이끄는 icosahedral 바이러스 캡시드 자가조립 메커니즘
초록
이 연구는 코스모스-그레인드 모델과 브라운 운동 시뮬레이션을 이용해, 유연한 폴리머(예: ssRNA)가 icosahedral 캡시드 내부에 포장되는 과정을 정량적으로 분석한다. 폴리머 길이, 단백질 농도, 용액 이온 강도 등 실험 변수에 따라 서로 다른 조립 메커니즘(핵형 형성, 협동적 폴리머‑단백질 이동, 포장 효율)이 나타나며, 이를 기반으로 조립 성공률을 예측하는 상전이 다이어그램을 제시한다. 결과는 바이러스 복제 억제 전략과 나노소재 설계에 활용될 수 있다.
상세 분석
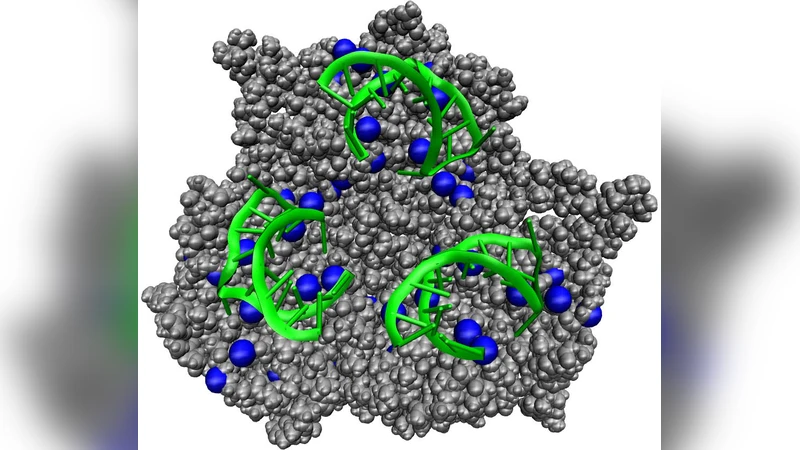
본 논문은 icosahedral 형태를 갖는 바이러스 캡시드가 유연한 폴리머를 둘러싸는 과정을, 입자 수준에서 직접 관찰하기 어려운 점을 보완하고자 코스모스-그레인드 모델을 구축하고 브라운 운동(Brownian dynamics) 시뮬레이션을 수행하였다. 모델은 캡시드 단백질 서브유닛을 5개의 결합 부위와 구형 핵심 입자로 단순화하고, 폴리머는 연속적인 비스코스 사슬로 표현하였다. 시뮬레이션 파라미터는 실험적으로 조절 가능한 세 가지 주요 변수, 즉 폴리머 길이(L), 캡시드 단백질 농도(C), 그리고 용액 이온 강도(σ)로 설정하였다.
시뮬레이션 결과는 네 가지 주요 메커니즘을 도출한다. 첫째, ‘핵형 형성’(nucleation) 단계에서 폴리머가 단백질 서브유닛을 물리적으로 끌어당겨 초기 핵형을 형성한다. 이때 폴리머의 굴곡성(flexibility)이 핵형의 안정성에 직접적인 영향을 미치며, 너무 짧은 폴리머는 핵형을 충분히 안정화시키지 못해 조립이 중단된다. 둘째, ‘협동적 폴리머‑단백질 이동(cooperative polymer‑protein motion)’으로, 이미 결합된 서브유닛이 폴리머를 따라 미끄러지듯 이동하면서 주변 단백질을 추가로 끌어들인다. 이 과정은 전통적인 ‘핵형‑성장’ 모델과 달리 폴리머 자체가 동적인 템플릿 역할을 수행한다는 점에서 혁신적이다. 셋째, ‘곡률 유도( curvature induction)’ 메커니즘에서는 폴리머가 내부 압력을 증가시켜 캡시드 표면에 국소적인 곡률을 유도하고, 이는 icosahedral 대칭을 유지하면서도 완전한 포장을 가능하게 한다. 넷째, ‘포장 효율(encapsulation efficiency)’은 위 세 메커니즘의 상호작용에 따라 비선형적으로 변한다. 특히 단백질 농도가 일정 수준 이상일 때, 과잉 단백질이 비특이적 결합을 일으켜 비정상적인 다중 캡시드 형성을 초래한다.
이러한 메커니즘을 바탕으로 저자들은 실험 파라미터 공간을 3차원 상전이 다이어그램으로 시각화하였다. 다이어그램은 ‘성공적 포장’, ‘불완전 포장’, ‘오버패키징(과잉 단백질에 의한 다중 캡시드)’ 및 ‘무조립’ 네 영역으로 구분되며, 각 영역은 특정 L·C·σ 조합에 대응한다. 예를 들어, 폴리머 길이가 300~500 뉴클레오타이드이고 단백질 농도가 5–10 μM, 이온 강도가 100–150 mM인 경우가 ‘성공적 포장’ 영역에 해당한다.
이 연구는 두 가지 중요한 함의를 제공한다. 첫째, 바이러스 복제 억제제 설계 시, 폴리머(또는 RNA)와 캡시드 단백질 사이의 동적 결합을 방해하는 작은 분자를 타깃으로 하면 핵형 형성 자체를 차단할 수 있다. 둘째, 나노소재 공학에서는 폴리머 길이와 용액 조건을 정밀하게 조절함으로써 캡시드 기반 나노캡슐을 맞춤형으로 제작할 수 있다. 특히, 협동적 이동 메커니즘을 이용하면 캡시드 내부에 기능성 물질을 효율적으로 포장하는 새로운 전략이 가능해진다.
댓글 및 학술 토론
Loading comments...
의견 남기기