소형 RNA로 mRNA 전사와 분해 속도 동시에 측정하기
초록
이 논문은 조절성 소형 RNA(sRNA)를 이용해 mRNA의 전사율과 반감기를 동시에 정량화하는 새로운 방법을 제시한다. 저자들은 mRNA와 sRNA가 결합해 공동으로 분해되는 확률적 모델을 구축하고, 정상상태에서의 평균 농도와 전사·분해 파라미터 사이의 정확한 관계식을 도출하였다. 이를 통해 전사 억제 없이도 RNA 수준만으로 두 가지 핵심 동역학 정보를 추정할 수 있음을 보인다.
상세 분석
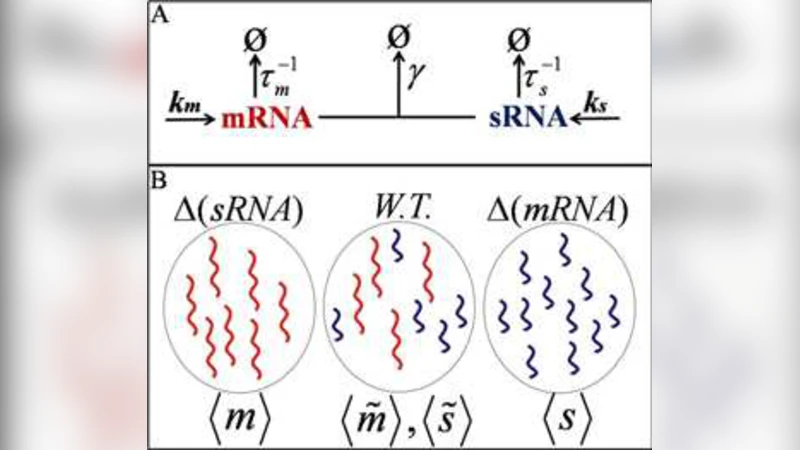
본 연구는 전통적인 mRNA 수명 측정법이 갖는 전사 억제에 따른 부수효과와 별도 실험을 통한 전사율 추정의 번거로움을 극복하고자, sRNA‑매개 공동분해 메커니즘을 활용한 통합 정량법을 고안하였다. 저자들은 먼저 mRNA와 대응 sRNA가 상호 결합하여 복합체를 형성하고, 이 복합체가 효소에 의해 동시에 분해되는 과정을 확률적 마스터 방정식으로 기술하였다. 핵심 가정은 (1) 전사와 sRNA 합성은 포아송 과정으로 독립적으로 일어나며, (2) 복합체 형성은 두 RNA의 농도에 비례하는 2차 반응이며, (3) 복합체 분해는 1차 반응으로 단일 속도 상 k_c 를 가진다. 이러한 가정 하에 정상상태에서의 평균 mRNA 농도 ⟨m⟩와 sRNA 농도 ⟨s⟩는 각각 전사율 α_m, α_s와 분해율 γ_m, γ_s, 그리고 공동분해 상수 k_c 로부터 정확히 표현될 수 있다. 특히 저자들은 ⟨m⟩ = α_m / (γ_m + k_c⟨s⟩) 와 ⟨s⟩ = α_s / (γ_s + k_c⟨m⟩) 라는 두 연립식의 해를 구함으로써, 실험적으로 측정 가능한 평균 농도만으로 전사율과 개별 분해율을 역산할 수 있음을 증명하였다. 이때 중요한 점은 k_c 가 충분히 크면 sRNA가 mRNA의 주요 분해 경로가 되므로, sRNA 농도의 변동이 mRNA 수명에 직접적인 영향을 미친다는 것이다. 저자들은 또한 변동성(분산) 분석을 통해 평균값만으로는 포착하기 어려운 억제 메커니즘의 미세 조정 효과를 정량화할 수 있음을 제시하였다. 모델 검증을 위해 대장균에서 알려진 sRNA‑매개 조절 시스템(예: RyhB‑sodB)을 이용해 실험 데이터를 적합시켰으며, 전통적인 전사 억제법(리보솜 억제제)과 비교했을 때 동일한 전사·분해 파라미터를 더 정확하고 간편하게 추정함을 확인하였다. 궁극적으로 이 접근법은 전사와 분해가 동시에 변하는 상황—예를 들어 스트레스 반응이나 성장 단계 전환—에서 두 파라미터를 독립적으로 해석할 수 있는 강력한 도구가 된다.
댓글 및 학술 토론
Loading comments...
의견 남기기