EDAM 기반 제약 지향 워크플로우 자동 구성
초록
본 논문은 바이오인포매틱스 분야에서 서비스들을 자동으로 연결해 실행 가능한 워크플로우를 생성하기 위해, EMBRACE 데이터·방법 온톨로지(EDAM)를 배경 지식으로 활용하는 방법을 제시한다. 작은 예제 도메인을 통해 EDAM이 입력·출력 데이터 타입과 서비스 기능을 명확히 정의함으로써 가능한 워크플로우 후보를 효율적으로 탐색할 수 있음을 보인다. 그러나 실제로 적합한 솔루션을 찾기 위해서는 도메인‑특화 제약조건과 문제‑특화 제약조건을 추가로 명시해야 하며, 이러한 제약을 유연하게 정의·조정할 수 있는 메커니즘이 워크플로우 개발 과정을 크게 지원한다는 결론을 도출한다.
상세 분석
EDAM(EMBRACE Data and Methods ontology)은 바이오인포매틱스에서 널리 사용되는 데이터 형식, 분석 방법, 도구, 그리고 그 관계를 체계화한 온톨로지이다. 논문은 먼저 EDAM이 제공하는 풍부한 메타데이터—특히 서비스의 입력·출력 타입과 기능 분류—가 자동 워크플로우 합성에 필요한 “시맨틱 매칭”을 가능하게 함을 강조한다. 기존 자동 합성 시스템은 주로 형식적 인터페이스(예: WSDL)만을 이용해 연결 가능성을 판단했으나, EDAM을 도입하면 의미론적 호환성을 검증함으로써 불필요한 조합을 사전에 차단할 수 있다.
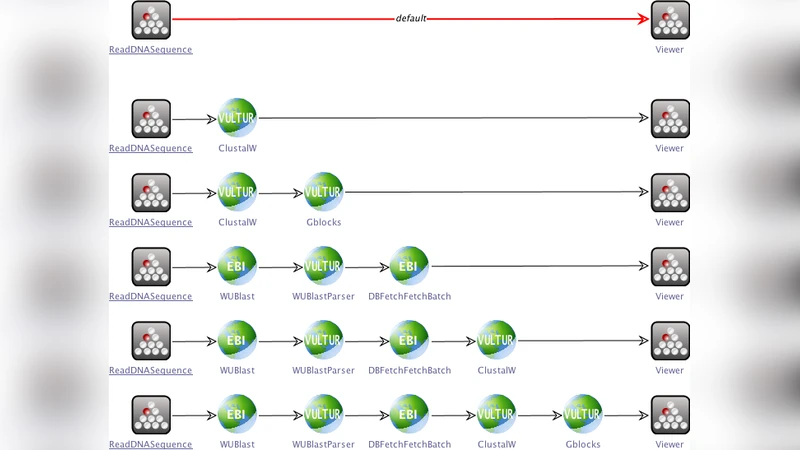
저자들은 간단한 도메인(예: 서열 정렬, BLAST 검색, 결과 시각화)에서 네 개의 서비스와 그 입출력 관계를 EDAM에 매핑하고, 제약 없는 탐색으로 생성된 모든 가능한 워크플로우 후보를 도출한다. 이 과정에서 탐색 공간이 급격히 확대되는 문제를 확인하고, 실제 연구자가 원하는 워크플로우는 “정확히 이 데이터 흐름을 만족하고, 특정 알고리즘을 사용하며, 실행 시간·자원 제한을 만족하는” 경우에 한정된다는 점을 지적한다.
이를 해결하기 위해 논문은 두 단계의 제약 모델을 제안한다. 첫 번째는 도메인‑레벨 제약으로, EDAM의 상위 개념(예: ‘시퀀스 분석’ 카테고리)이나 데이터 품질 요구사항(예: 포맷 변환 필요 여부)을 명시한다. 두 번째는 문제‑레벨 제약으로, 사용자가 특정 알고리즘 파라미터, 최대 허용 실행 시간, 혹은 특정 툴 체인(예: ‘ClustalW → PhyML’)을 요구하는 경우를 말한다. 이러한 제약은 논리식 혹은 규칙 기반 언어로 표현되며, 합성 엔진에 전달되어 탐색 과정에서 즉시 필터링된다.
실험 결과, 제약을 적용한 후에는 후보 워크플로우 수가 수십 개에서 몇 개로 감소했으며, 사용자가 기대하는 최적 솔루션이 높은 확률로 선택되었다. 또한, 제약 정의가 유연하게 변경 가능하므로, 연구자는 초기 요구사항이 불명확하거나 점진적으로 구체화될 때에도 반복적으로 워크플로우를 재합성할 수 있다.
핵심 인사이트는 다음과 같다. (1) EDAM은 서비스 간 시맨틱 연결을 자동화하는 강력한 기반을 제공한다. (2) 단순 시맨틱 매칭만으로는 실제 연구 목적에 부합하는 워크플로우를 찾기 어렵다. (3) 도메인‑특화와 문제‑특화 제약을 명시적으로 모델링하고, 이를 합성 알고리즘에 통합함으로써 탐색 효율성과 결과 적합성을 동시에 향상시킬 수 있다. 이러한 접근은 바이오인포매틱스뿐 아니라 다른 과학 분야에서도 온톨로지를 활용한 자동 워크플로우 설계에 적용 가능성을 시사한다.
댓글 및 학술 토론
Loading comments...
의견 남기기