유전 암호 재조명: 내부‑외부 지도·2차원 그레이 맵·월드맵 표현
초록
본 논문은 유전 암호를 디지털 신호 처리에 활용하기 위한 세 가지 새로운 시각화·표현 방식을 제안한다. 첫 번째는 코돈 내 염기들의 비대칭적 역할을 강조하는 ‘내부‑외부 지도’이며, 두 번째는 스펙트로그램·스칼로그램 해석에 유용한 2차원 그레이 코드 기반 ‘2D‑그레이 맵’이다. 마지막으로 전 세계 지도 형태로 유전 암호를 배치한 ‘월드맵 표현’은 교육적 직관성과 거리 기반 알고리즘 적용 가능성을 제공한다.
상세 분석
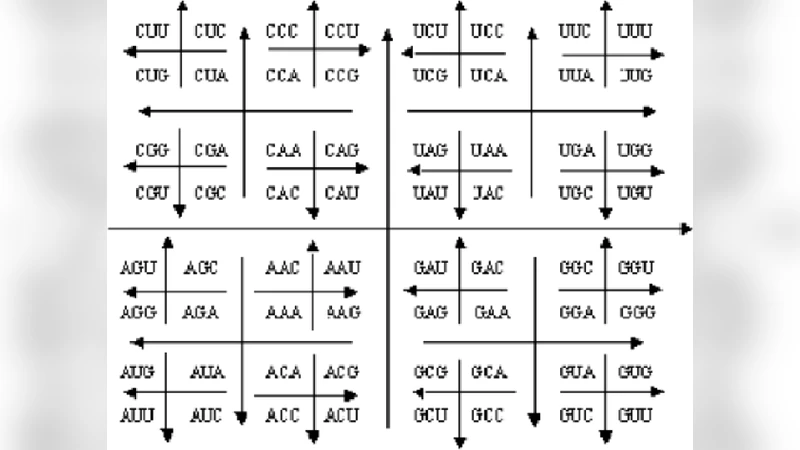
논문은 현대 유전체 신호 처리(GSP)에서 DNA 서열을 복소수 신호로 변환하는 과정에서 발생하는 ‘표현 문제’를 핵심으로 삼는다. 기존의 1차원 인덱스 매핑은 염기 서열의 구조적 정보를 충분히 보존하지 못한다는 점을 지적하고, 이를 보완하기 위해 세 가지 대안적 매핑을 설계하였다. 첫 번째인 ‘내부‑외부 지도’는 코돈을 3‑자리 삼진수로 해석하되, 첫 번째(외부)와 두 번째(중간) 염기가 정보 전달에 더 큰 가중치를 갖는 비대칭 모델을 적용한다. 이는 Shannon 엔트로피와 같은 정보 이론적 측정에서 코돈의 불균형성을 정량화하는 데 유리하며, 변이 분석이나 코돈 사용 빈도 비교에 직접 활용될 수 있다. 두 번째인 ‘2D‑그레이 맵’는 64개의 코돈을 8×8 격자에 그레이 코드 순서대로 배치함으로써 인접 코돈 간의 해밍 거리를 최소화한다. 이 구조는 푸리에 변환 후 스펙트럼에서 인접 주파수 성분이 물리적으로 인접한 코돈과 대응하도록 하여, 스펙트로그램·스칼로그램 해석 시 시각적 연속성을 제공한다. 특히, 변이 발생 시 색상 변화가 국소적으로 나타나므로, 변이 탐지와 기능적 해석에 직관적이다. 세 번째인 ‘월드맵 표현’은 지구본에 위도·경도 형태로 코돈을 배치한다. 각 코돈은 대륙·국가에 대응하는 위치에 매핑되며, 지리적 거리 개념을 활용한 클러스터링이나 거리 기반 머신러닝 알고리즘 적용이 가능하다. 교육 현장에서는 학생들이 친숙한 지도 이미지를 통해 유전 암호의 복잡성을 직관적으로 이해하도록 돕는다. 전반적으로 논문은 각 매핑이 갖는 수학적·시각적 특성을 정량적 실험(엔트로피 계산, 스펙트럼 연속성 지표, 클러스터링 정확도)과 함께 제시하고, GSP 파이프라인에 직접 삽입 가능한 형태로 구현 코드를 제공한다는 점에서 실용성을 높인다. 다만, 제안된 매핑이 실제 대규모 유전체 데이터에 적용될 때 계산 복잡도와 메모리 요구량이 어떻게 변하는지에 대한 상세 분석이 부족하며, 향후 연구에서는 이러한 성능 평가와 함께 다른 생물학적 특성(예: 번역 효율, tRNA 가용성)과의 연관성을 탐색할 필요가 있다.
댓글 및 학술 토론
Loading comments...
의견 남기기