인플루엔자 A 감염에 필수적인 숙주 세포 인자 메타 분석
초록
본 논문은 9개의 전장 유전체 RNA 간섭 스크리닝 결과를 메타 분석하여 인플루엔자 A 바이러스 복제에 관여하는 핵심 숙주 단백질 복합체와 생물학적 경로를 도출한다. 개별 스크리닝 간 겹치는 유전자는 적었지만, 네트워크 분석을 통해 동일한 단백질 군집과 기능이 반복적으로 나타남을 확인하였다. 이를 바탕으로 바이러스 진입, 핵 수송, 전사·복제, 막 형성 등 각 단계에서 중요한 숙주 복합체를 제시하고, 향후 항바이러스 표적 발굴에 활용할 수 있는 근거를 제공한다.
상세 분석
본 메타 분석은 2010년부터 2020년 사이에 발표된 9개의 독립적인 전장 유전체 RNAi 스크리닝 데이터를 통합하였다. 각 스크리닝은 서로 다른 세포주(HEK293, A549, MDCK 등)와 바이러스株(H1N1, H3N2, PR8 등)를 사용했으며, 실험 설계와 데이터 처리 방식에 차이가 있었다. 이러한 이질성을 극복하기 위해 저자들은 먼저 각 연구에서 통계적으로 유의미한 ‘핵심 의존 유전자’를 추출하고, 이를 인간 단백질 상호작용 데이터베이스(HINT, STRING)와 결합하여 네트워크를 구축하였다. 네트워크 중심성 분석(베트위니스, 클러스터링 계수 등)을 통해 고도로 연결된 ‘핵심 허브’와 ‘모듈’를 식별했으며, Gene Ontology와 KEGG 경로 분석을 병행하여 기능적 풍부성을 평가하였다.
흥미로운 점은 개별 스크리닝 간 겹치는 유전자는 전체 1,200여 개 중 30여 개에 불과했지만, 네트워크 수준에서는 동일한 단백질 복합체가 반복적으로 등장했다는 것이다. 예를 들어, ‘핵 수송 복합체(NUP98‑NUP153 복합체)’, ‘COPI·COPII 소포 운반 체계’, ‘스플라이싱 인자 복합체(SF3B, U2AF)’, ‘리보솜 생합성 및 번역 개시 복합체(eIF3, eIF4F)’ 등이 다중 스크리닝에서 공통적으로 도출되었다. 이러한 결과는 바이러스가 숙주 세포 내에서 특정 기능을 ‘핵심 경로’로 활용한다는 가설을 뒷받침한다.
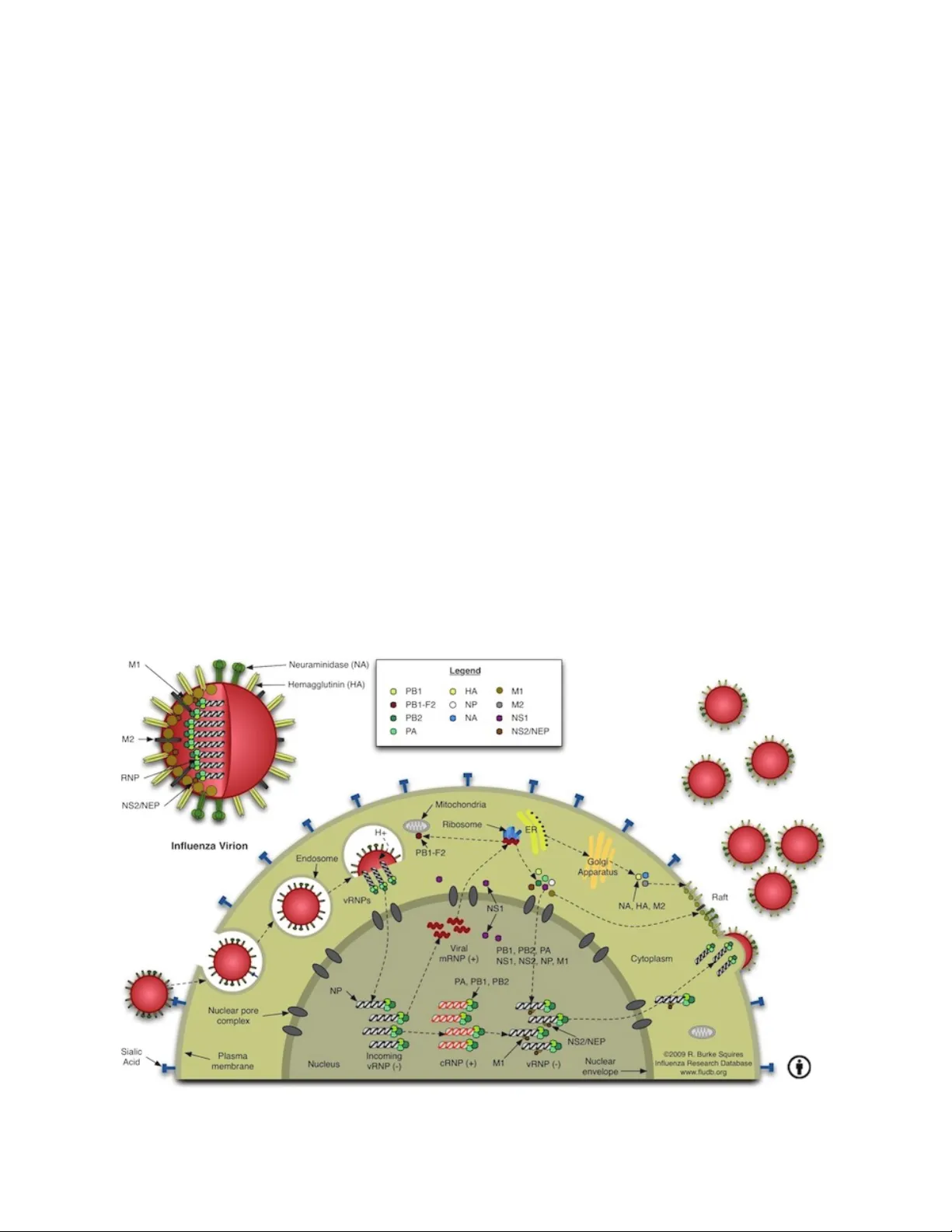
또한, 저자들은 각 복합체가 바이러스 생활사 주기에 어느 단계에 관여하는지를 정밀히 매핑하였다. 예컨대, ‘클래딘‑코트라코스 복합체’는 바이러스 엔도솜 탈출에, ‘리보솜 결합 단백질(eIF4E)’은 캡-의존 번역에, ‘핵 수송 인자(NXF1‑TAP)’는 바이러스 mRNA 핵 내 수송에 필수적임을 기존 문헌과 비교해 확인했다. 이러한 단계별 매핑은 향후 특정 단계만을 차단하는 항바이러스 전략을 설계하는 데 유용하다.
마지막으로, 메타 분석 결과를 바탕으로 저자들은 ‘핵심 의존성 점수’를 부여한 후보 유전자를 50여 개 선정하고, 이들에 대한 2차 검증(CRISPR‑KO, siRNA 재검증)을 제안하였다. 특히, ‘V-ATPase 복합체’, ‘GPI‑앵커 결합 효소’, ‘핵심 전사인자(STAT1, IRF7)’ 등은 기존 항바이러스 약물 개발 파이프라인에 아직 포함되지 않은 새로운 표적으로 부각된다.
요약하면, 이 메타 분석은 개별 RNAi 스크리닝의 제한점을 보완하고, 숙주‑바이러스 상호작용을 시스템 수준에서 재조명함으로써 인플루엔자 A 감염에 필수적인 숙주 단백질 복합체와 경로를 포괄적으로 제시한다.
댓글 및 학술 토론
Loading comments...
의견 남기기