시각적 통합 유전체 기반 암 환자 군집화 시스템 iGPSe
초록
iGPSe는 유전체·전사체·마이크로RNA 등 다중 오믹스 데이터를 시각적으로 통합·분석하여 암 환자를 임상 결과에 따라 자동 군집화하는 도구이다. 비지도 클러스터링, 그래프와 평행 집합 시각화, 그리고 생존 분석을 결합해 연구자가 복합 바이오마커를 빠르게 탐색하고 검증할 수 있게 한다. TCGA 유방암 데이터를 활용한 사례에서 mRNA와 miRNA 조합이 생존 예측에 유의미함을 확인하였다.
상세 분석
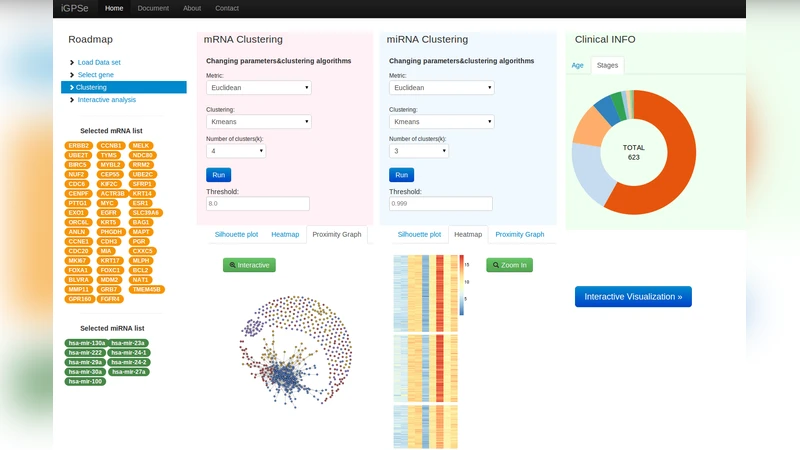
iGPSe는 현대 암 연구에서 필수적인 ‘통합 오믹스’ 분석을 시각적 인터페이스와 결합함으로써, 데이터 과학자와 임상 연구자 사이의 인지적 격차를 크게 줄인다. 시스템은 먼저 사용자가 선택한 유전자·마이크로RNA 피처 집합을 기반으로 비지도 클러스터링(주로 K‑means 혹은 계층적 군집)을 수행한다. 클러스터링 결과는 노드와 엣지로 구성된 그래프 형태로 시각화되며, 각 노드는 환자를, 엣지는 유사성을 나타낸다. 이때 그래프 레이아웃은 거리 기반 차원 축소(t‑SNE, MDS 등)를 적용해 고차원 관계를 2D/3D 공간에 보존한다.
다음 단계에서는 ‘평행 집합(parallel sets)’ 시각화를 통해 여러 피처 조합에 따른 군집 변화를 직관적으로 비교한다. 사용자는 슬라이더와 체크박스로 피처를 동적으로 추가·제거하면서, 각 군집의 크기·구성·임상 변수(예: 연령, 종양 단계) 변화를 실시간으로 관찰한다. 특히, 생존 분석 모듈은 Kaplan‑Meier 곡선과 로그‑rank 검정을 자동으로 실행해, 선택된 군집 간의 통계적 차이를 즉시 제시한다.
iGPSe의 핵심 강점은 ‘시각‑분석 루프’를 짧게 만든다는 점이다. 전통적인 파이프라인에서는 데이터 전처리 → 차원 축소 → 클러스터링 → 통계 검정 → 결과 해석 순으로 수일~수주가 소요되지만, iGPSe는 GUI 기반 인터랙션으로 동일 과정을 몇 분 안에 반복한다. 또한, 시스템은 TCGA와 같은 공개 데이터베이스와 직접 연동해 메타데이터(임상 정보, 치료 기록)를 자동 가져오며, 사용자 정의 데이터도 손쉽게 업로드 가능하도록 설계되었다.
기술적 한계로는 현재 지원되는 클러스터링 알고리즘이 제한적이며, 대규모(수만 명) 환자 데이터에 대한 실시간 그래프 렌더링이 GPU 의존적이라는 점이다. 또한, 피처 선택이 주관적이기 때문에 과적합 위험이 존재한다. 향후에는 자동 피처 중요도 평가, 베이지안 네트워크 기반 인과 추론, 그리고 클라우드 기반 스케일링을 도입해 이러한 제약을 보완할 필요가 있다.
댓글 및 학술 토론
Loading comments...
의견 남기기