염색질 구조 기반 모델로 인간 세포 DNA 복제 시기 정확히 예측
초록
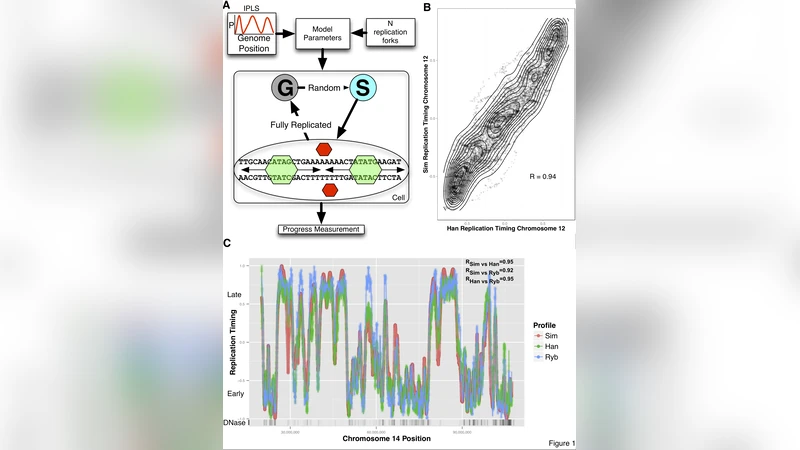
이 논문은 DNase 과민성 부위를 복제 시작점으로 활용하고, 복제 포크 수 하나만을 조정 변수로 삼는 간소화된 메커니즘 모델을 제시한다. 모델은 인간 여러 세포주의 복제 시기 데이터를 0.92 이상의 피어슨 상관계수로 재현하며, 복제 시기가 특정 조절 메커니즘에 의존하지 않고 염색질 구조에 의해 자연스럽게 나타나는 현상임을 보여준다.
상세 분석
연구진은 복제 시작 확률 지형(IPLS)을 정의하고, 각 복제 포크가 무작위로 아직 복제되지 않은 부위에 접근해 일정 확률로 시작하도록 시뮬레이션하였다. 핵심 가정은 복제 시작 위치가 DNase 과민성 부위와 높은 상관관계를 가진다는 점이며, 이를 입증하기 위해 ENCODE 프로젝트의 167가지 세포특이적 마크를 비교하였다. DNase HS가 가장 높은 예측 정확도(r=0.87)를 보였고, 다른 마크들은 DNase HS와의 겹침을 제거하면 성능이 급격히 떨어졌다. 이는 DNase HS가 복제 시기의 독립적인 결정인자임을 의미한다. 모델의 유일한 생물학적 파라미터는 동시에 활성화될 수 있는 복제 포크 수(N)이며, 각 염색체 길이에 비례해 선형적으로 증가한다는 사실을 실험적으로 확인하였다. 또한, 모델은 인간뿐 아니라 마우스 섬유아세포에서도 높은 재현성을 보였으며, 염색체 전위가 복제 시기에 미치는 영향을 시뮬레이션으로 재현하였다. 파라미터가 거의 없고, DNase HS 위치만으로도 높은 정확도를 얻는 점은 모델이 과적합 위험이 낮고, 복제 시기가 염색질 구조의 집합적 효과에 의해 emergent하게 나타난다는 강력한 증거가 된다.
댓글 및 학술 토론
Loading comments...
의견 남기기