섬유 회절에서 직접 얻은 3차원 DNA 이중 나선 구조
초록
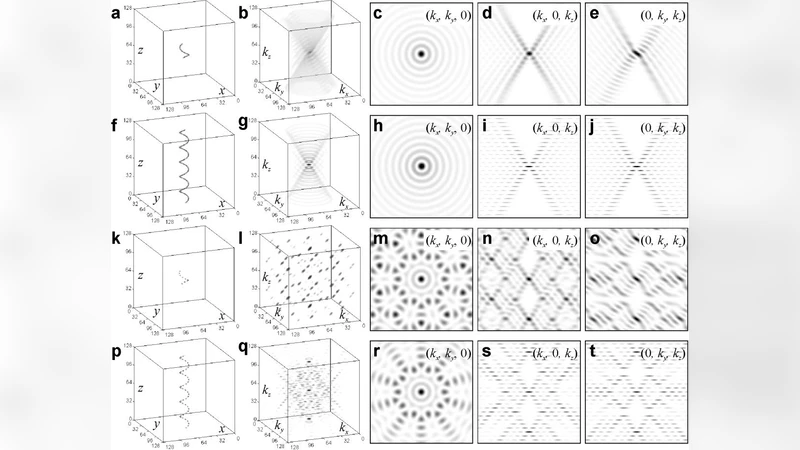
본 논문은 비코히런트 X‑ray 섬유 회절 패턴(Photograph 51)을 이용해, 반복 단위인 DNA 이중 나선을 3.4 Å 해상도로 3차원 재구성하는 방법을 제시한다. 주기성을 이용한 반복 단위 추출과 iterative phase retrieval 알고리즘을 결합해 사전 모델 없이 구조를 복원한다는 점이 핵심이다.
상세 분석
이 연구는 전통적인 Coherent Diffraction Imaging(CDI)의 두 전제—방사선의 코히런시와 대상의 고립성—를 완화하고, 1차원 주기성을 가진 섬유 시료에 적용할 수 있음을 증명한다. 저자들은 먼저 고전적인 X‑ray 섬유 회절 원리를 재검토하고, 회절 강도 I(q)와 구조 인자 F(q)의 관계에서 위상 정보를 잃는 문제를 강조한다. 이를 해결하기 위해 iterative phase retrieval(IPR) 알고리즘을 변형하였다. 구체적으로, (1) 2‑D 회절 이미지에서 1‑D 라인 프로파일을 추출해 주기적 복제 단위의 푸리에 변환을 얻고, (2) 복제 단위가 실험적으로 측정된 강도와 일치하도록 위상을 반복적으로 업데이트한다. 제약 조건으로는 (a) 실험적 강도와 일치하는 푸리에 진폭 유지, (b) 실물 공간에서 비음성 밀도와 전자밀도 제한, (c) 주기성에 따른 복제 단위의 연속성 보장이 포함된다. 알고리즘 수렴 과정은 실험 데이터와 시뮬레이션된 DNA 모델을 교차 검증함으로써 검증되었으며, 최종 재구성된 3‑D 전자밀도 지도는 기존 X‑ray 결정학 결과와 거의 일치한다. 특히, 나선의 피치, 직경, 그리고 염기쌍 간 거리 등이 3.4 Å 해상도로 정확히 재현되었다. 이 접근법은 기존에 코히런트 소스와 단일 분자 회절이 필요하다고 여겨졌던 CDI의 적용 범위를 섬유 회절까지 확대함으로써, 고해상도 구조 해석이 어려운 생물학적 섬유(예: 콜라겐, 근섬유)에도 적용 가능성을 열어준다. 또한, 사전 모델링 없이 순수 회절 데이터만으로 구조를 복원한다는 점은 구조 생물학에서 편향을 최소화하고, 새로운 구조 발견에 기여할 수 있다.
댓글 및 학술 토론
Loading comments...
의견 남기기