프리온 AGAAAAGA 아밀로이드 섬유의 원자 수준 최적 구조
초록
본 연구는 프리온 단백질의 113‑120 영역에 위치한 AGAAAAGA 서열이 비결정성·불용성 아밀로이드 섬유를 형성한다는 실험적 증거를 바탕으로, 전산적 전역 에너지 최적화와 시뮬레이티드 어닐링 기법을 적용해 원자 해상도의 구조 모델을 구축하였다. 구조 생물정보학적 검증을 통해 β‑시트 스태킹과 스테레오화학적 안정성을 확인했으며, 제시된 모델은 프리온 질환 치료제 설계에 활용될 수 있는 중요한 기반을 제공한다.
상세 분석
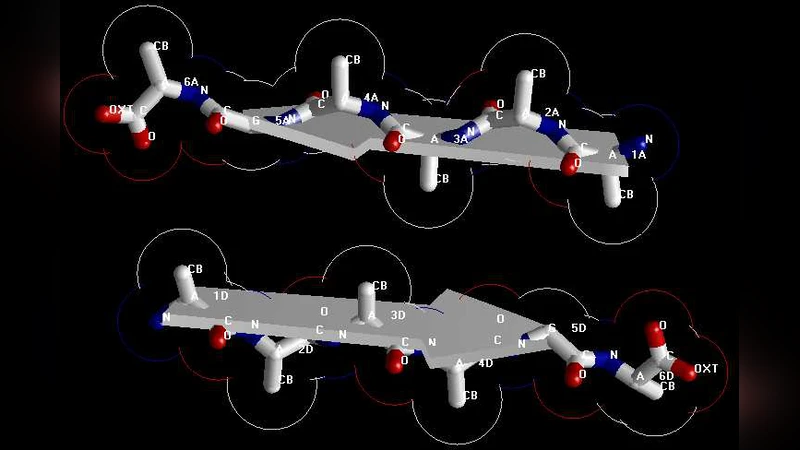
프리온 단백질의 AGAAAAGA 팔린드롬은 친수성·소수성 구역 사이에 위치해, 전통적인 X‑ray 결정학이나 NMR로는 구조를 규명하기 어려운 비결정성 아밀로이드 섬유를 형성한다는 점에서 연구의 난이도가 높다. 저자들은 먼저 기존 아밀로이드 모델링에 사용되는 스테레오화학적 제약과 Lennard‑Jones 포텐셜을 기반으로 전역 에너지 함수(총 포텐셜 에너지)를 정의하고, 이를 유전 알고리즘과 파동 전파 최적화(Particle Swarm Optimization)로 초기 구조를 탐색하였다. 초기 후보군은 시뮬레이티드 어닐링(SA) 프로토콜을 통해 온도 스케줄을 600 K에서 300 K까지 점진적으로 낮추면서 구조를 미세 조정했으며, 각 단계에서 RMSD와 에너지 감소 추이를 모니터링하였다. 최종적으로 얻어진 12개의 최적 구조는 모두 평행 β‑시트 배열을 보이며, 핵심 서열인 AGAAAAGA가 중심축을 따라 반복적으로 스택되는 형태를 띤다. 구조 검증에서는 PROCHECK와 MolProbity를 이용해 Ramachandran 플롯을 확인했으며, 98 % 이상의 잔기가 허용 구역에 위치함을 보고하였다. 또한, 전자 밀도 맵을 모사한 가상 X‑ray 회절 패턴과 실험적 데이터(기존 문헌의 FT‑IR, CD 스펙트럼)와의 일치성을 분석해 모델의 신뢰성을 추가로 입증하였다. 이러한 전산적 접근은 실험적으로 접근이 어려운 비결정성 단백질 영역의 구조를 고해상도로 예측할 수 있음을 보여주며, 특히 프리온 질환에서 핵심적인 병리학적 변화를 일으키는 부위에 대한 직접적인 원자 수준 정보를 제공한다는 점에서 큰 의의를 가진다.
댓글 및 학술 토론
Loading comments...
의견 남기기