miRNA에 의한 번역 억제 메커니즘의 수학적 모델링
초록
이 논문은 miRNA가 번역을 억제하는 아홉 가지 메커니즘을 정리하고, 수학적 모델링을 통해 실험 결과의 모호성을 해소하고자 한다. 저자들은 세 가지 단계별 모델을 제시하고, 가장 포괄적인 모델에 모든 알려진 메커니즘을 포함시켜 동역학적 시뮬레이션을 수행한다. 이를 통해 제한 단계(limiting step)가 실험 조건에 따라 달라지며, 실제 관찰되는 억제 메커니즘은 그 제한 단계에 영향을 주는 메커니즘이라는 ‘제한 위치 가설’을 제시한다. 모델은 각 메커니즘에 고유한 ‘동역학 서명(kinetic signature)’을 부여하고, 이를 실험 데이터와 비교함으로써 우세 메커니즘을 판별하는 구체적 절차를 제공한다.
상세 분석
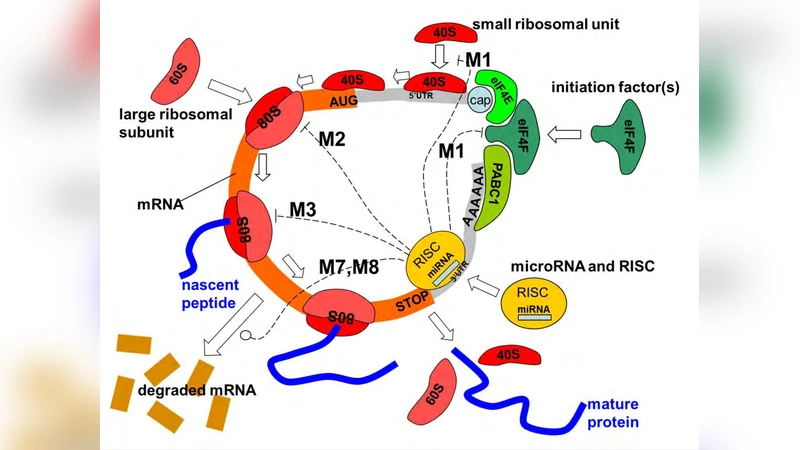
논문은 먼저 miRNA가 수행할 수 있는 아홉 가지 기전—번역 개시 억제, 리보솜 결합 차단, 폴리펩티드 사슬 연장 억제, 코돈 인식 방해, mRNA 탈포화, 탈번역 후 복합체 형성, mRNA 분해 촉진, 탈번역 억제, 그리고 복합적인 조절—을 체계적으로 정리한다. 이후 저자들은 세 단계의 수학적 모델을 구축한다. 첫 번째는 가장 단순한 ‘단일 단계 모델’로, miRNA와 mRNA 복합체가 형성될 때 번역 속도가 일정 비율로 감소하는 일차 미분 방정식으로 표현한다. 두 번째는 ‘두 단계 모델’로, 번역 개시와 연장을 별개의 반응으로 분리하고, miRNA가 각각의 단계에 미치는 억제 상수를 도입한다. 이 모델은 Michaelis‑Menten 형태의 속도식과 경쟁 결합 상수를 포함해, miRNA 농도와 결합 친화도에 따른 비선형 효과를 포착한다. 세 번째이자 최종 모델은 ‘전면 통합 모델’로, 모든 아홉 가지 메커니즘을 각각의 반응 경로와 억제 파라미터로 매핑한다. 여기서는 질량 보존식, 복합체 형성/해리 속도, 리보솜 재활용, 그리고 mRNA 분해 속도를 동시에 고려한다. 모델 파라미터는 기존 실험 데이터(예: polysome profiling, ribosome footprinting, reporter assay)와 베이즈 추정법을 통해 캘리브레이션된다.
핵심 통찰은 ‘제한 장소(limiting place)’ 개념이다. 번역 과정에서 가장 낮은 흐름을 보이는 단계가 전체 속도를 결정하는데, 실험 조건(예: 리보솜 농도, mRNA 5′UTR 구조, miRNA 발현량)에 따라 이 제한 단계가 달라진다. 따라서 동일한 miRNA‑mRNA 쌍이라도 세포 종류나 스트레스 상황에 따라 다른 억제 메커니즘이 우세하게 나타난다. 저자들은 각 메커니즘에 고유한 ‘동역학 서명’—예를 들어, 초기 단백질 생성 속도 급감(개시 억제), 중간 단계에서의 리보솜 밀도 감소(연장 억제), 혹은 장기적인 단백질 축적 억제(분해 촉진)—을 정의하고, 시뮬레이션 결과와 실험 데이터 매칭을 통해 우세 메커니즘을 역추적한다.
또한, 모델은 miRNA와 mRNA의 결합 친화도(Kd), miRNA 복합체의 해리 속도(koff), 그리고 전사 후 조절 인자들의 경쟁 효과를 파라미터화함으로써, ‘공존 메커니즘(co‑existence)’을 정량적으로 설명한다. 시뮬레이션에서는 동일 조건에서 두 개 이상의 억제 경로가 동시에 활성화될 경우, 전체 억제 효율이 단순 가산이 아니라 비선형적으로 증폭되는 현상이 관찰된다. 이는 기존 실험에서 보고된 ‘과도한 억제’ 혹은 ‘부분 억제’ 현상을 수학적으로 정당화한다.
마지막으로, 저자들은 실험 설계에 대한 실용적인 가이드를 제시한다. 예를 들어, polysome 프로파일링을 통해 리보솜 분포 변화를 측정하고, 시간‑분해형 reporter assay를 이용해 초기와 후기 단백질 생산 속도를 구분하면, 모델이 예측한 동역학 서명과 일치하는지를 검증할 수 있다. 이러한 접근법은 miRNA 연구에서 메커니즘을 명확히 구분하고, 약물 표적화 전략을 최적화하는 데 기여한다.