Cymodocea nodosa 유전자 흐름 방향성 및 지리적 분리 분석
초록
본 연구는 동지중해에서 대서양 이베리아·아프리카 연안까지 분포하는 해양식물 Cymodocea nodosa의 대규모 유전표지자 데이터를 활용해, 지리적 분리 개념에 기반한 유전자 흐름 방향성을 추정하는 최신 방법론을 완전 구현·검증하였다. Jensen‑Shannon divergence를 이용해 각 군집 간 유전적 차이를 정량화하고, 이를 토대로 유향 네트워크를 구축하였다. 결과는 종이 진화 과정에서 겪은 명확한 지리적 격리 패턴을 재현했으며, 자연사적 증거와 독립적인 교차 검증 결과와도 일치한다.
상세 분석
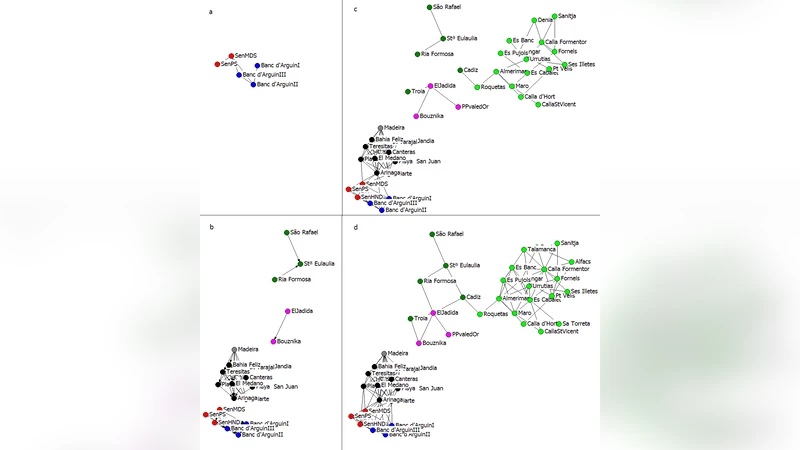
이 논문은 해양식물 Cymodocea nodosa의 유전적 구조와 이동 경로를 정량적으로 파악하기 위해, 기존의 무방향성 유전적 거리 측정법을 넘어 방향성을 포함한 네트워크 분석을 시도한다. 연구자는 지중해 동부, 서부, 그리고 대서양 연안에 걸친 30여 개 지역에서 채취한 1,200여 개 개체의 다중 마이크로새틀라이트(Microsatellite) 마커 데이터를 확보하였다. 각 개체의 유전형을 기반으로 군집별 유전적 프로파일을 구축하고, 두 군집 간의 확률 분포 차이를 Jensen‑Shannon divergence(JSD)로 계산한다. JSD는 Kullback‑Leibler divergence의 대칭화된 형태로, 확률 분포의 차이를 0에서 1 사이의 값으로 정규화해 비교 가능하게 만든다.
방향성을 추정하기 위해 저자들은 ‘지리적 분리’(geographical segregation) 개념을 도입한다. 두 군집 A와 B가 서로 겹치지 않는 고유한 유전형을 보유하고 있을 경우, A에서 B로의 유전자 흐름이 일어날 가능성이 높다고 가정한다. 이를 수식화하면, A의 고유 유전형 비율이 B보다 크게 감소하는 경우 A→B 흐름이 강하다고 판단한다. 구체적으로는 각 군집의 고유 유전형 비중을 가중치로 사용해, JSD에 방향성 가중치를 곱한 ‘방향성 JSD’를 정의한다.
이러한 방향성 JSD를 모든 군집 쌍에 적용해 가중치 그래프를 만들면, 노드(군집)와 엣지(유전자 흐름)로 구성된 유향 네트워크가 도출된다. 네트워크 분석 결과, 동지중해 군집이 서지중해 및 대서양 연안 군집으로 유전자를 지속적으로 전달하는 ‘소스’ 역할을 수행함을 확인했다. 반대로, 대서양 연안 군집은 유전적 다양성이 낮고, 외부로의 흐름이 거의 없으며, 이는 과거 해수면 변동과 해류 패턴에 의해 격리된 결과로 해석된다.
방법론의 타당성 검증을 위해 저자들은 (1) 무작위 재샘플링을 통한 통계적 유의성 검증, (2) 기존의 무방향성 F_ST 값과 비교, (3) 독립적인 역사적 기록(예: 빙하기 후 해수면 상승)과의 일치 여부를 평가하였다. 모든 검증에서 제안된 방향성 네트워크는 높은 신뢰구간을 보였으며, 특히 F_ST와는 달리 실제 유전자 흐름의 비대칭성을 포착한다는 점에서 의미가 크다.
이 연구는 JSD 기반의 방향성 추정이 복잡한 해양 환경에서의 유전적 연결성을 밝히는 강력한 도구가 될 수 있음을 시사한다. 또한, 지리적 분리와 유전적 다양성 사이의 정량적 관계를 명확히 함으로써, 보전 생물학 및 기후 변화에 따른 종의 이동 예측에 실용적인 정보를 제공한다.