ModuLand Cytoscape 플러그인 겹치는 네트워크 모듈과 계층적 레이어 분석
초록
**
ModuLand 플러그인은 Cytoscape 환경에서 겹치는 네트워크 모듈을 효율적으로 탐지하고, 모듈 간 계층 구조를 자동으로 구축한다. 모듈 코어와 브리지 노드를 제공해 생물학적 기능을 예측하며, 단백질 구조와 대사 네트워크에 적용한 사례를 통해 그 유용성을 입증한다.
**
상세 분석
**
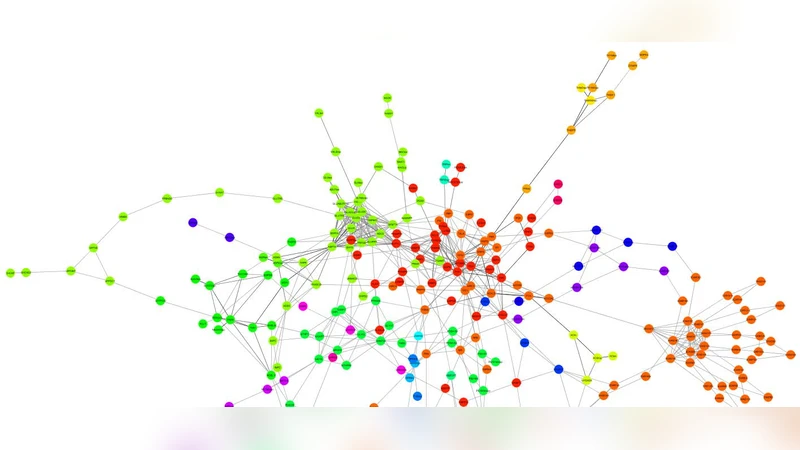
본 논문은 기존 Cytoscape 클러스터링 플러그인들이 겹치는 모듈 탐지와 계층적 구조 구축에 한계를 가지고 있음을 지적하고, ModuLand 프레임워크를 기반으로 한 새로운 플러그인을 제시한다. 핵심 알고리즘은 두 단계로 이루어진다. 첫 번째는 LinkLand 방식으로 각 노드·엣지의 ‘영향 영역(influence zone)’을 계산해 지역적 영향을 정량화한다. 두 번째는 ProportionalHill 방법으로 이러한 영향 영역을 합산해 ‘커뮤니티 중심성(community centrality)’을 산출하고, 이를 3차원 ‘커뮤니티 랜드스케이프’의 높이(z축)로 시각화한다. 랜드스케이프의 봉우리는 겹치는 모듈을 형성하며, 각 봉우리의 기울기와 넓이는 모듈의 강도와 범위를 나타낸다.
플러그인은 이 랜드스케이프를 기반으로 모듈 코어(가장 높은 할당값을 가진 노드)를 자동 지정하고, 여러 모듈에 동시에 속하는 노드를 ‘브리지(bridgeness)’ 점수로 평가한다. 이러한 점수는 다중 모듈 간 정보 흐름을 매개하는 핵심 아미노산이나 대사 효소를 식별하는 데 활용된다.
계층적 모듈 구조는 하위 레벨의 모듈을 메타노드로 축소하고, 모듈 간 겹침 정도를 메타엣지 가중치로 변환함으로써 상위 레벨을 재귀적으로 생성한다. 이 과정은 네트워크가 단일 메타노드가 될 때까지 진행되며, 각 레벨마다 모듈 수와 메타엣지 수가 급격히 감소한다. 구현상의 최적화로 작은 가중치 메타엣지를 제거해 계산 복잡도를 O(n³)에서 실질적으로 7배 가량 가속한다.
실험에서는 E. coli Met‑tRNA 합성효소의 단백질 구조 네트워크에 적용해 5개의 기능적 서브도메인과 일치하는 5개의 모듈을 도출하였다. 특히, 알려진 통신 경로에 관여하는 아미노산이 모듈 코어 또는 브리지 노드에 위치함을 확인해 기능적 해석 가능성을 입증했다. 또한, E. coli와 공생 박테리아 B. aphidicola의 대사 네트워크를 비교해, 환경 변동성이 큰 종의 네트워크가 더 많은, 그리고 더 특화된 모듈을 형성한다는 생태학적 의미를 도출하였다. 이러한 결과는 기존 비겹침 모듈 방법과도 높은 일치도를 보이며, ModuLand가 제공하는 모듈 코어와 브리지 개념이 생물학적 기능을 정확히 반영함을 시사한다.
전반적으로 ModuLand 플러그인은 (1) 광범위한 겹침을 허용하는 모듈 탐지, (2) 자동 계층적 모듈 구축, (3) 모듈 중심 및 브리지 노드 정량화, (4) 직관적인 시각화와 사용자 친화적 인터페이스를 제공한다는 점에서 기존 도구들을 뛰어넘는 종합 솔루션이다.
**
댓글 및 학술 토론
Loading comments...
의견 남기기