고대 유전자 재현과 실험 진화의 융합
초록
본 논문은 고대 단백질 서열을 재구성해 현대 미생물에 삽입하고, 이를 실험 진화 시스템에 투입함으로써 ‘역사적 재생‑재생성’ 실험을 설계한다. 고대-현대 유전자의 기능 차이를 실시간으로 관찰하고, 우연성과 결정론이 진화 경로에 미치는 영향을 정량화한다.
상세 분석
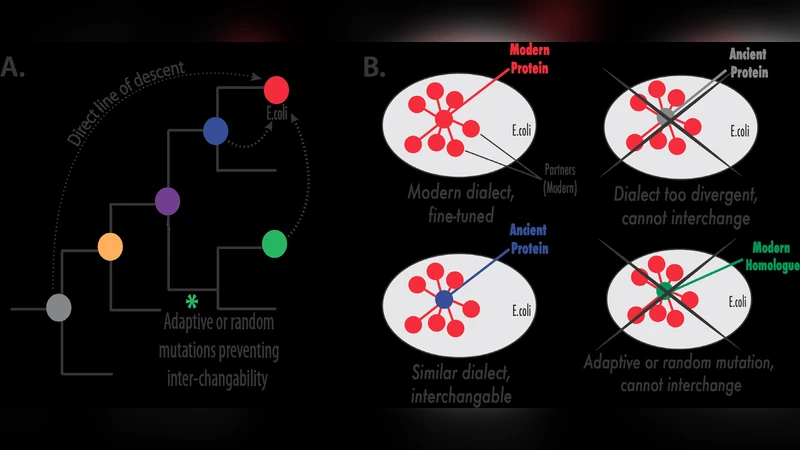
이 연구는 두 개의 독립적인 방법론, 즉 고대 서열 복원(Ancestral Sequence Reconstruction, ASR)과 실험 진화(Experimental Evolution, EE)를 통합한 새로운 실험 플랫폼을 제시한다. ASR 단계에서는 베이즈 추정과 최대우도 방법을 이용해 고대 효소나 조절 단백질의 아미노산 서열을 추정하고, 합성 DNA를 통해 현대 대장균 혹은 효모에 삽입한다. 여기서 핵심은 ‘컨텍스트 의존성’이다; 고대 단백질이 현대 세포 내에서 올바르게 접히고 기능을 발휘하도록, 보조 인자와 상호작용 파트너를 동시에 재구성하거나, 필요시 현대 파트너와의 상호작용을 최소화하도록 설계한다.
EE 단계에서는 마이크로플루이드 디바이스 혹은 자동화된 배양 시스템을 활용해 대규모 병렬 진화 라인을 구축한다. 각 라인은 동일한 초기 고대-현대 하이브리드 균주를 시작점으로 하며, 선택 압력(예: 특정 기질 이용, 항생제 내성, 온도 스트레스 등)을 다양하게 설정한다. 이때 ‘리와인드‑리플레이’ 개념을 구현하기 위해, 동일한 선택 조건을 여러 번 반복 적용하거나, 조건을 점진적으로 변화시켜 고대 단백질이 새로운 환경에 적응하는 과정을 관찰한다.
데이터 수집은 전통적인 성장 곡선, 경쟁 실험 외에도, 전사체·단백질체 분석, 단일 세포 유전체 시퀀싱, 그리고 실시간 진화 추적을 위한 CRISPR‑Cas 기반 라벨링을 포함한다. 이렇게 얻은 시계열 데이터는 베이지안 네트워크 모델이나 머신러닝 기반 적합도 지형 추정에 투입돼, 특정 변이가 언제, 어떤 선택 압력 하에서 고정되었는지를 정량화한다.
핵심 통찰은 다음과 같다. 첫째, 고대 단백질은 현대 파트너와의 ‘비호환성’으로 인해 초기 적합도가 낮지만, 진화 과정에서 보상 변이가 빠르게 축적되어 기능을 회복한다. 둘째, 동일한 선택 압력 하에서도 라인마다 서로 다른 보상 경로가 선택되며, 이는 우연성(Contingency)의 역할을 강조한다. 셋째, 특정 환경에서는 고대 단백질이 현대 형태보다 더 높은 효율을 보이기도 하는데, 이는 진화적 ‘잠재적 적합도(cryptic fitness)’가 존재함을 시사한다. 마지막으로, 고대‑현대 하이브리드 시스템은 단백질‑네트워크 수준에서의 진화적 제약을 직접 측정할 수 있는 강력한 도구가 된다.
이러한 결과는 진화론적 논쟁인 ‘우연 vs 결정론’에 실험적 근거를 제공하며, 고대 생물학, 합성 생물학, 그리고 진화 공학 분야에 새로운 연구 패러다임을 제시한다.
댓글 및 학술 토론
Loading comments...
의견 남기기