호지킨 림프종 자동 이미지 분석
초록
본 연구는 CD30 면역염색된 호지킨 림프종 조직 슬라이드의 디지털 이미지를 자동으로 전처리·분류하여, 비림프종, 결절경화형, 혼합세포형 세 그룹의 CD30 발현 양상을 정량화하였다. 전처리 단계에서 배경을 효과적으로 제거하고, 지도학습 기반 픽셀 분류를 통해 각 클래스의 면적 비율을 추출하였다. 결과는 결절경화형과 비림프종이 CD30 양에서 차이를 보이며, 혼합세포형은 높은 변동성을 보여 다른 두 그룹과 겹친다는 점을 확인했다. 이는 고해상도 이미지에서 종양 영역을 자동으로 식별하고, 이후 객체 검출 등 비용이 큰 분석을 집중할 수 있는 기반을 제공한다.
상세 분석
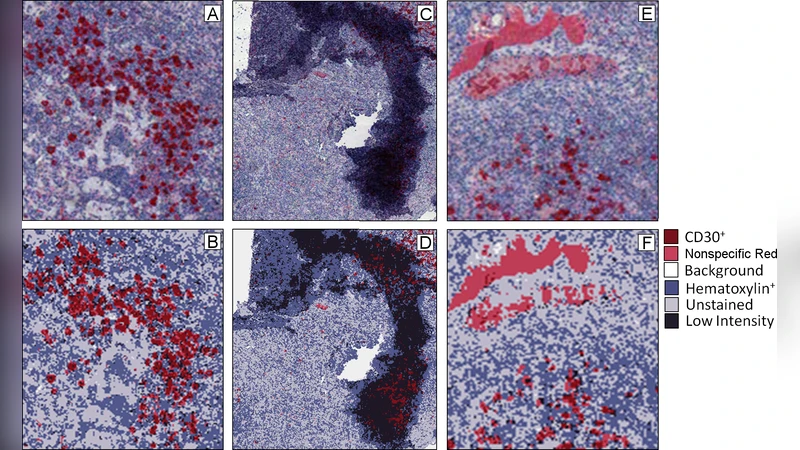
이 논문은 호지킨 림프종(Hodgkin lymphoma, HL)의 병리학적 특성을 디지털 이미지 분석으로 정량화하려는 최초의 시도 중 하나로, 특히 CD30이라는 표지자를 이용한 면역염색(slide) 이미지를 대상으로 한다. 연구팀은 Aperio SVS 포맷으로 저장된 고해상도 슬라이드 이미지를 다루기 위해, 먼저 전체 이미지를 1/16 정도로 다운스케일링한 뒤 전처리 과정을 적용하였다. 전처리 단계는 색상 공간 변환과 임계값 기반 이진화, 형태학적 연산을 결합해 조직 영역과 배경을 명확히 구분한다. 이 과정에서 배경(주로 유리 슬라이드와 비색소화 영역)이 효과적으로 제거되어, 이후의 분류 작업이 잡음에 방해받지 않도록 설계되었다.
분류 단계에서는 지도학습(supervised learning) 접근법을 채택했으며, 사전에 정의된 네 가지 클래스(예: CD30 양성, CD30 음성, 비특이적 염색, 배경)를 픽셀 수준에서 할당한다. 학습 데이터는 전문가가 라벨링한 소규모 샘플을 이용해 SVM 혹은 랜덤 포레스트와 같은 전통적인 분류기를 훈련시켰으며, 특징으로는 RGB 및 HSV 색상값, 텍스처(라플라시안, Gabor 필터) 등을 사용하였다. 결과적으로 각 이미지에 대해 클래스별 면적 비율이 정량화되었고, 이를 통해 세 가지 조직군(비림프종, 결절경화형, 혼합세포형)의 CD30 발현 양상을 비교하였다.
통계 분석 결과, 결절경화형과 비림프종은 CD30 양성 영역의 평균 비율에서 유의한 차이를 보였으며(p < 0.01), 혼합세포형은 높은 분산을 나타내어 다른 두 그룹과 겹치는 경향을 보였다. 이는 혼합세포형이 조직 내 CD30 발현이 불균일하고, 종양 미세환경이 다양함을 시사한다. 또한, 전처리와 픽셀 분류 파이프라인이 고해상도 원본 이미지(수십억 픽셀)에서 직접 적용될 경우 연산 비용이 크게 증가함을 감안해, 먼저 저해상도 단계에서 종양 영역을 대략적으로 식별하고, 이후 고해상도에서 집중적인 객체 검출(예: 라켄시 세포)으로 전환하는 전략을 제안한다.
이 연구의 강점은 (1) 실제 임상 병리 현장에서 흔히 사용되는 SVS 포맷을 그대로 활용한 자동화 파이프라인 구축, (2) 배경 제거와 색상 기반 전처리로 잡음 최소화, (3) 픽셀 수준의 정량적 분류를 통해 조직군 간 차이를 통계적으로 검증한 점이다. 반면, 제한점으로는 (가) 학습 데이터가 제한적이어서 분류기의 일반화 능력이 충분히 검증되지 않았으며, (나) CD30 외 다른 면역표지자(예: CD15, PAX5)를 동시에 분석하지 않아 다중 마커 기반의 종양 이질성을 포착하지 못했다는 점이다. 향후 연구에서는 더 다양한 라벨링 데이터와 딥러닝 기반의 세그멘테이션 모델을 도입해 정확도를 높이고, 다중표지자 이미지와 결합해 종양 마이크로환경을 종합적으로 해석하는 방향이 기대된다.
댓글 및 학술 토론
Loading comments...
의견 남기기