엔트로믹스: 염기 삽입 반응의 열역학과 장거리 유전체 조직
초록
이 논문은 차세대 시퀀싱의 제로 모드 웨이브가이드(ZMW) 기술을 이용해 DNA 합성 효소의 염기 삽입 반응이 서열에 따라 달라지는 현상을 관찰하고, 이를 ‘삽입 화학 퍼텐셜 Δμ’라는 새로운 물리량으로 정의한다. 그래프 이론과 통계열역학을 결합해 Δμ의 열역학 모델을 구축하고, 이를 ‘삽입 엔트로피’로 정량화한다. 논문은 Δμ를 유전체 서열로부터 계산하는 공식들을 제시하고, Δμ의 열역학적 제약이 DNA의 구조적 제약과 유전체 조립 원칙에 어떤 영향을 미치는지 분석한다. 마지막으로 이러한 제약이 전체 유전체에 걸친 장거리 상관성을 만들어내며, 이를 활용한 기능적·생물학적 응용 사례를 보여준다.
상세 분석
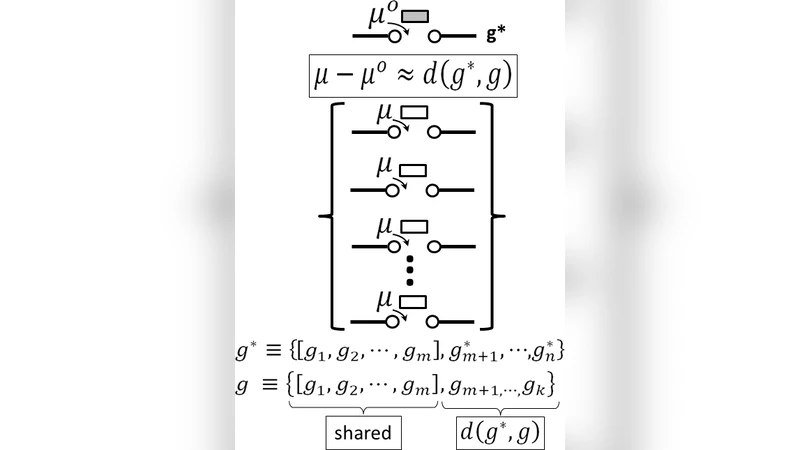
본 연구는 ZMW 기반 실시간 단일분자 시퀀싱에서 관찰된 염기 삽입 속도의 서열 의존성을 물리학적 변수인 화학 퍼텐셜 Δμ로 정량화한다. 저자들은 DNA 서열을 정점과 간선으로 표현하는 그래프 모델을 구축하고, 각 정점(염기) 주변의 국소 서열 패턴을 ‘상태 공간’으로 정의한다. 통계열역학적 접근을 통해 각 상태의 자유 에너지와 엔트로피를 계산하고, Δμ_i = μ_i^* – μ_i^0 형태의 식으로 삽입 반응의 화학 퍼텐셜 차이를 도출한다. 여기서 μ_i^*는 실제 실험에서 측정된 삽입 반응의 자유 에너지, μ_i^0는 무작위 서열 가정하의 기준값이다. 중요한 점은 Δμ_i가 단순히 염기 종류에 의존하는 것이 아니라, 주변 10~30bp 정도의 이웃 서열 구조와 전자·수소 결합 네트워크에 의해 크게 변한다는 것이다. 이를 ‘삽입 엔트로피’ S_i = –∂Δμ_i/∂T 로 정의함으로써 온도 의존성을 포함한 열역학적 특성을 확보한다.
또한, 저자들은 Δμ_i의 분포가 전체 유전체에 걸쳐 비정상적인 장거리 상관성을 보인다는 통계적 증거를 제시한다. 푸리에 변환과 상관 함수 분석을 통해 특정 염기 패턴(예: CpG 섬, 전사인자 결합 부위) 주변에서 Δμ_i가 주기적으로 변동하며, 이는 ‘엔트로픽 파동’이라 부른다. 이러한 파동은 DNA 복제·전사 과정에서 에너지 효율성을 최적화하는 진화적 압력으로 해석될 수 있다.
논문은 마지막으로 Δμ_i를 직접 계산할 수 있는 알고리즘을 제시한다. 입력으로 FASTA 파일을 받아, 각 위치의 k‑mer(보통 k=15)를 그래프 이론적 방법으로 매핑하고, 사전 학습된 파라미터(결합 에너지, 전자 구름 밀도 등)를 적용해 Δμ_i와 S_i를 출력한다. 이 알고리즘은 기존의 염기 서열 분석 툴과 통합 가능하며, 변이 탐지, 전사인자 결합 예측, 염색체 구조 모델링 등에 활용될 수 있다. 전체적으로 본 연구는 DNA 서열을 단순한 정보 코드가 아니라, 물리‑화학적 에너지 흐름을 내포한 동적 시스템으로 재해석하는 중요한 전환점을 제공한다.
댓글 및 학술 토론
Loading comments...
의견 남기기