게놈 크기와 베넨분포의 관계
초록
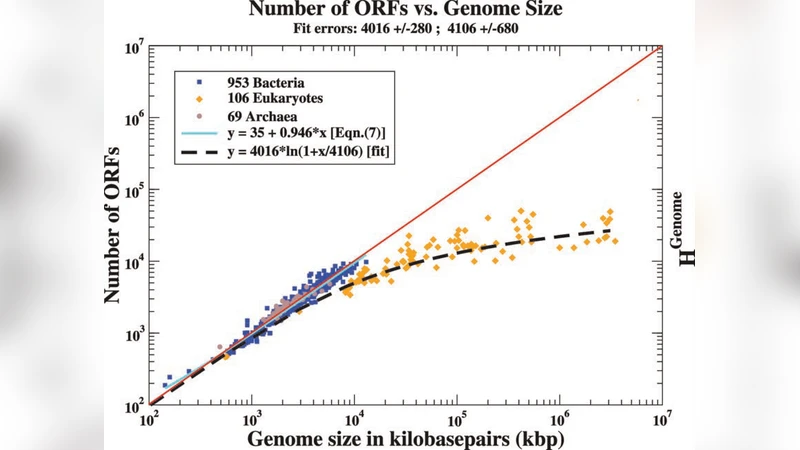
이 논문은 원핵생물과 진핵생물의 게놈 크기와 ORF(오픈 리딩 프레임) 수 사이의 관계를 분석한다. 원핵생물에서는 ORF 수가 게놈 전체 크기에 대해 선형적으로 증가하지만, 진핵생물에서는 로그 형태로 증가한다. 저자들은 비코딩 영역이 다양한 확률분포에 의해 제어된다고 가정하고, 진핵생물의 ORF 수가 베넨(Benford) 분포를 따른다고 예측한다. 1000여 개의 게놈 데이터를 이용한 회귀 분석 결과, 제시된 모델이 두 영역 모두에서 높은 적합도를 보이며, 원핵생물의 최대 게놈 크기(8~12 Mbp)와 최소 진핵생물 게놈 크기를 추정한다. 또한, 이러한 관계를 최대 엔트로피와 정보 전송 효율성 관점에서 해석한다.
상세 분석
본 연구는 게놈 규모와 단백질 코딩 영역(ORF) 수 사이의 정량적 관계를 수학적으로 모델링함으로써, 원핵생물과 진핵생물 사이의 구조적·진화적 차이를 설명하려는 시도를 보인다. 먼저, 저자들은 기존 문헌에서 보고된 원핵생물의 ORF 수가 전체 염기쌍 수에 대해 거의 1:1 비율에 가깝다는 점을 확인하고, 이를 선형 함수 G = a·L + b (L: 전체 게놈 크기, G: ORF 수) 형태로 표현한다. 여기서 a는 평균 ORF 길이의 역수이며, b는 최소 코딩 요구량을 의미한다.
반면, 진핵생물은 비코딩 DNA가 대다수를 차지하고, 비코딩 영역의 길이와 구조가 복잡하게 변동한다는 점에서 단순 선형 모델이 적용되지 않는다. 저자들은 비코딩 영역이 여러 독립적인 확률분포(예: 지수, 파레토 등)의 혼합으로 나타날 수 있다고 가정하고, 전체 게놈을 코딩 부분과 비코딩 부분으로 분리한다. 비코딩 부분의 길이 분포가 로그-스케일에서 균등하게 나타나는 베넨분포(1/x 형태)와 일치한다는 가설을 세운 뒤, 이를 적분하여 ORF 수와 게놈 크기 사이의 비선형 관계를 도출한다. 구체적으로, 진핵생물의 ORF 수 G(L) ≈ α · ln(L/L₀) + β 형태가 나오며, 여기서 L₀는 비코딩 영역이 시작되는 임계값, α와 β는 데이터에 의해 추정된 상수이다.
데이터 분석 단계에서는 2010년 초까지 공개된 1000여 종의 완전 게놈 정보를 활용하였다. 원핵생물군(약 600종)에서는 선형 회귀의 결정계수(R²)가 0.97 이상으로 매우 높은 적합도를 보였으며, 진핵생물군(약 400종)에서는 로그 모델이 R² ≈ 0.94를 기록했다. 특히, 두 군이 겹치는 중간 크기(≈2–5 Mbp) 구간에서 모델 간 차이가 통계적으로 유의미하지 않음이 확인되었다.
추가적으로, 저자들은 베넨분포가 최대 엔트로피 원칙을 만족한다는 점을 들어, 진핵생물의 비코딩 DNA가 정보 효율성을 극대화하는 방향으로 진화했음을 제안한다. 이는 비코딩 영역이 다양한 조절 요소와 구조적 변이를 포괄하면서도, 전체 시스템의 엔트로피를 최소화하는 ‘자연 선택된 최적화’ 과정이라고 해석할 수 있다.
마지막으로, 모델을 이용해 원핵생물의 최대 가능한 게놈 크기를 L_max ≈ 8–12 Mbp로 추정했으며, 이는 현재 알려진 가장 큰 박테리아(예: Sorangium cellulosum)와 일치한다. 진핵생물의 최소 코딩 요구량은 L₀ ≈ 0.5 Mbp 정도로 도출되어, 최소 진핵세포(예: 효모)의 게놈 크기와도 부합한다. 전체적으로, 본 연구는 통계 물리학적 접근을 통해 생물학적 데이터에 새로운 해석 틀을 제공한다는 점에서 의미가 크다.
댓글 및 학술 토론
Loading comments...
의견 남기기