통합 mRNA와 DNA 복제수 분석을 통한 암 유전자 우선순위 선정 비교 리뷰
초록
본 리뷰는 유전체 복제수(CN)와 전사발현(GE) 데이터를 동시에 활용해 암 관련 유전자를 우선순위화하는 12가지 알고리즘을 비교한다. 시뮬레이션 데이터와 실제 유방암·백혈병 데이터셋을 이용해 ROC‑AUC, 상위 200개 유전자에서의 진양성 비율, 실행 시간을 평가했으며, edira, Ortiz‑Estevez, pint/simcca, PREDA/SODEGI R이 전반적으로 우수한 성능을 보였다. 또한, R 패키지 intcomp을 통해 투명한 벤치마크 파이프라인을 제공한다.
상세 분석
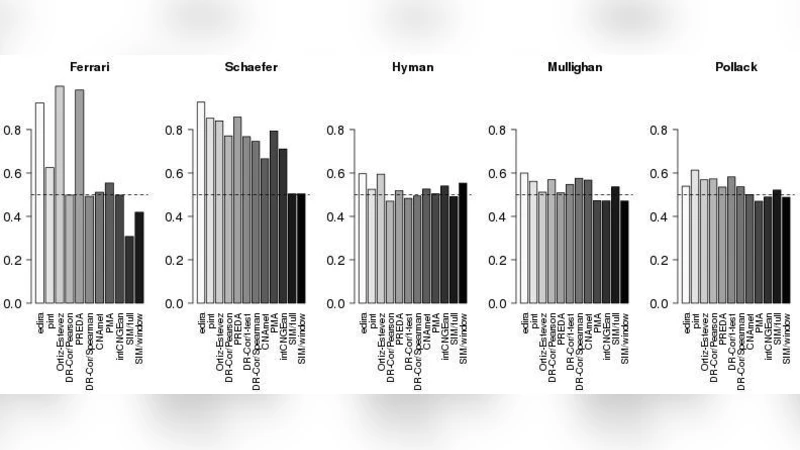
이 논문은 암 연구에서 흔히 수행되는 복제수(CN)와 전사발현(GE) 데이터의 통합 분석을 체계적으로 정량 비교한다. 먼저 기존 문헌과 Bioconductor 저장소를 탐색해 CN‑GE 통합에 사용 가능한 12개의 알고리즘을 선정했으며, 각 방법은 두 단계 접근법, 회귀 모델, 상관 기반, 정준 상관(Canonical Correlation Analysis), 잠재 변수 모델 등 다양한 통계적·기계학습적 프레임워크를 포함한다. 두 개의 시뮬레이션 데이터셋(‘Schäfer’와 ‘Ferrari’)은 복제수와 발현이 동시에 변하는 블록 구조와 다양한 잡음 수준을 모사해 알고리즘의 민감도와 특이도를 테스트한다. 실제 데이터는 두 개의 유방암 마이크로어레이와 하나의 급성 림프구성 백혈병 데이터셋으로, 각각 알려진 암 유전자 리스트(유방암 유전자, Cancer Gene Census)를 골드 스탠다드로 사용했다. 성능 평가는 (i) 전체 유전자 리스트에 대한 ROC‑AUC, (ii) 상위 200개, 100개, 50개, 20개 유전자에서의 진양성 비율, (iii) 실행 시간으로 구분했다. 결과는 edira가 전반적인 AUC에서 가장 높은 중위 순위를 기록했으며, Ortiz‑Estevez와 pint/simcca가 그 뒤를 이었다. 특히 상위 200개 유전자에서 진양성 비율이 가장 높은 방법은 pint/simcca였으며, edira와 PREDA/SODEGI R도 높은 순위를 차지했다. 실행 시간 측면에서는 edira와 PMA가 1분 이내로 가장 빠르게 동작했으며, Ortiz‑Estevez는 최대 3분, 반면 permutation 기반 방법(CNAmet, DR‑Correlate 등)은 수십 분에서 수시간까지 걸렸다. 논문은 또한 시뮬레이션에서 높은 성능을 보인 일부 알고리즘이 실제 데이터에서는 과적합 위험이 있음을 지적한다. 마지막으로, R‑패키지 intcomp을 공개함으로써 연구자들이 새로운 알고리즘이나 데이터셋을 손쉽게 추가·비교할 수 있는 투명한 벤치마크 환경을 제공한다.
댓글 및 학술 토론
Loading comments...
의견 남기기