CytoITMprobe: 사이토스케이프를 위한 네트워크 정보 흐름 플러그인
초록
CytoITMprobe는 기존 ITM Probe 알고리즘을 Cytoscape 환경에 통합한 플러그인으로, 사용자가 任의 가중치·방향성을 가진 네트워크를 입력하고, 출발·도착 노드와 감쇠 계수를 지정하면 정보 흐름 모델(발신·흡수·채널)을 실행한다. 결과는 의미 있는 서브네트워크와 요약 테이블 형태로 제공되며, 로컬 실행·웹 서비스 두 가지 방식으로 접근 가능하고, 다른 Cytoscape 플러그인과의 연계가 용이하도록 설계되었다.
상세 분석
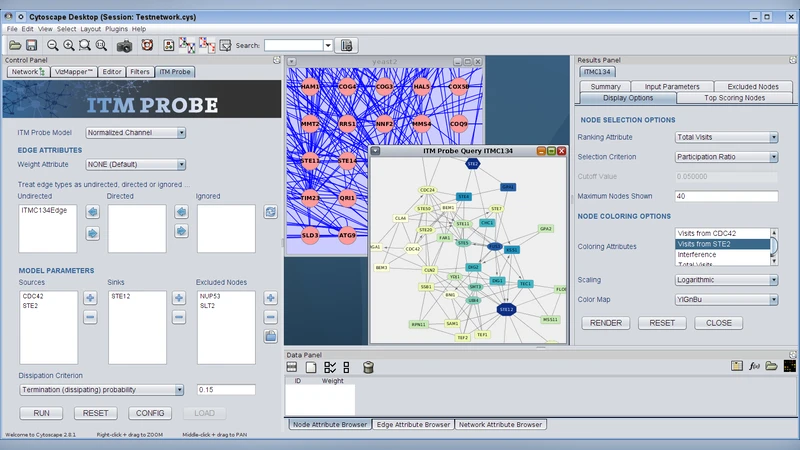
CytoITMprobe는 ITM Probe가 제안한 이산시간 랜덤 워크 기반 정보 흐름 프레임워크를 Cytoscape 플러그인 형태로 구현함으로써, 기존 웹 서비스가 갖는 네트워크 제한을 극복한다. 핵심은 (1) 사용자 정의 가중치와 방향성을 가진 임의의 그래프를 입력으로 받아들일 수 있다는 점이며, (2) 세 가지 모델—발신(emitting), 흡수(absorbing), 채널(channel)—을 동일한 인터페이스에서 선택·실행할 수 있다는 점이다. 발신 모델은 지정된 소스 노드에서 시작한 워커가 네트워크를 탐색하며 각 중간 노드에 도달하는 평균 방문 횟수 H_si 를 반환하고, 흡수 모델은 각 중간 노드에서 지정된 싱크 노드로 도달할 확률 F_ik 를 계산한다. 채널 모델은 H_si와 F_ik를 결합해 Φ_s,i,k = H_si·F_ik 를 정의하고, 이를 정규화한 ˆΦ_s,i,K 를 통해 소스‑싱크 사이의 가장 가능성 높은 경로와 중간 노드의 기여도를 시각화한다.
감쇠 파라미터 µ(0<µ<1)는 각 단계마다 워커가 네트워크를 떠날 확률을 조절한다. µ가 작을수록 워커는 짧은 거리 내에서 소멸해 지역적 정보를 강조하고, µ가 1에 가까울수록 장거리 탐색이 가능해 전역 구조를 반영한다. 이는 물리·생물학적 상황(예: 단백질 분해)과도 일맥상통한다.
알고리즘 구현 측면에서 CytoITMprobe는 백엔드로 Python 기반 ITM Probe를 사용한다. 대규모 희소 비대칭 행렬의 직접 해를 구하기 위해 SciPy의 SuperLU와 UMFPACK을 활용한다. UMFPACK이 BLAS와 연동될 경우 성능이 크게 향상되지만 설치가 까다로워, 플러그인은 기본적으로 원격 웹 서비스 호출을 지원해 사용자가 로컬 환경을 구성하지 않아도 된다.
사용자 인터페이스는 Cytoscape API로 구현된 Java GUI이며, 쿼리 폼에서 네트워크, 경계 노드, 감쇠 계수를 입력받아 백엔드에 전달한다. 결과는 원본 네트워크의 노드·엣지 속성으로 저장돼 Cytoscape의 레이아웃, 스타일링, 다른 플러그인(예: 기능 풍부화, 클러스터링)과 자유롭게 연계할 수 있다. 출력은 서브네트워크 형태와 탭 구분 텍스트 파일(CSV) 두 가지 형태로 제공돼 downstream 분석 파이프라인에 바로 삽입 가능하다.
CytoITMprobe의 주요 강점은 (1) 임의 네트워크 적용 가능성, (2) 감쇠와 경계 설정을 통한 흐름 범위 조절, (3) Cytoscape 생태계와의 원활한 통합이다. 따라서 단백질‑단백질 상호작용망뿐 아니라 신경망, 사회망, 대사망 등 다양한 도메인에 적용할 수 있다. 또한, 랜덤 워크와 확산 모델을 수학적으로 명확히 정의하고, 선형 시스템 해법을 이용해 효율적으로 계산함으로써 대규모 데이터에서도 실용성을 확보한다.
댓글 및 학술 토론
Loading comments...
의견 남기기