인간과 영장류 유전체 비정렬 비교와 암흑 물질 탐색
초록
본 연구는 k‑mer 기반 조성 스펙트럼(CS) 분석을 이용해 인간과 네 종의 영장류(침팬지, 고릴라, 오랑우탄, 마카크) 유전체를 비정렬 방식으로 비교하였다. 전체 유전체뿐 아니라 반복 서열과 유전자 영역을 마스킹한 ‘암흑 물질’ 영역에서도 유의미한 보존된 시너지 패턴을 발견했으며, GC 함량과 k‑mer 분포를 결합한 거리 측정이 시너지 검출 효율을 크게 향상시켰다.
상세 분석
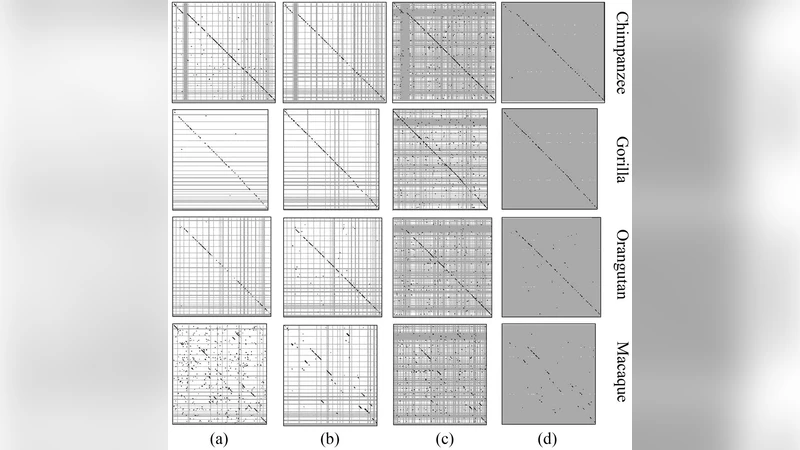
이 논문은 전통적인 정렬 기반 방법이 의존하는 이산적 앵커(유전자, 고보존 비코딩 요소) 대신, 연속적인 ‘퍼지 유사성’에 기반한 거리 행렬을 구축한다는 점에서 혁신적이다. 1 Mb 길이의 구간을 점으로 전환하고, 각 구간 간의 거리로는 (i) 10‑mer(4‑알파벳), (ii) 6‑mer(4‑알파벳), (iii) 20‑mer(2‑알파벳, 퓨린‑피리미딘) 빈도와 (iv) GC 함량 차이를 사용한다. 거리 함수는 스피어만 순위 상관계수를 적용해 변동성을 최소화했으며, 네 가지 거리 모두에서 로컬 최소값을 추출해 ‘T‑set’을 만든다. 이후 T‑set들의 교집합(T₁~T₄)으로 트랙을 정의하고, 메인 대각선(바이시터) 근처에 연속적으로 나타나는 트랙을 ‘주 패턴’이라 명명한다.
주요 결과는 다음과 같다. 첫째, 인간‑침팬지·고릴라·오랑우탄 간에는 마스크 여부와 관계없이 대각선에 긴 트랙이 집중돼 전반적인 시너지 보존을 확인한다. 둘째, 인간‑마카크 비교에서는 초기에는 트랙이 흩어져 있었지만, 마카크 염색체 순서를 재배열하면 대각선에 트랙이 재집중된다. 이는 기존의 염색체 재배열 연구와 일치하며, CS 기반 거리 행렬이 실제 염색체 재배열 신호를 포착함을 시사한다. 셋째, 트랙 길이가 4 점 이상인 경우는 우연 발생 확률이 극히 낮으며, 거리 측정에 사용된 네 가지 지표를 동시에 적용할수록 잡음 트랙이 급격히 감소한다는 통계적 검증을 제시한다. 넷째, ‘암흑 물질’(반복 서열·유전자 마스크 후 남은 영역)에서도 GC와 k‑mer 조합이 충분히 강력한 신호를 제공해, 비코딩·반복 영역이 진화적 보존 정보를 담고 있음을 입증한다.
이러한 접근법은 (1) 정렬이 어려운 대규모 유전체 비교에 적용 가능하고, (2) 비코딩·반복 영역까지 포괄하는 전반적인 유전체 구조 보존을 정량화할 수 있다는 점에서 유전체 진화 연구에 새로운 도구를 제공한다. 또한, k‑mer 기반 조성 스펙트럼이 GC 함량과 상보적으로 작용한다는 발견은 향후 다중 스케일(구성 vs 조직) 분석 모델 구축에 중요한 시사점을 제공한다.
댓글 및 학술 토론
Loading comments...
의견 남기기