네트워크 재구성을 위한 협조형 온라인 순위 학습기
초록
본 논문은 단백질‑단백질 상호작용(PPI) 예측을 이진 분류가 아닌 순위 매김 문제로 전환하고, 각 단백질에 대한 로컬 모델을 네트워크 구조와 연계해 동시에 학습하는 온라인 패시브‑어그레시브(PA) 알고리즘인 COLoR을 제안한다. 실험 결과, 전역 SVM보다 높은 정밀도를 보였지만, 동일 네트워크에 대해 개별 로컬 SVM이 가장 우수함을 확인하였다.
상세 분석
COLoR은 “협조형 온라인 순위 학습기”라는 이름 그대로, 네트워크 내 각 정점(단백질)에 대해 별도의 로컬 스코어링 함수를 학습하면서 인접 정점들의 파라미터가 서로 가깝도록 L2 정규화를 부여한다. 이때 전역 모델 W₀와 로컬 모델 Wᵢ를 β라는 가중치로 혼합해 S(p,q)=β pᵀWᵢ q+(1‑β) pᵀW₀ q 라는 이중 구조를 만든다. β=0이면 순수 전역 학습, β=1이면 완전 로컬 학습이 된다. 손실 함수는 삼중항(피벳, 양성, 음성) 기반의 힌지 손실 l_W(p, p⁺, p⁻)=max(0, 1‑S(p,p⁺)+S(p,p⁻))이며, 이는 순위 매김에 적합한 마진 기반 목표이다.
대규모 네트워크에서 모든 Wᵢ를 동시에 최적화하는 것은 계산량이 급증하므로, 저자들은 온라인 PA 프레임워크를 채택한다. 매 반복마다 하나의 단백질 pᵢ와 양성·음성 파트너(p⁺, p⁻)를 샘플링하고, 현재 파라미터와 인접 모델들의 평균 Wⱼ( j∈N(i) ) 사이의 거리 제약을 포함한 2차 최적화 문제를 풀어 τ라는 스칼라 업데이트 양을 구한다. τ는 C(허용 오차)와 현재 마진에 기반해 제한되며, 이를 통해 Wᵢ←Wⱼ+ (1/Nₑ)τV, W₀←W₀+τV (V=p(p⁺‑p⁻)ᵀ) 로 업데이트한다. 이 과정은 각 단계마다 파라미터가 급격히 변하지 않도록 “이전 단계와의 거리” 제약을 추가함으로써 안정성을 확보한다.
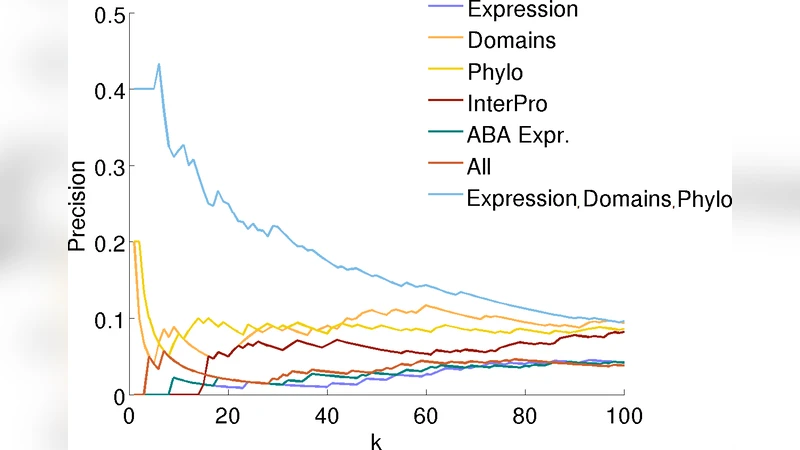
실험은 포스트시냅스 밀도(PSD) PPI 네트워크(114단백질, 211상호작용)에서 수행되었다. 특징으로는 마우스 뇌 관련 마이크로어레이 발현, 99종의 정교한 계통 발생 데이터, Pfam·InterPro 도메인·시그니처, 그리고 Allen Brain Atlas의 뇌 부위별 발현이 사용되었다. 각 특징은 TF‑IDF 가중치를 적용해 벡터화했으며, 다양한 조합을 시험해 가장 높은 정밀도를 보인 조합은 발현+도메인+시그니처+계통 발생 데이터였다.
성능 평가는 5‑fold 교차 검증 후 상위 k개 예측쌍에 대한 정밀도(precision@k)로 이루어졌다. 결과는 (1) 전역 SVM이 가장 낮은 정밀도를 보였고, (2) COLoR이 전역 SVM보다 상위 40개 정도에서 유의미하게 우수했으며, (3) 개별 로컬 SVM이 전체적으로 가장 높은 정밀도를 기록했다는 점이다. 이는 로컬 모델이 각 단백질의 특수한 특징을 충분히 포착할 수 있지만, COLoR이 인접 정점 간 파라미터 공유를 통해 일반화 능력을 어느 정도 확보한다는 것을 의미한다. 또한, 알란 뇌 지도 데이터는 단독으로는 예측력을 제공하지 못했으며, 다른 특징과 결합될 경우 오히려 성능을 저하시켰다.
한계점으로는 (가) 네트워크 규모가 수천 노드 수준으로 확대될 경우 인접 정점 간 L2 정규화 비용이 급증할 수 있다. (나) β 파라미터와 C 값에 대한 민감도 분석이 부족해 실제 적용 시 튜닝이 필요하다. (다) 로컬 SVM이 가장 좋은 성능을 보였음에도 불구하고, 로컬 모델을 학습하기 위한 충분한 라벨 데이터가 없을 경우 COLoR과 같은 다중 작업 협조 학습이 유리할 수 있다는 점을 더 명확히 검증할 여지가 있다. 전반적으로, 본 연구는 PPI 예측을 순위 매김 관점에서 재구성하고, 온라인 PA 기반 다중 작업 학습이라는 새로운 설계를 제시했으며, 향후 대규모 네트워크와 다양한 도메인에 적용 가능한 기반을 제공한다.
댓글 및 학술 토론
Loading comments...
의견 남기기