코돈 레벨 기반 유전암호 진화 모델: 캡처와 애매중간 시나리오의 통합 해석
초록
**
본 논문은 코돈과 tRNA의 “형상 공간”을 이용해 유전암호 진화의 두 주요 가설인 코돈 캡처와 애매중간 시나리오를 하나의 물리적 모델로 통합한다. 1차원 ‘코돈 레벨’이라는 스칼라 값을 도입해 코돈 군집과 인식 범위의 변화를 수학적으로 표현하고, 각각의 시나리오에 맞는 선택 압력(아미노산 합성 비용, 중성 돌연변이) 하에서 시뮬레이션을 수행한다. 결과는 애매중간 시나리오에서 코돈 재배정이 매우 빠르게 일어나며, 코돈 캡처 시나리오에서는 중성 돌연변이만을 보존하는 세포가 살아남는다는 점을 보여준다.
**
상세 분석
**
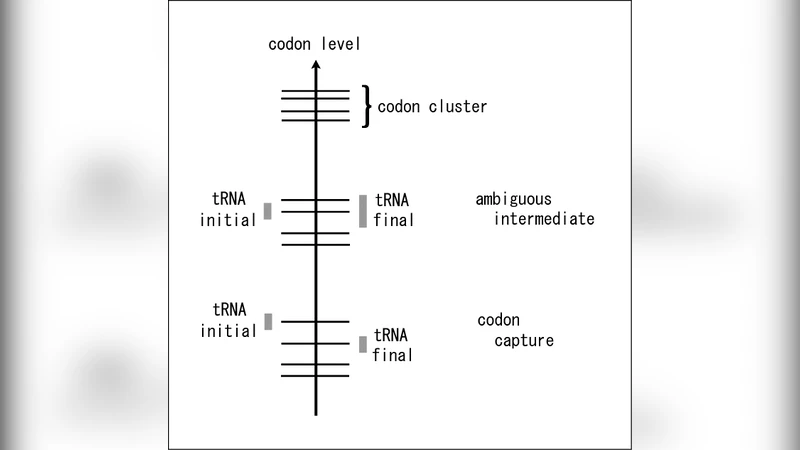
이 연구는 기존 유전암호 진화 이론을 물리학적 ‘형상 공간’ 개념에 접목시킨 점이 가장 큰 혁신이다. 코돈을 고차원 벡터가 아니라 1차원 스칼라인 ‘코돈 레벨’로 단순화함으로써, 코돈 군집(가족 상자)과 그 사이의 레벨 간격을 시각적으로 이해할 수 있게 했다. 특히, 코돈 레벨의 클러스터와 그 사이의 ‘갭’은 wobble pairing에 의해 같은 아미노산으로 번역되는 코돈들의 물리적 근접성을 설명한다.
두 시나리오를 구분하는 핵심은 tRNA 변이가 발생하는 위치이다. 안티코돈 변이는 레벨 중심 자체를 이동시켜 코돈 캡처를, 안티코돈 외부 변이는 인식 범위(폭)를 확대·축소시켜 애매중간 상황을 만든다. 이러한 구분은 실제 생물학적 관찰(정지코돈 → 아미노산, 혹은 아미노산 간 교체)과도 일치한다.
시뮬레이션 설계는 네 단계(변이 도입 → 비정상 tRNA 제거 → 비용 기반 복제 → 세포 분열)로 구성되며, 변이율 μ는 실험적 시간 스케일을 조정하는 파라미터일 뿐 실제 돌연변이 빈도와는 무관하게 설정되었다. 비용 선택 메커니즘은 아미노산 합성 비용 차이를 복제율에 직접 반영함으로써, 비용이 높은 tRNA(aa‑2)가 빠르게 도태되는 과정을 재현한다. 결과 그래프(그림 6‑8)에서 볼 수 있듯이, 한 번 두 코돈을 모두 인식하는 tRNA가 등장하면 대체 과정은 급격히 가속화돼 약 10세대 내에 완결된다. 이는 애매중간 시나리오가 “비특이적 번역” 단계에서 겪는 불리함을 최소화한다는 중요한 생물학적 함의를 제공한다.
코돈 캡처 시나리오에 대한 별도 시뮬레이션은 제시되지 않았지만, 논문은 중성 돌연변이만을 보존하는 세포가 GC 함량 감소 압력 하에서 살아남는다고 주장한다. 이는 실제 미토콘드리아와 원핵생물에서 관찰되는 GC 감소 경향과 일맥상통한다.
비판적으로 보면, 1차원 코돈 레벨 모델은 실제 코돈-안티코돈 상호작용의 복잡성을 과도하게 단순화한다. 또한, tRNA 변이를 안티코돈 외부와 내부로만 구분했지만, 아미노산‑tRNA 합성효소(aaRS) 변이, 리보솜 변이 등 다른 요인들을 무시한 점은 모델의 적용 범위를 제한한다. 향후 연구에서는 다차원 형상 공간을 도입하고, aaRS와 리보솜 변이를 포함한 복합 선택 압력을 고려함으로써 보다 현실적인 진화 경로를 탐색할 필요가 있다.
**
댓글 및 학술 토론
Loading comments...
의견 남기기