스케일프리 토폴로지를 활용한 유전자조절망 추론을 위한 반복 특징 선택 방법
초록
**
본 논문은 유전자 발현 시계열 데이터로부터 유전자조절망(GRN)을 추론할 때, 기존의 특징 선택 알고리즘인 SFFS에 스케일프리(Barabási‑Albert) 네트워크 토폴로지를 사전 지식으로 결합한 SFFS‑BA를 제안한다. 검색 공간을 파워‑법칙 가중치로 축소하고, 조합 수가 적을 때는 폭넓게, 많아질 때는 깊이 있게 탐색함으로써 SFS·SFFS 대비 높은 네트워크 복원 정확도를 달성한다.
**
상세 분석
**
논문은 먼저 GRN 추론이 샘플 수는 적고 차원은 수천에 달하는 고차원·저샘플 문제임을 강조한다. 기존 방법들은 순수 통계적 추정에 의존해 잡음과 과적합에 취약했으며, 이를 보완하기 위해 생물학적 사전 지식, 특히 네트워크 토폴로지를 활용하는 접근이 최근 주목받고 있다. 저자는 복잡계 네트워크 이론 중 스케일프리 특성(노드 차수가 파워‑법칙을 따름)을 GRN에 적용한다. Barabási‑Albert 모델을 기반으로 각 유전자의 연결 가능성을 사전 확률로 정의하고, 이 확률을 특징 선택 과정에서 가중치로 사용한다.
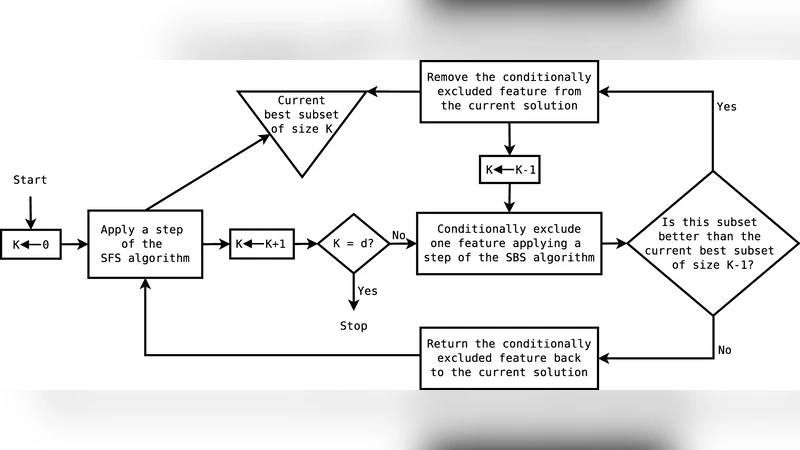
기존 SFFS는 “floating” 메커니즘으로 삽입·제거를 반복해 nesting effect를 완화하지만, 탐색 공간이 여전히 지수적으로 증가한다. SFFS‑BA는 두 단계 전략을 도입한다. 첫 번째 단계(k ≤ 2)에서는 모든 후보 조합을 폭넓게(breadth‑first) 평가해 초기 후보 집합을 만든다. 두 번째 단계(k ≥ 3)에서는 파워‑법칙 가중치를 적용해 높은 차수를 가진 노드(허브) 중심으로 탐색을 깊게(depth‑first) 진행한다. 이렇게 하면 조합 수가 폭발적으로 늘어나는 상황에서도 계산량을 크게 줄이면서 허브 중심의 중요한 규제 관계를 놓치지 않는다.
평가에는 평균 조건 엔트로피를 기준 함수로 사용한다. 이는 목표 유전자의 조건부 확률 분포가 균일할수록 엔트로피가 높아져 상호 정보가 낮아지는 특성을 이용해 직접적인 조절 관계를 검출한다. 실험에서는 인공적으로 생성한 스케일프리 네트워크와 기존 SFS·SFFS와의 비교를 통해 정밀도·재현율·F‑score 모두에서 유의미한 개선을 보였다. 특히 허브 유전자의 연결을 정확히 복원하는 비율이 크게 상승했으며, 잡음 수준이 높아도 안정적인 성능을 유지한다.
한계점으로는 사전 토폴로지 정보가 실제 생물학적 네트워크와 일치하지 않을 경우 성능 저하 가능성이 있으며, 파라미터(예: 파워‑법칙 지수 γ)의 설정이 결과에 민감하게 작용한다는 점을 들 수 있다. 또한 실험이 주로 시뮬레이션 데이터에 국한돼 있어 실제 마이크로어레이·RNA‑Seq 데이터에 대한 검증이 추가로 필요하다.
**
댓글 및 학술 토론
Loading comments...
의견 남기기