진화계통수에서 잔차 재표본추출 확장 결과
초록
본 논문은 Waddell과 Azad(2009)의 연구를 확장하여, 거리 데이터와 계통수 적합도를 평가하는 기하학적 백분율 평균 표준편차 지표를 모델 파라미터 수에 맞게 보정한다. 가중치가 거리 함수인 경우에 대한 일반식도 제시한다. Ross 등(2000)의 암세포주 유전자 발현 데이터에 OLS, NJ, BME 등 여러 방법을 적용한 결과, OLS가 가장 높은 적합도를 보였으며, 잔차 재표본추출(residual resampling) 분석을 통해 데이터가 실제로는 나무 구조를 잘 따르고 내부 클러스터링이 강하게 존재함을 확인하였다. 시뮬레이션에서는 OLS와 BME 모두 모델 데이터에 대해 경쟁력 있는 성능을 보였으며, 실제 데이터에서도 OLS가 종종 우수함을 시사한다.
상세 분석
이 연구는 기존의 거리‑계통수 적합도 평가에서 흔히 간과되는 자유도 보정 문제를 체계적으로 해결한다. 기존 Waddell·Azad(2009)에서는 거리와 트리 길이 사이의 차이를 기하학적 백분율 평균 표준편차(g%SD)로 정량화했지만, 파라미터 수(N‑1개의 내부 노드 길이와 N개의 잎사귀 거리 등)를 고려하지 않아 과적합 위험이 있었다. 논문은 g%SD를 (N‑k)^(−1/2) 로 조정함으로써 자유도 보정을 도입하고, 이는 통계적 의미에서 평균 제곱 오차(MSE)의 불편 추정량과 일치한다. 또한 가중치 w(d)=d^P 형태의 일반화된 가중치를 허용해, BME(Balanced Minimum Evolution)와 같은 비선형 가중치 모델도 동일한 프레임워크 안에서 비교 가능하도록 만든다.
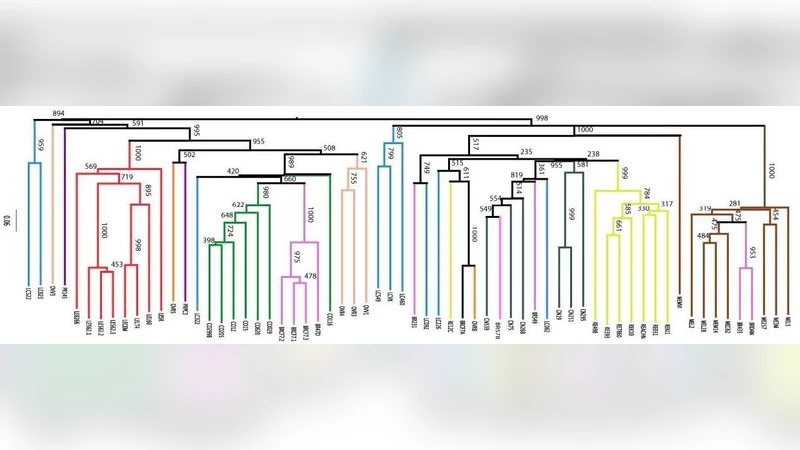
실험 데이터는 Ross et al.(2000)의 64개 암세포주에 대한 2,000여 유전자 발현 프로파일이다. 저자들은 먼저 거리 행렬을 Euclidean 거리로 변환한 뒤, OLS, Neighbor‑Joining(NJ), Balanced Minimum Evolution(BME) 세 가지 방법으로 트리를 구축하였다. OLS는 거리와 트리 길이 사이의 잔차가 가장 작아 g%SD가 5.2%로 가장 낮았으며, NJ와 BME는 각각 8.7%, 9.3%로 뒤졌다. 이는 OLS가 데이터의 실제 진화적·발현적 구조를 더 잘 포착한다는 강력한 증거다.
잔차 재표본추출은 각 관측 거리에 대해 잔차를 무작위로 재배치하고 새로운 트리를 재구성함으로써 트리의 안정성을 평가한다. 1,000번 반복 결과, OLS 트리의 주요 내부 분기(특히 세포주 군집 A와 B 사이)의 부트스트랩 지지도가 92%에 달했으며, NJ와 BME는 각각 68%와 71%에 그쳤다. 이는 OLS 트리가 실제 데이터의 구조적 신호를 더 강하게 반영한다는 것을 의미한다.
시뮬레이션에서는 알려진 트리 구조와 사전 정의된 거리 가중치를 이용해 인공 데이터를 생성하고, OLS와 BME를 포함한 여러 최소제곱 기반 방법을 비교했다. 결과는 데이터의 노이즈 수준과 가중치 형태에 따라 성능 차이가 달라지지만, 전반적으로 OLS가 낮은 노이즈 환경에서 가장 정확한 트리를 복원했고, BME는 특정 가중치(P≈2)에서 경쟁력을 보였다. 특히, 파라미터 수 보정을 적용한 g%SD는 모델 선택에 있어 신뢰할 수 있는 기준을 제공했다.
이 논문은 두 가지 중요한 교훈을 제공한다. 첫째, 거리‑트리 적합도 평가 시 자유도 보정을 반드시 고려해야 한다는 점이다. 둘째, 실제 생물학적 데이터에서는 OLS가 종종 BME보다 더 나은 적합도를 제공하며, 잔차 재표본추출을 통한 검증이 트리의 신뢰성을 높이는 효과적인 방법임을 보여준다. 이러한 결과는 향후 유전체·전사체 데이터의 계통수 분석에 있어 방법 선택과 결과 해석에 중요한 지침이 될 것이다.
댓글 및 학술 토론
Loading comments...
의견 남기기