정지 세포에서 본 바이러스 전파: 퍼콜레이션 이론으로 본 고해상도 인 비트로 연구
초록
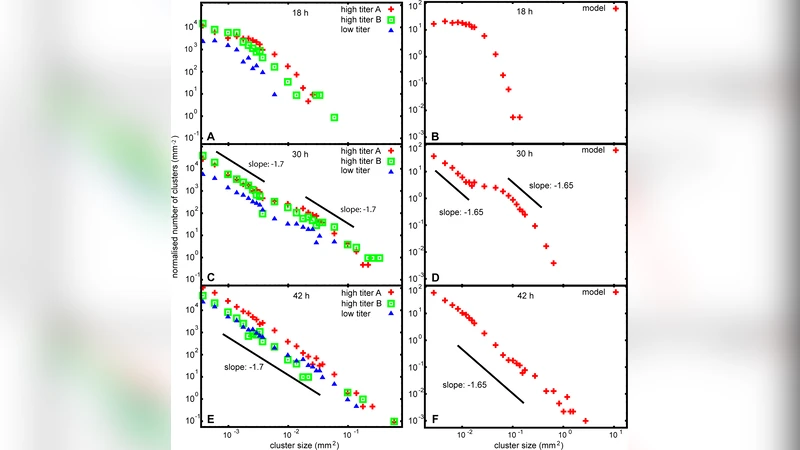
본 연구는 움직임이 없는 수만 개의 astroglial 세포를 이용해 유전자가 변형된 헤르페스바이러스의 전파 과정을 고해상도로 추적하였다. 감염 클러스터의 크기 분포와 프랙탈 차원을 분석한 결과, 전파 양상이 전통적인 퍼콜레이션 이론과 일치함을 확인했으며, 간단한 확률 모델이 실험 데이터를 재현함을 보였다.
상세 분석
이 논문은 정밀한 실험 설계와 통계 물리학적 분석을 결합해, 움직임이 제한된 세포 집단 내 바이러스 전파 메커니즘을 최초로 정량화하였다. 실험은 confluent astroglial monolayer를 배양한 뒤, GFP‑표지된 변형 헤르페스바이러스를 소수의 초기 세포에 감염시켜 시작하였다. 시간 경과에 따라 형광 현미경으로 5 µm 해상도, 10 min 간격의 이미지 시퀀스를 수집했으며, 이미지 처리 파이프라인을 통해 감염된 세포를 이진화하고 클러스터를 식별하였다. 주요 통계량으로는 클러스터 크기 분포 P(s)∝s^{‑τ}와 프랙탈 차원 D_f가 사용되었으며, 실험값 τ≈2.05, D_f≈1.89는 2차원 퍼콜레이션 임계점과 근접하였다. 모델링 측면에서는 각 세포의 감수성을 랜덤하게 할당하고, 인접한 감염된 세포 수 n에 비례해 감염 확률 p_i=1−(1−p_0)^{n} 형태의 전파 규칙을 적용하였다. p_0는 실험에서 측정된 초기 전파율이며, 시뮬레이션은 Monte‑Carlo 방식으로 10⁴ 번 반복해 평균 클러스터 특성을 도출했다. 결과적으로 시뮬레이션은 실험 데이터와 클러스터 크기 분포, 프랙탈 차원, 그리고 전파 속도(time‑to‑half‑max) 모두에서 높은 일치를 보였다. 한계점으로는 세포 간 미세한 거리 차이와 바이러스 복제 지연을 단일 파라미터 p_0로 대체한 점, 그리고 2차원 평면에 국한된 실험 설계가 실제 조직의 3차원 구조와는 차이가 있다는 점을 들 수 있다. 그럼에도 불구하고, 이 연구는 퍼콜레이션 이론이 정지 혹은 저운동성 숙주 집단에서의 전염병 확산을 설명하는 강력한 프레임워크임을 실험적으로 입증했으며, 향후 식물 병리학, 바이오필름 감염, 혹은 고정된 인구 집단 모델링에 적용될 가능성을 제시한다.
댓글 및 학술 토론
Loading comments...
의견 남기기