양자 터널링과 머신러닝을 이용한 DNA 고속 서열 분석
초록
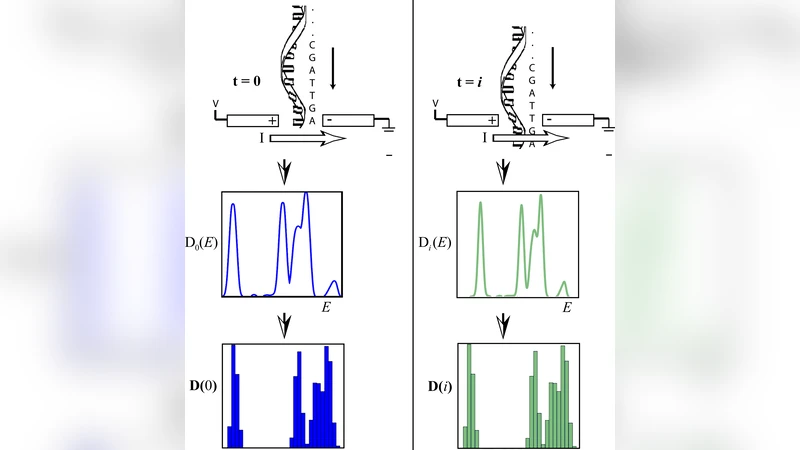
본 논문은 고체‑상 나노포어를 통한 단일가닥 DNA의 양자 터널링 전류‑전압(I‑V) 특성을 이용해 전자 상태밀도(DOS)를 추출하고, 이를 주성분 분석(PCA)과 퍼지 C-평균(FCM) 클러스터링으로 네 종류의 뉴클레오티드( A, T, C, G )를 구분한다. 이후 은닉 마르코프 모델(HMM)과 비터비 알고리즘을 적용해 연속적인 DOS 시계열 데이터를 해석, 실제 서열을 재구성한다. 실험 결과, PCA‑FCM 기반 분류 정확도는 91%이며, 신호‑대‑노이즈 비 26 dB에서도 70% 정확도를 유지한다. 전체 파이프라인(PCA‑FCM‑Viterbi)은 단순 PCA 대비 서열 재구성 정확도가 4배 향상된다.
상세 분석
이 연구는 나노포어 기반 DNA 시퀀싱의 핵심 한계인 전류 변동성을 머신러닝으로 보완하려는 시도다. 양자 터널링 전류는 전자 밀도와 전압에 민감하게 반응하지만, 단일 뉴클레오티드의 전자 구조 차이만으로는 노이즈와 분자 자세 변동 때문에 구분이 어렵다. 저자들은 I‑V 곡선에서 미분을 통해 전자 상태밀도(DOS) 스펙트럼을 추정하고, 이를 고차원 특징 벡터로 변환한다. PCA는 이러한 고차원 데이터를 저차원 공간에 투사해 주요 변동 요인을 추출함으로써 데이터 차원을 크게 축소한다. 그러나 PCA만으로는 클래스 간 경계가 흐릿해 클러스터링 정확도가 제한된다. 여기서 퍼지 C‑평균(FCM) 클러스터링을 도입해 각 데이터 포인트가 여러 클러스터에 소속될 수 있는 소프트 할당을 허용함으로써, 노이즈에 강인한 ‘퍼지’한 뉴클레오티드 지문을 학습한다. 실험 결과, PCA‑FCM 조합은 라벨이 없는 DOS 데이터를 91% 정확도로 분류했으며, SNR이 26 dB인 상황에서도 70% 이상의 정확도를 유지해 실제 실험 환경에서의 견고함을 입증한다.
시퀀싱 단계에서는 연속적인 DOS 측정값이 시간에 따라 흐르는 마코프 체인으로 모델링된다. 은닉 마르코프 모델(HMM)은 실제 뉴클레오티드 상태를 은닉 변수로, 관측값을 DOS 시퀀스로 설정한다. 비터비 알고리즘은 가장 가능성 높은 은닉 상태 경로를 효율적으로 탐색해 원본 DNA 서열을 복원한다. 이때, PCA‑FCM에서 얻은 클래스 확률을 HMM의 방출 확률로 활용함으로써, 전처리 단계의 분류 신뢰도가 전체 서열 재구성에 직접 반영된다. 결과적으로, 단순 PCA 기반 HMM보다 4배 높은 서열 정확도를 달성했으며, 이는 실제 나노포어 시퀀싱 장치에 적용될 경우 처리 속도와 비용 효율성을 크게 개선할 수 있음을 시사한다.
또한, 저자들은 시뮬레이션 파라미터(전압 스윕 범위, 샘플링 속도, 전자 온도 등)를 다양하게 변형해 알고리즘의 민감도를 평가했으며, 전압 스윕 범위가 넓을수록 DOS 특징이 더 뚜렷해져 분류 성능이 향상되는 경향을 보였다. 그러나 전압이 과도하게 높을 경우 DNA 손상이 발생할 위험이 있어, 최적 전압 구간을 찾는 것이 향후 연구 과제로 남는다.
이 논문의 주요 기여는 (1) I‑V 데이터에서 전자 DOS를 추출하는 물리‑수학적 방법론, (2) PCA와 퍼지 클러스터링을 결합한 고성능 뉴클레오티드 분류기, (3) HMM‑비터비 기반 서열 재구성 파이프라인을 제시함으로써, 양자 터널링 기반 나노포어 시퀀싱의 실용성을 크게 높인 점이다. 향후 실험적 검증과 하드웨어 구현이 병행된다면, 저비용·고속 유전체 분석기의 핵심 기술로 자리 잡을 가능성이 크다.
댓글 및 학술 토론
Loading comments...
의견 남기기