리보솜 내부 사이클을 고려한 비대칭 배제 과정 모델
초록
본 연구는 전통적인 비대칭 단순 배제 과정(ASEP) 모델에 리보솜의 두 단계 생화학적 사이클을 도입하여, 평균장 이론으로 입자 흐름의 고밀도·저밀도·최대 전류 상을 분석한다. 내부 사이클을 포함하면 상전이 임계값이 기존 ASEP와 달라짐을 보이며, 이는 mRNA 번역 과정의 실제 동역학을 더 정확히 반영한다는 점을 강조한다.
상세 분석
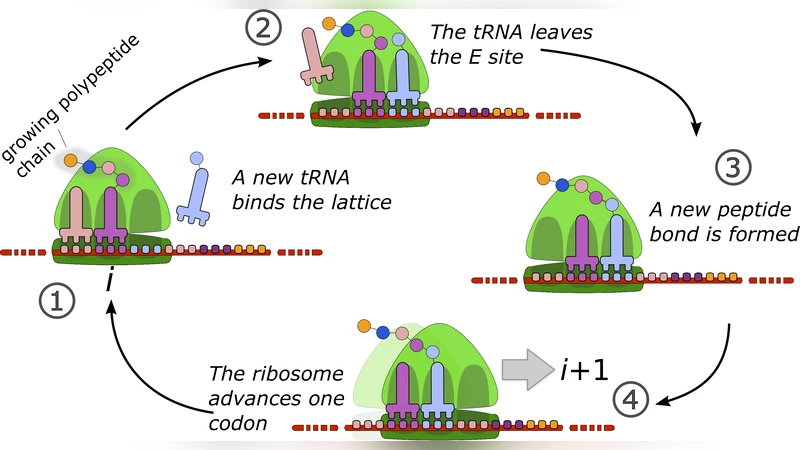
본 논문은 기존 ASEP 기반의 mRNA 번역 모델이 리보솜의 복합적인 생화학적 과정을 단순히 한 단계 이동으로 축소함으로써 발생하는 한계를 지적한다. 저자들은 리보솜이 펩타이드 결합 형성(step 1)과 전이(step 2)라는 두 개의 기본적인 내부 사이클을 거친다고 가정하고, 이를 ‘내부 상태’를 갖는 입자로 모델링한다. 평균장 접근법을 적용해 각 내부 상태에 대한 점유 확률과 전이율을 연쇄적으로 연결함으로써 전체 시스템의 흐름 방정식을 도출한다. 중요한 결과는 전이율 k₁, k₂가 입자 밀도와 입구·출구 입장률(α, β)과 결합하여 유효 전이율을 형성한다는 점이다. 이 유효 전이율이 기존 ASEP의 단일 전이율과 달리 두 단계의 비대칭성에 따라 변동하므로, 고밀도·저밀도·최대 전류 상의 경계가 α와 β의 임계값이 달라진다. 예컨대, 전이율 k₁이 느릴 경우 전이 단계가 ‘병목’이 되어 전류 제한이 α가 아닌 k₁에 의해 결정되며, 이는 전통적인 ASEP에서는 관찰되지 않는다. 또한, 저자들은 파라미터 공간을 3차원(α, β, k₁/k₂)으로 확장해 상도표를 제시하고, 각 상에서 평균 리보솜 밀도와 전류의 정량적 식을 제공한다. 이러한 분석은 코돈 사용 최적화, 리보솜 충돌 회피, 번역 효율 조절 등 생물학적 현상을 물리학적 관점에서 해석하는 데 유용하다. 마지막으로, 실험적 데이터와 비교했을 때 내부 사이클을 포함한 모델이 실제 번역 속도와 리보솜 분포를 더 정확히 재현한다는 점을 강조하며, 모델의 확장 가능성(예: 추가적인 내부 상태, 코돈 의존성 전이율)도 논의한다.
댓글 및 학술 토론
Loading comments...
의견 남기기