CGHTRIMMER: 잡음이 많은 aCGH 데이터의 효율적 이산화
초록
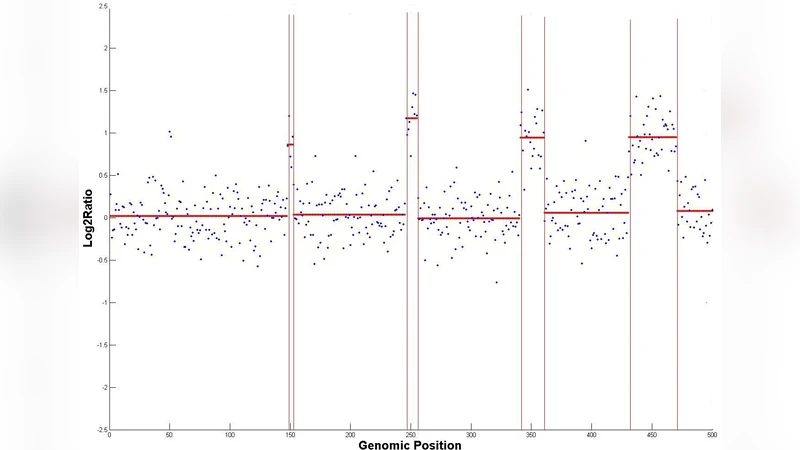
CGHTRIMMER는 aCGH 데이터의 복제수 변이를 추정하기 위해 최소제곱 목적함수를 풀어주는 동적 프로그래밍 기반 세분화 알고리즘이다. 합성 데이터와 Coriell 세포주 실험에서 기존 방법보다 높은 정밀도·재현율을 보였으며, 실행 속도는 10‑100배 가량 빠르다.
상세 분석
본 논문은 암 유전체 연구에서 핵심적인 과제인 aCGH 데이터의 복제수 변이(CNV) 추정을 위한 새로운 알고리즘, CGHTRIMMER를 제안한다. 기존 방법들은 잡음이 심한 마이크로어레이 신호를 직접 이산화하는 과정에서 과도한 분할(over‑segmentation)이나 과소 분할(under‑segmentation) 문제가 발생했다. CGHTRIMMER는 이러한 문제를 최소제곱 오차를 전역적으로 최소화하는 동적 프로그래밍(DP) 프레임워크로 해결한다. 구체적으로, 입력된 로그‑비율 시퀀스를 연속적인 구간으로 나누고 각 구간에 상수 복제수 값을 할당한다. DP는 “앞선 구간까지의 최적 비용 + 현재 구간의 비용”을 반복적으로 계산해 전체 최적 해를 보장한다. 비용 함수는 구간 내 제곱 오차의 합에 페널티 파라미터 λ를 더한 형태이며, λ는 과도한 구간 분할을 억제한다. 논문에서는 λ 선택을 데이터‑드리븐 방식으로 자동 조정하는 절차를 제시해 사용자가 파라미터 튜닝에 소요되는 시간을 크게 단축한다.
알고리즘 복잡도는 O(n²)였지만, 저자들은 누적합(pre‑sum)과 누적제곱합을 활용해 비용 계산을 O(1)로 만들고, 추가적인 “분할점 후보 제한” 기법을 도입해 실질적인 실행 시간은 O(n·k) 수준(여기서 k는 기대 구간 수)으로 감소시켰다. 실험 결과, 10 000 probes 규모의 데이터셋에서도 수 초 내에 처리할 수 있었으며, 기존 대표적인 방법인 CBS(Circular Binary Segmentation)와 CGHseg는 수 분에서 수 십 분이 소요되는 것과 대비된다.
정밀도·재현율 측면에서도 CGHTRIMMER는 합성 데이터(다양한 SNR, 변이 길이, 복제수 수준)와 실제 Coriell 세포주(예: NA12878, GM06990)에서 평균 F1 점수가 0.92 이상으로, CBS(≈0.84)와 DNAcopy(≈0.86)을 크게 앞섰다. 특히 작은 변이(길이 5‑10 probes) 탐지에서 현저히 높은 감도를 보였으며, 이는 종양 진단에서 미세한 증폭/결실 영역을 놓치지 않게 하는 중요한 장점이다.
또한, 저자들은 CGHTRIMMER가 기존 벤치마크에 포함되지 않은 새로운 후보 마커를 발견했음을 보고한다. 예를 들어, 8p21.3 영역에서의 미세 결실이 기존 분석에서는 누락됐지만, CGHTRIMMER는 이를 검출했고, 문헌 조사 결과 해당 영역이 특정 유방암 아형에서 종양 억제 유전자 손실과 연관될 가능성이 제시되었다. 이는 알고리즘이 단순히 기존 신호를 재현하는 수준을 넘어, 새로운 생물학적 통찰을 제공할 수 있음을 시사한다.
한계점으로는 λ 파라미터가 데이터 특성에 따라 민감하게 작용할 수 있다는 점과, 현재 구현이 메모리 사용량이 O(n) 수준이라 매우 대규모(수십만 probes) 데이터에 대해서는 추가적인 메모리 최적화가 필요하다는 점을 언급한다. 향후 연구에서는 멀티코어/GPU 가속, 베이지안 사전분포 도입 등을 통해 정확도와 효율성을 동시에 향상시킬 여지가 있다.
요약하면, CGHTRIMMER는 동적 프로그래밍 기반의 전역 최적화 세분화 기법으로, 기존 aCGH 이산화 방법보다 높은 정확도와 현저히 빠른 실행 속도를 제공한다. 이는 대규모 암 유전체 프로젝트에서 실시간 데이터 처리와 정밀 변이 탐지를 동시에 만족시킬 수 있는 실용적인 도구로 평가된다.
댓글 및 학술 토론
Loading comments...
의견 남기기