유전자 조절망의 기본 계산 구조
초록
본 연구는 대장균, 바실러스 subtilis, 효모 Saccharomyces cerevisiae의 유전자 조절망(GRN)을 비교 분석하여, 최소 핵심 인과 관계를 추출하고 동적·인과적 관점에서 계층적·모듈적 조직을 규명한다. 세균에서는 상위‑하위 구조가 뚜렷하고 여러 작은 동적 모듈이 존재하지만, 효모는 중앙에 거대한 단일 모듈을 갖는 ‘보우‑타이’ 형태를 보인다. 이러한 차이는 전사 개시, 대사 제어, 신호 전달, 스트레스 반응, 포자 형성, 세포 주기 등 기능적 측면에서도 서로 다른 논리적 조직 방식을 시사한다.
상세 분석
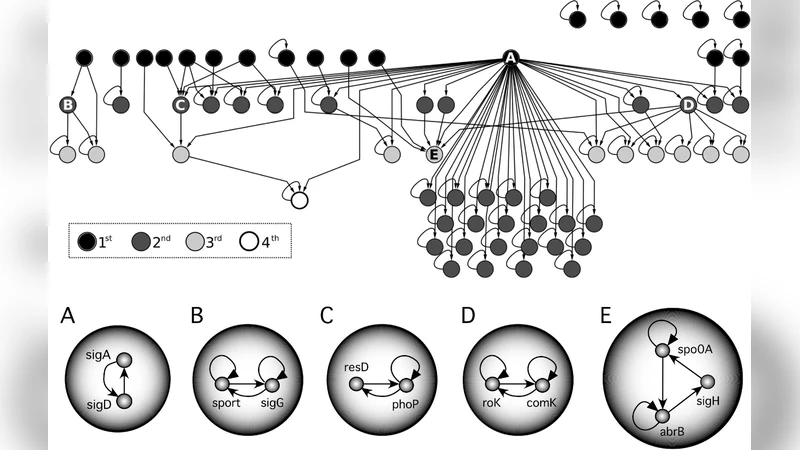
이 논문은 기존의 정적 토폴로지 분석을 넘어, 네트워크 내 인과 흐름을 동적 시뮬레이션과 결합한 새로운 프레임워크를 제시한다. 먼저 각 종의 GRN을 전사인자(TF)와 표적 유전자의 연결 고리로 모델링하고, ‘인과 최소 핵심(causal core)’을 도출하기 위해 강인성(robustness)과 필수성(essentiality) 기준을 적용한다. 핵심 네트워크는 전체 연결의 약 10%에 불과하지만, 정보 흐름과 피드백 루프를 대부분 포함하고 있어 ‘계산적 골격’이라고 할 수 있다.
계층 구조는 네트워크를 상위(입력) 레이어, 중간(전달) 레이어, 하위(출력) 레이어로 구분하고, 각 레이어 간의 인과적 흐름을 DAG(Directed Acyclic Graph) 형태로 시각화한다. 대장균과 B. subtilis에서는 상위 레이어에 전사인자들이 집중되고, 하위 레이어는 대사 효소와 스트레스 반응 유전자가 주를 이룬다. 이때 중간 레이어에 위치한 작은 ‘동적 모듈’은 특정 환경 신호에 대한 빠른 응답을 담당하며, 모듈 간 연결은 주로 단일 혹은 이중 피드백 루프 형태로 제한된다.
반면 효모 GRN은 전사 조절이 복잡한 다중 피드백 네트워크를 형성하고, 중앙에 위치한 대규모 ‘동적 모듈’이 전체 네트워크의 40% 이상을 차지한다. 이 모듈은 세포 주기, DNA 복구, 핵심 대사 경로 등을 포괄하며, 입력 신호가 모듈 내부에서 여러 단계의 변환을 거쳐 출력으로 전달되는 ‘보우‑타이’ 구조를 만든다. 즉, 입력과 출력이 모듈 양쪽 끝에 위치하고, 모듈 자체가 정보 처리와 저장을 동시에 수행한다는 점에서 세균형과 근본적으로 다르다.
기능적 분석에서는 GO(term) 풍부도 검정을 통해 각 모듈이 담당하는 생물학적 프로세스를 매핑하였다. 세균의 작은 모듈은 ‘전사 개시’, ‘아미노산 대사’, ‘스트레스 반응’ 등 비교적 단일 기능에 특화된 반면, 효모의 대형 모듈은 ‘세포 주기 조절’, ‘핵심 대사 조절’, ‘신호 전달 경로 통합’ 등 복합적인 기능을 동시에 수행한다. 이는 진화적 압력에 따라 복잡성 요구가 달라졌음을 시사한다.
또한 네트워크 견고성을 평가하기 위해 무작위 노드/엣지 제거 실험을 수행했으며, 세균의 경우 핵심 모듈이 손실되면 전체 네트워크가 급격히 붕괴되는 반면, 효모는 대형 모듈 내부의 다중 경로 덕분에 부분적인 손실에도 비교적 안정성을 유지한다. 이러한 차이는 ‘분산형’ vs ‘집중형’ 논리 설계의 장단점을 각각 보여준다.
결론적으로, 논문은 (1) 인과 최소 핵심을 통한 네트워크 축소 방법, (2) 동적 모듈 기반 계층 구조 해석, (3) 세균과 진핵생물 간 논리 조직의 진화적 차이를 제시한다는 점에서 GRN 연구에 새로운 패러다임을 제공한다. 향후 합성생물학, 약물 표적 탐색, 그리고 인공 세포 설계 등에 이 접근법을 적용하면, 복잡한 유전 회로를 보다 효율적으로 설계·조절할 수 있을 것으로 기대된다.
댓글 및 학술 토론
Loading comments...
의견 남기기