극값 이론으로 짧은 DNA 모티프 탐지
초록
짧은 전사인자 결합부위(모티프)의 통계적 유의성을 평가하기 위해 극값 이론의 Peak‑over‑Threshold(POT) 방법을 적용하였다. 인위적인 위치특이 빈도 행렬(PSFM)과 실제 에스트로겐 반응 요소(ERE) 데이터를 이용해 배경과 실제 프로모터에서 점수 분포를 비교하고, 두 단계의 유의성 기준을 설정함으로써 기존 방법 대비 거짓 양성을 크게 감소시켰다.
상세 분석
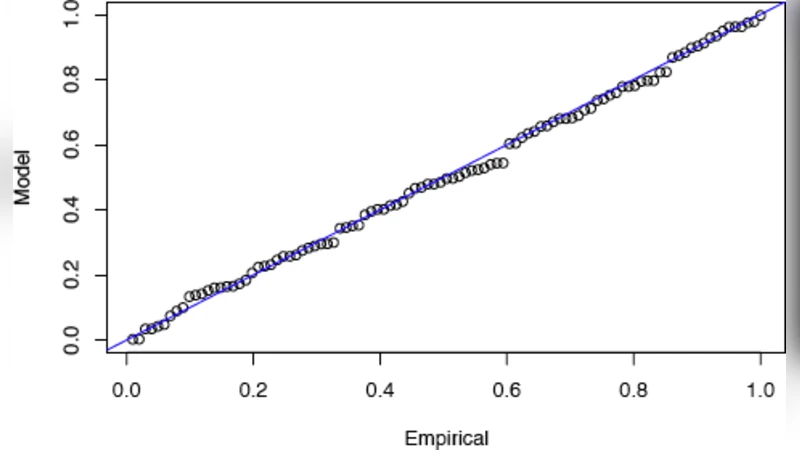
본 논문은 전사인자 결합부위 탐지를 위한 기존의 가우시안 기반 통계 검정이 짧은 모티프(길이 5~20)에서는 근본적인 한계를 가진다는 점을 명확히 지적한다. 짧은 서열에서는 로그우도 점수 Wₖ가 적은 수의 독립 항목 합으로 구성돼 중심극한정리가 적용되지 않으며, 따라서 점수의 최대값 분포는 일반적인 가우시안 극값 분포(Gumbel)와 크게 다를 수 있다. 이를 해결하기 위해 저자들은 극값 이론 중 Generalized Pareto Distribution(GPD)을 기반으로 하는 Peak‑over‑Threshold(POT) 접근을 도입하였다. 구체적으로, 전체 프로모터에서 계산된 점수 집합 {Wₖ}에 대해 높은 임계값 u를 설정하고, u를 초과하는 초과값 Yₖ=Wₖ−u의 분포를 GPD에 적합시켜 형태 매개변수 ξ와 규모 매개변수 σ를 추정한다. 이때 ξ는 극값 분포의 꼬리 형태를 결정하며, ξ>0이면 Fréchet, ξ<0이면 Weibull, ξ≈0이면 Gumbel에 해당한다.
임계값 u는 평균 초과값(eₙ(u))와 u의 선형 관계를 이용해 최적화한다. 즉, eₙ(u)≈σ+ξ u/(1−ξ) 가 성립하는 구간을 찾아야 하는데, 이는 초과값이 실제로 GPD를 따를 때만 가능한 조건이다. 최적 u가 결정되면, 초과값들의 개수 N은 포아송 분포를 따른다고 가정하고, 각 초과값 Yₖ에 대해 최대 초과값이 Yₖ보다 클 확률 Pₖ=1−exp
댓글 및 학술 토론
Loading comments...
의견 남기기